deSolve R中的时变参数矩阵
deSolve R中的时变参数矩阵
提问于 2020-06-26 12:30:44
我为这件事挣扎了这么久。我有一个logistic增长函数,其中增长参数r是一个矩阵。该模型的构造方式,我有一个输出,两个N,N1和N2。
我希望能随着时间的推移改变r参数。当时间< 50时,我想要r= r1
r1=matrix(c(
2,3),
nrow=1, ncol=2当时间>= 50,我想r=r2在哪里
r2=matrix(c(
1,2),
nrow=1, ncol=2这是我的功能。任何帮助都是非常感谢的。
rm(list = ls())
library(deSolve)
model <- function(time, y, params) {
with(as.list(c(y,params)),{
N = y[paste("N",1:2, sep = "")]
dN <- r*N*(1-N/K)
return(list(c(dN)))
})
}
r=matrix(c(
4,5),
nrow=1, ncol=2)
K=100
params <- list(r,K)
y<- c(N1=0.1, N2=0.2)
times <- seq(0,100,1)
out <- ode(y, times, model, params)
plot(out)我想要这种理想的东西,但它不起作用
model <- function(time, y, params) {
with(as.list(c(y,params)),{
N = y[paste("N",1:2, sep = "")]
r = ifelse(times < 10, matrix(c(1,3),nrow=1, ncol=2),
ifelse(times > 10, matrix(c(1,4),nrow=1, ncol=2), matrix(c(1,2),nrow=1, ncol=2)))
print(r)
dN <- r*N*(1-N/K)
return(list(c(dN)))
})
}谢谢您抽时间见我。
回答 2
Stack Overflow用户
回答已采纳
发布于 2020-06-26 15:35:43
如果您想传递一个矩阵参数,您应该传递一个参数列表,并且在超过时间限制时,您可以在模型内修改它(在下面的示例中,您甚至不必将r矩阵传递给模型函数)
library(deSolve)
model <- function(time, y, params) {
with(as.list(c(y,params)),{
if(time < 3) r = matrix(c(2,3), nrow = 1, ncol = 2)
else r = matrix(c(1,3), nrow = 1, ncol = 2)
N = y[paste("N",1:2, sep = "")]
dN <- r*N*(1-N/K)
return(list(c(dN)))
})
}
y <- c(N1=0.1, N2=0.2)
params <- list(r = matrix(c(0,0), nrow = 1, ncol = 2), K=100)
times <- seq(0,10,0.1)
out <- ode(y, times, model, params)
plot(out)您可以看到这方面的例子,例如延迟微分方程?dede。
Stack Overflow用户
发布于 2020-06-27 17:15:20
这里是一种通用方法,它使用approx函数的扩展版本。还请注意模型函数和参数值的附加图的进一步简化。
编辑根据刘易斯·卡特的建议在t=3上修改参数,这样就可以看到效果。
library(simecol) # contains approxTime, a vector version of approx
model <- function(time, N, params) {
r <- approxTime(params$signal, time, rule = 2, f=0, method="constant")[-1]
K <- params$K
dN <- r*N*(1-N/K)
return(list(c(dN), r))
}
signal <- matrix(
# time, r[1, 2],
c( 0, 2, 3,
3, 1, 2,
100, 1, 2), ncol=3, byrow=TRUE
)
## test of the interpolation
approxTime(signal, c(1, 2.9, 3, 100), rule = 2, f=0, method="constant")
params <- list(signal = signal, K = 100)
y <- c(N1=0.1, N2=0.2)
times <- seq(0, 10, 0.1)
out <- ode(y, times, model, params)
plot(out)
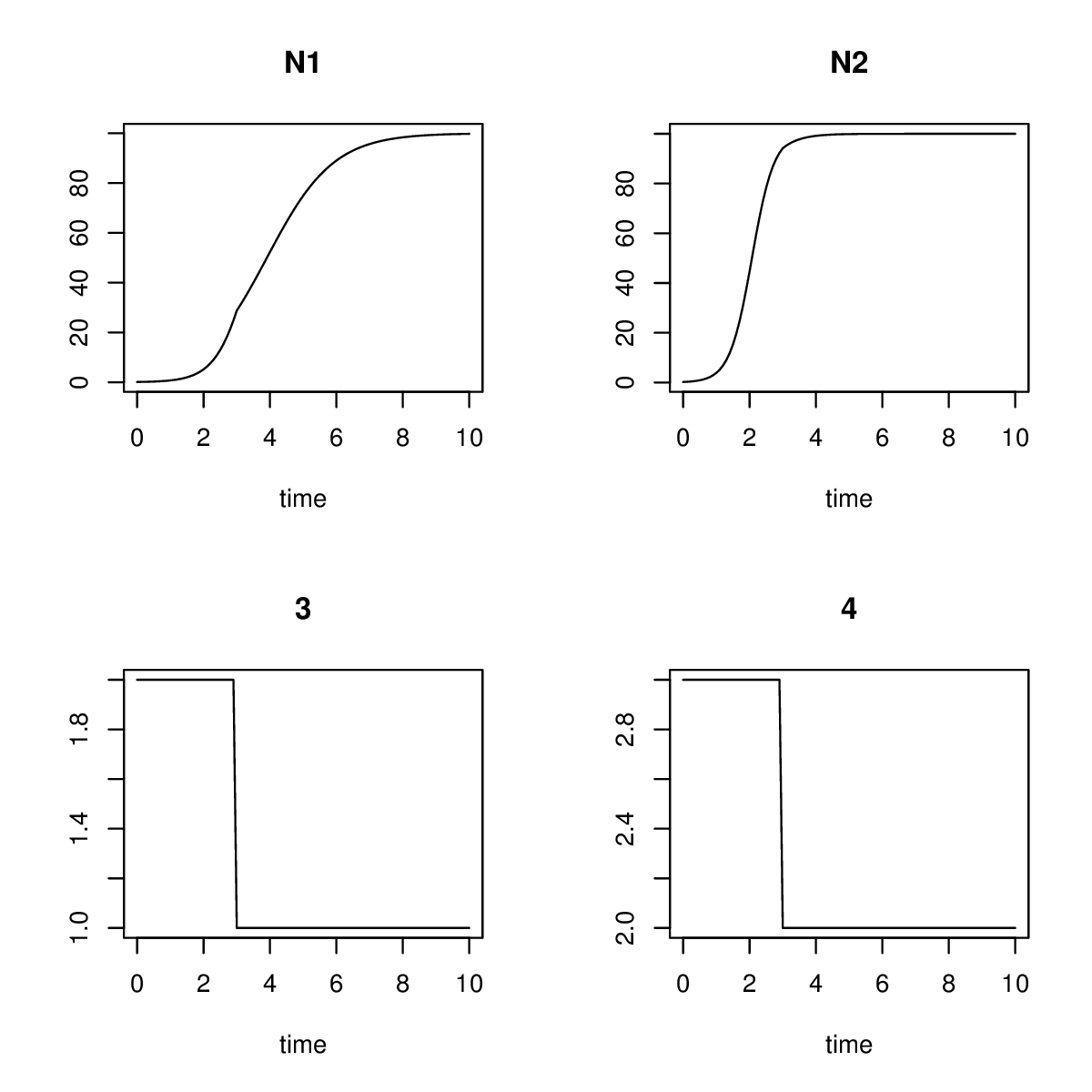
对于示例中的少量状态变量,使用approxfun与包stats分离的信号看起来不那么通用,但速度可能更快。
作为进一步的改进,人们可以考虑用一个更平稳的过渡来代替“艰难”的过渡。然后,可以直接将其表述为不需要approx、approxfun或approxTime的函数。
编辑2:
Package simecol导入deSolve,我们只需要从它获得一个小的函数。因此,不必加载simecol,也可以在代码中显式地包含approxTime函数。从数据帧到矩阵的转换提高了性能,但是在这种情况下,矩阵仍然是首选的。
approxTime <- function(x, xout, ...) {
if (is.data.frame(x)) {x <- as.matrix(x); wasdf <- TRUE} else wasdf <- FALSE
if (!is.matrix(x)) stop("x must be a matrix or data frame")
m <- ncol(x)
y <- matrix(0, nrow=length(xout), ncol=m)
y[,1] <- xout
for (i in 2:m) {
y[,i] <- as.vector(approx(x[,1], x[,i], xout, ...)$y)
}
if (wasdf) y <- as.data.frame(y)
names(y) <- dimnames(x)[[2]]
y
} 页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/62594803
复制相关文章
相似问题

