如何将图例手动添加到ggplot中
如何将图例手动添加到ggplot中
提问于 2020-09-20 08:22:07
我想手动添加一个图例到r。我的代码的问题是它没有显示正确的符号(蓝色点,蓝色虚线和红色实线)。这是密码和情节。
predict_ID1.4.5.6.7 <- predict(lm_mRNATime, ID1.4.5.6.7)
ID1.4.5.6.7$predicted_mRNA <- predict_ID1.4.5.6.7
colors <- c("data" = "Blue", "predicted_mRNA" = "red","fit"="Blue")
ggplot( data = ID1.4.5.6.7, aes(x=Time,y=mRNA,color="data")) +
geom_point()+
scale_x_discrete(limits=c('0','20','40','60','120'))+
labs(title="ID-1,ID-4,ID-5,ID-6,ID-7",y="mRNA", x="Time [min]", color = "Legend") +
scale_color_manual(values = colors)+
geom_line(aes(x=Time,y=predicted_mRNA,color="predicted_mRNA"),lwd=1.3)+
geom_smooth(method = "lm",aes(color="fit",lty=2),se=TRUE,lty=2)+
scale_color_manual(values = colors)+
theme(plot.title = element_text(hjust = 0.5),plot.subtitle = element_text(hjust = 0.5))
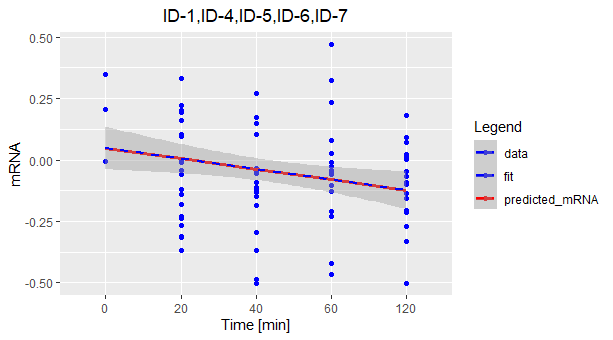
如何修改代码以获得与图例中的情节相关联的符号?
回答 1
Stack Overflow用户
回答已采纳
发布于 2020-09-20 09:24:52
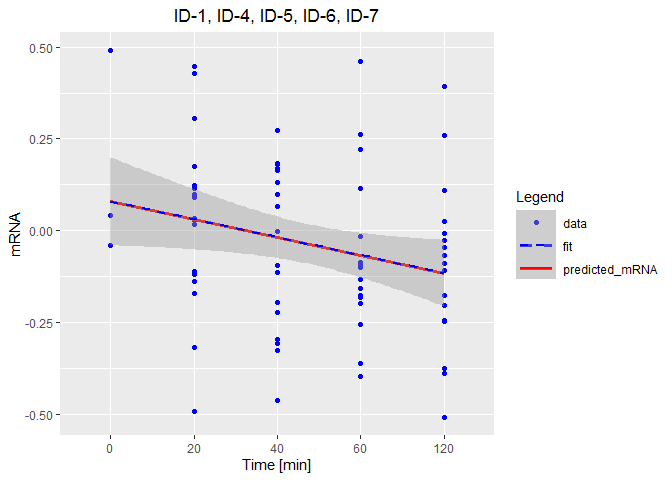
这里最困难的部分是为演示目的重新创建数据集。最好增加一个可重复的例子。无论如何,下面的内容应该是接近的:
library(ggplot2)
set.seed(123)
ID1.4.5.6.7 <- data.frame(Time = c(rep(1, 3),
rep(c(2, 3, 4, 5), each = 17)),
mRNA = c(rnorm(3, 0.1, 0.25),
rnorm(17, 0, 0.25),
rnorm(17, -0.04, 0.25),
rnorm(17, -0.08, 0.25),
rnorm(17, -0.12, 0.25)))
lm_mRNATime <- lm(mRNA ~ Time, data = ID1.4.5.6.7)现在,我们通过添加一个自定义颜色指南来运行您的代码:
predict_ID1.4.5.6.7 <- predict(lm_mRNATime, ID1.4.5.6.7)
ID1.4.5.6.7$predicted_mRNA <- predict_ID1.4.5.6.7
colors <- c("data" = "Blue", "predicted_mRNA" = "red", "fit" = "Blue")
p <- ggplot( data = ID1.4.5.6.7, aes(x = Time, y = mRNA, color = "data")) +
geom_point() +
geom_line(aes(x = Time, y = predicted_mRNA, color = "predicted_mRNA"),
lwd = 1.3) +
geom_smooth(method = "lm", aes(color = "fit", lty = 2),
se = TRUE, lty = 2) +
scale_x_discrete(limits = c('0', '20', '40', '60', '120')) +
scale_color_manual(values = colors) +
labs(title = "ID-1, ID-4, ID-5, ID-6, ID-7",
y = "mRNA", x = "Time [min]", color = "Legend") +
guides(color = guide_legend(
override.aes = list(shape = c(16, NA, NA),
linetype = c(NA, 2, 1)))) +
theme(plot.title = element_text(hjust = 0.5),
plot.subtitle = element_text(hjust = 0.5),
legend.key.width = unit(30, "points"))
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/63976953
复制相关文章
相似问题

