用Arviz绘制的旧PyMC3风格分组跟踪图
用Arviz绘制的旧PyMC3风格分组跟踪图
提问于 2020-10-25 20:25:27
我有一个老博客,在那里我正在训练一个PyMC3模型。您可以找到blogpost 这里,但是模型的要点如下所示。
with pm.Model() as model:
mu_intercept = pm.Normal('mu_intercept', mu=40, sd=5)
mu_slope = pm.HalfNormal('mu_slope', 10, shape=(n_diets,))
mu = mu_intercept + mu_slope[df.diet-1] * df.time
sigma_intercept = pm.HalfNormal('sigma_intercept', sd=2)
sigma_slope = pm.HalfNormal('sigma_slope', sd=2, shape=n_diets)
sigma = sigma_intercept + sigma_slope[df.diet-1] * df.time
weight = pm.Normal('weight', mu=mu, sd=sigma, observed=df.weight)
approx = pm.fit(20000, random_seed=42, method="fullrank_advi")在这个数据集中,我估计了Diet对鸡体重的影响。这就是追踪图的样子。
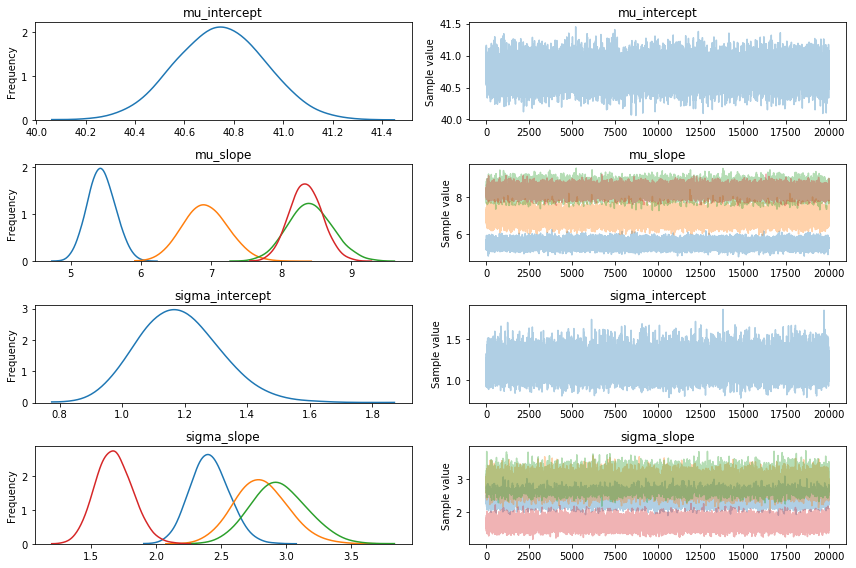
看看它有多漂亮!每种饮食都有自己的饮食路线!漂亮的!
Arviz变化
此跟踪图是使用较早的PyMC3 API创建的。现在,这个功能已经转移到arviz了。所以试着重做这个作品但是..。情节看起来很不一样。
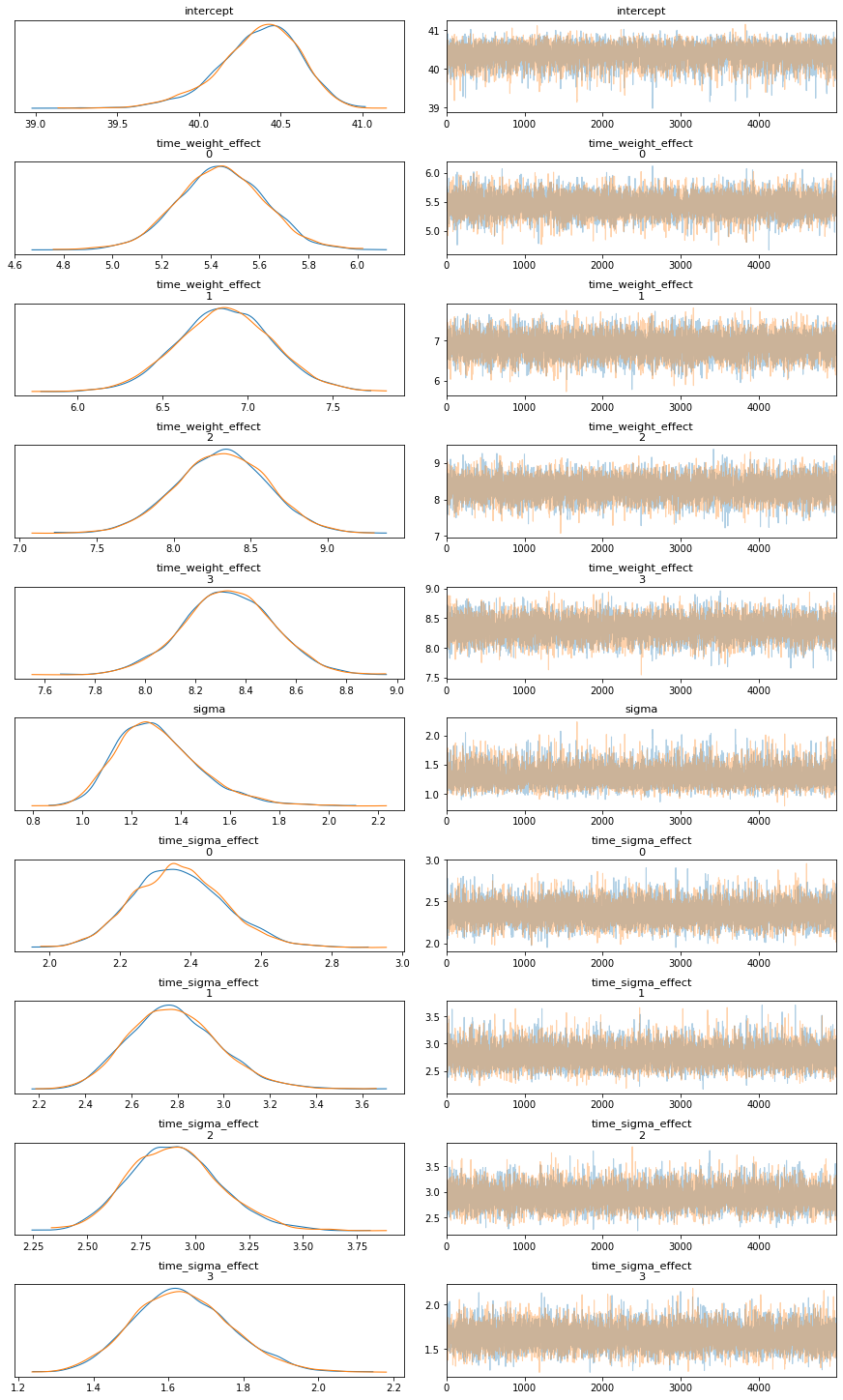
我在这里使用的代码略有不同。我现在正在使用pm.Data,但我怀疑这是否会导致这种差异。
with pm.Model() as mod:
time_in = pm.Data("time_in", df['time'].astype(float))
diet_in = pm.Data("diet_in", dummies)
intercept = pm.Normal("intercept", 0, 2)
time_effect = pm.Normal("time_weight_effect", 0, 2, shape=(4,))
diet = pm.Categorical("diet", p=[0.25, 0.25, 0.25, 0.25], shape=(4,), observed=diet_in)
sigma = pm.HalfNormal("sigma", 2)
sigma_time_effect = pm.HalfNormal("time_sigma_effect", 2, shape=(4,))
weight = pm.Normal("weight",
mu=intercept + time_effect.dot(diet_in.T)*time_in,
sd=sigma + sigma_time_effect.dot(diet_in.T)*time_in,
observed=df.weight)
trace = pm.sample(5000, return_inferencedata=True)我需要做些什么才能让每个饮食中的不同颜色恢复原样?
回答 1
Stack Overflow用户
回答已采纳
发布于 2020-10-26 08:00:57
在新的plot_trace函数中有一个参数。这起作用很大;
az.plot_trace(trace, compact=True)页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/64528416
复制相关文章
相似问题

