如何显示网络图中链接的状态?
如何显示网络图中链接的状态?
提问于 2021-01-05 15:36:46
我正在用networkx库创建一个图形,使用邻接列表作为输入文件。这些类型的列表只允许每行、源和目的地两个值(任意多个目的地)。
我正在过滤创建的条目文件,只添加向上的边缘。
- before filtering :
OK node1 node10
OK node10 node99
KO node20 node99
- after filtering :
node1 node10
node10 node99当我在看我的图表时,我看不出一个节点是否从前一个节点中消失了,因为我有很多。
例如,是否可以解析边缘的状态并以虚线显示红色节点?
是否有可能将我的图表与理论图表进行比较,并以不同的颜色显示缺失的链接?
回答 1
Stack Overflow用户
回答已采纳
发布于 2021-01-05 17:48:01
也许有一个更快的方法,但这是我的逻辑:
G -最终图(干净,边少)
T -理论图(原始的,更多的边)
首先计算理论图和最终图的边差:
diff = T.edges() - G.edges()然后,像您假装的那样,绘制在此差异内的节点和边缘:
if e in diff:
for n in e:
if n not in G:
res.add_node(n, color="red")
else:
res.add_node(n, color='#1f78b4') # default networkx color
res.add_edge(*e, style='--')在此差异范围内的节点和边缘通常会绘制:
else:
res.add_node(e[0], color = '#1f78b4') # default networkx color
res.add_node(e[1], color = '#1f78b4')
res.add_edge(*e, style='-')最后,查找节点的颜色和边缘的样式并绘制:
colors = [u[1] for u in res.nodes(data="color")]
styles = [res[u][v]['style'] for u,v in res.edges()]
nx.draw(res, with_labels =True, node_color = colors, style = styles)全码
def draw_theorethical(G,T):
diff = T.edges() - G.edges()
# print("Extra Edges in T", diff, "\nExtra Nodes in T", T.nodes() - G.nodes())
res = nx.Graph()
for e in T.edges():
if e in diff:
for n in e:
if n not in G:
res.add_node(n, color="red")
else:
res.add_node(n, color='#1f78b4') # Node invisible... default networkx color
res.add_edge(*e, style='--')
else:
res.add_node(e[0], color = '#1f78b4')
res.add_node(e[1], color = '#1f78b4')
res.add_edge(*e, style='-')
colors = [u[1] for u in res.nodes(data="color")]
styles = [res[u][v]['style'] for u,v in res.edges()]
nx.draw(res, with_labels =True, node_color = colors, style = styles)示例:
对于两个图,G和T:
T = nx.Graph()
T.add_edge("A","B")
T.add_edge("A","C")
T.add_edge("B","D")
T.add_edge("B","F")
T.add_edge("C","E")
G = nx.Graph(T)
G.remove_edge("C","E")
G.remove_node("E")draw_theorethical(G,T)绘制:
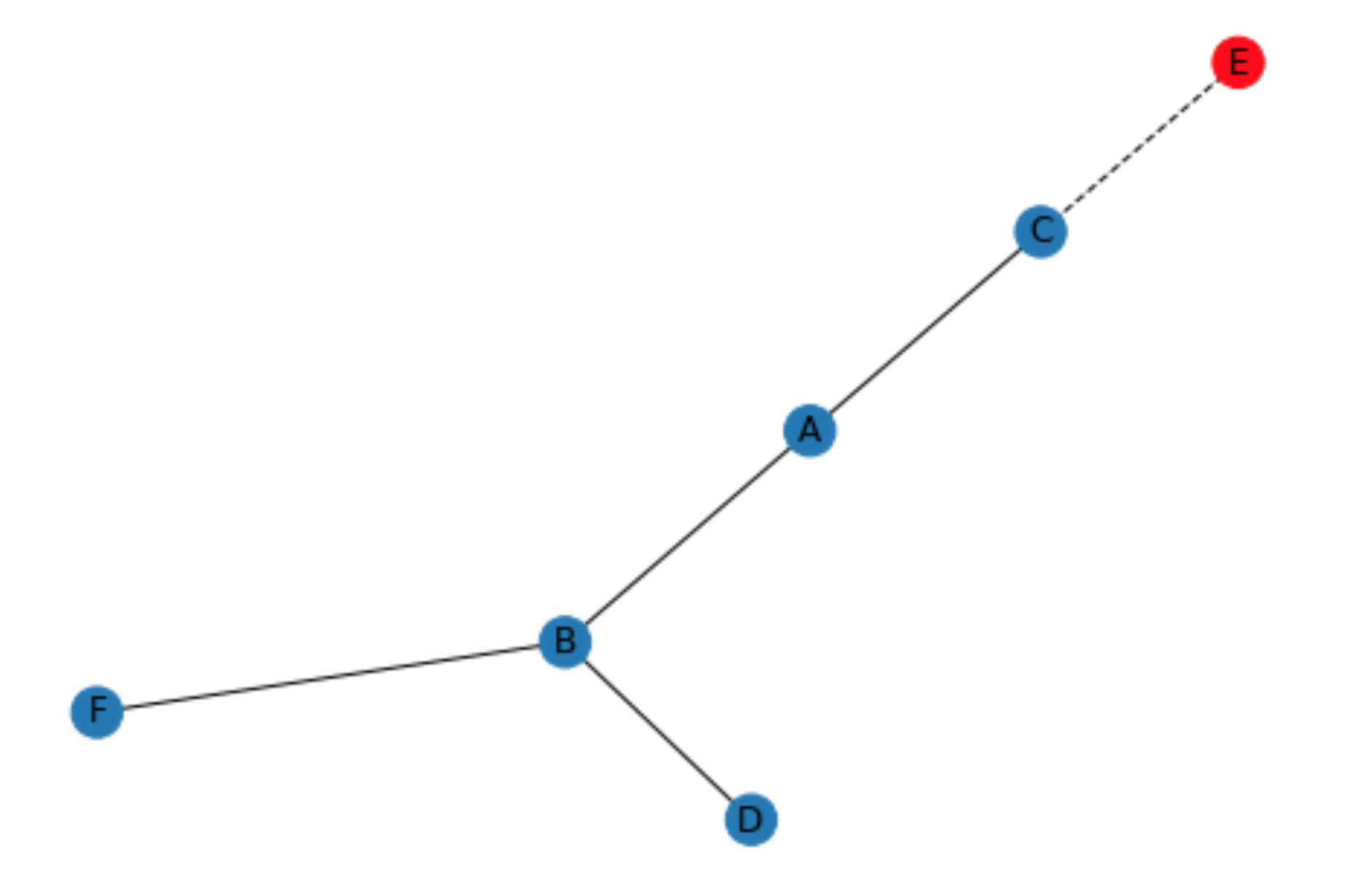
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/65581914
复制相关文章
相似问题

