R:清理GGally地块
R:清理GGally地块
提问于 2021-01-22 22:26:43
我正在使用R编程语言,我是一个新的GGally库。我在线学习了一些基本教程,并运行了以下代码:
#load libraries
library(GGally)
library(survival)
library(plotly)我更改了一些数据类型:
#manipulate the data
data(lung)
data = lung
data$sex = as.factor(data$sex)
data$status = as.factor(data$status)
data$ph.ecog = as.factor(data$ph.ecog)现在我想象:
#make the plots
#I dont know why, but this comes out messy
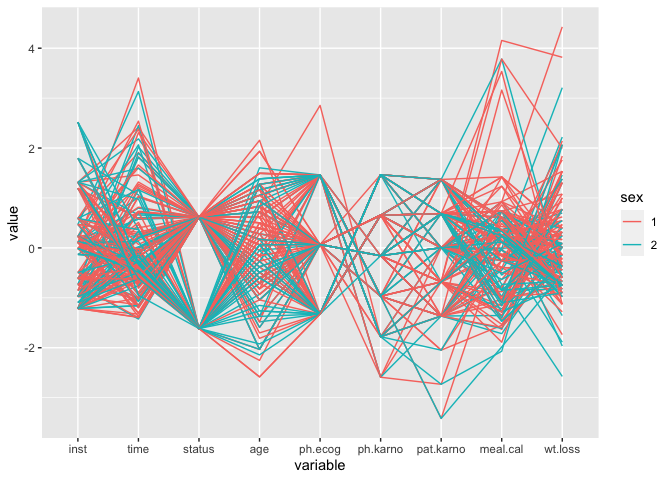
ggparcoord(data, groupColumn = "sex")
#Cleaner
ggparcoord(data)两个ggparcoord()代码段都成功运行,但是第一个代码段运行起来非常混乱(轴标签似乎已经损坏)。有办法修复标签吗?
在第二个图表中,很难知道因素变量是如何在其各自的轴上贴上标签的(例如,对于“性别”栏,是“男性”底部还是“女性”底部类型)。有人知道有没有办法解决这个问题吗?
最后,是否有一种为"ggally“对象使用"ggplotly()”函数的方法?
例如:
a = ggparcoord(data)
ggplotly(a)谢谢
回答 1
Stack Overflow用户
回答已采纳
发布于 2021-01-22 22:52:47
看起来,在添加groupColumn时,数据列被转换为一个因子。为了防止出现这种情况,可以将groupColumn从要绘制的columns中排除出来:
顺便说一句:不确定一般情况。但至少对于ggparcoord ggplotly works来说是这样。
library(GGally)
library(survival)
data(lung)
data = lung
data$sex = as.factor(data$sex)
data$status = as.factor(data$status)
data$ph.ecog = as.factor(data$ph.ecog)
#I dont know why, but this comes out messy
ggparcoord(data, seq(ncol(data))[!names(data) %in% "sex"], groupColumn = "sex")
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/65853563
复制相关文章
相似问题

