R中基于日期和时间的移动平均计算方法
R中基于日期和时间的移动平均计算方法
提问于 2021-02-18 22:35:06
我上传了数据。https://filebin.net/a29fn87b8wpfnos0/Plume_2.csv?t=iouc5vg7
它看起来像csv文件格式的
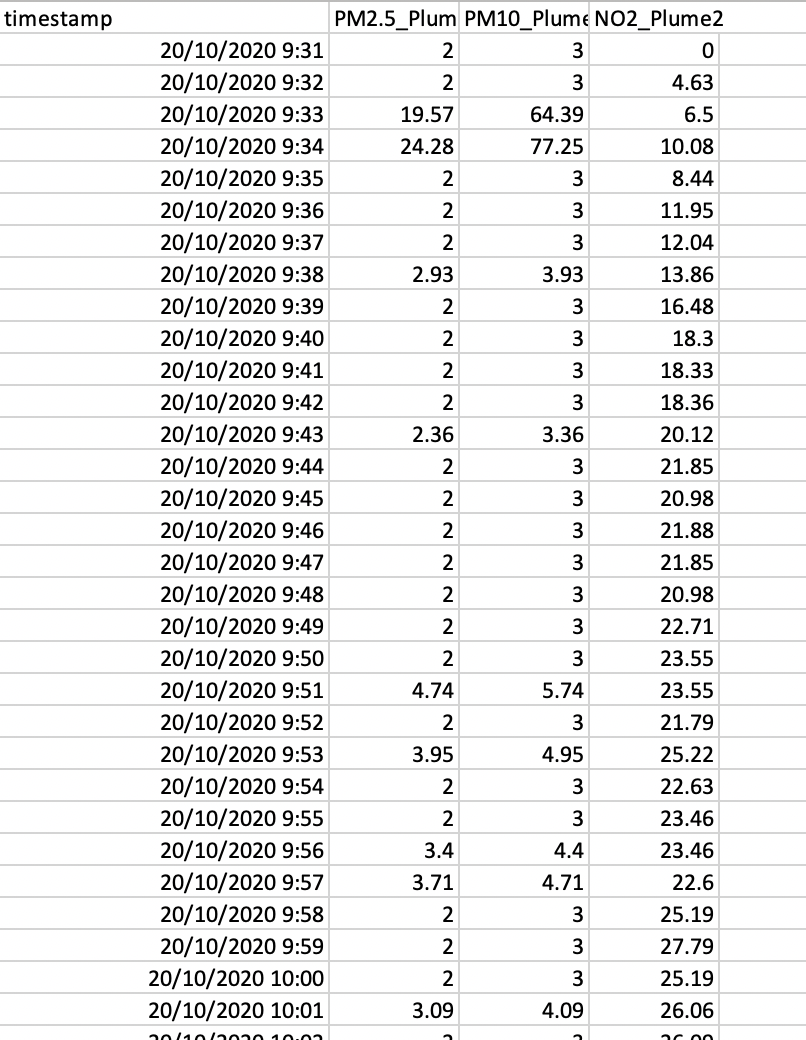
我试着寻找一个适合我的数据的正确答案。我找不到它,我花了大约一个月的时间来解决它。
首先,我需要做一个移动平均值:
- 30分钟
- 1小时
- 1天
- 1周
F 211
每PM2.5,PM10,NO2
但是,我不能手动使用这种类型的代码:
Plume_2$PM2.5_30min_ <- TTR ::SMA(Plume_2$pm2.5, n=31)
Plume_2$PM2.5_1hour_ <- TTR ::SMA(Plume_2$pm2.5, n=61)
Plume_2$PM2.5_1day_ <- TTR ::SMA(Plume_2$pm2.5, n=1441)
Plume_2$PM2.5_1week_ <- TTR ::SMA(Plume_2$pm2.5, n=10080)使用这些代码,n值不符合我的日期。
也使用了这段代码,看起来一般情况下效果不佳。
library(runner)
dates = Plume_2$timestamp
value = Plume_2$PM2.5_Plume2
Plume_2$MA <- mean_run(x = value, k = 7, lag = 1, idx = as.Date(dates))最后的输出将是一个包含这些不同移动平均线的图表。
有人能帮我吗?
回答 2
Stack Overflow用户
回答已采纳
发布于 2021-02-19 05:30:27
我希望这是一个令人满意的解决方案。
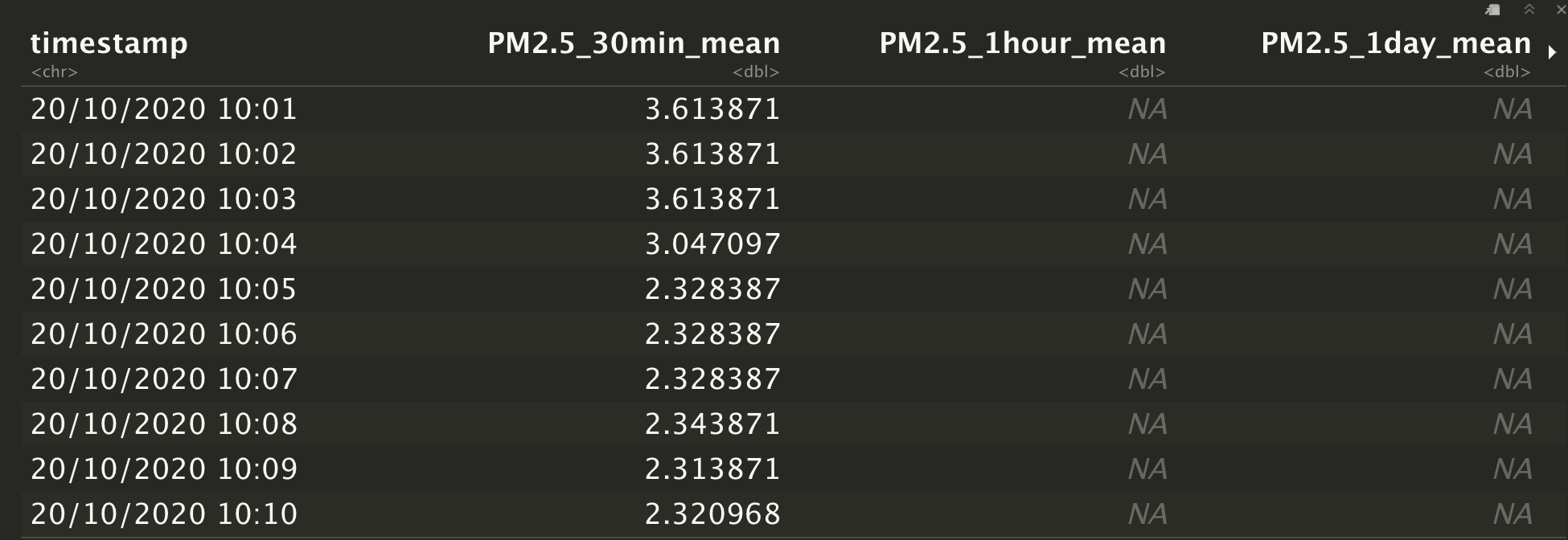
library(data.table)
dt <- fread("https://filebin.net/a29fn87b8wpfnos0/Plume_2.csv?t=phgmlykh")
dt[,.(timestamp,
PM2.5_30min_mean = frollmean(PM2.5_Plume2,31),
PM2.5_1hour_mean = frollmean(PM2.5_Plume2,61),
PM2.5_1day_mean = frollmean(PM2.5_Plume2, 1441),
PM2.5_1week_mean = frollmean(PM2.5_Plume2,10080))]结果显示为
然后,我想使用ggplot来绘制结果。这里我选择PM2.5_30min作为示例。
library(lubriate) # turn timestamp into POSIXct format with dmy_hm function
ggplot(dt2, aes(dmy_hm(timestamp), PM2.5_1hour_mean,na.rm = TRUE)) +
geom_line() +
scale_x_datetime()Stack Overflow用户
发布于 2021-02-20 02:47:32
使用动物园的rollmeanr函数和来自dplyr的across可以帮助您完成这一任务。
library(dplyr)
library(zoo)
df <- read.csv('https://filebin.net/a29fn87b8wpfnos0/Plume_2.csv?t=up70ngy3')
df %>%
mutate(across(PM2.5_Plume2:NO2_Plume2,
list(avg_30min = ~rollmeanr(.x, 30, fill = NA),
avg_hour = ~rollmeanr(.x, 60, fill = NA),
avg_day = ~rollmeanr(.x, 1440, fill = NA),
avg_week = ~rollmeanr(.x, 10080, fill = NA)))) -> result
result页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/66269164
复制相关文章
相似问题

