绘制dr4pl剂量响应曲线,以及如何与ggplot2集成?
绘制dr4pl剂量响应曲线,以及如何与ggplot2集成?
提问于 2021-03-25 19:44:13
我试图建立一种高通量的方法,从一个大型筛选实验中绘制出剂量反应曲线。棱镜显然有最简单的方法做剂量-反应曲线很好,但我不能复制和粘贴这么多的数据。
由于CRAN删除了drc,所以包dr4pl似乎是可行的,但目前可用的指令非常少。
#make data frame
dose <- c("0.078125","0.156250","0.312500","0.625000","1.250000","2.500000","5.000000","10.000000","20.000000")
POC<-c("1.05637425", "0.87380081", "0.79171200", "0.83166848", "0.77361290", "0.35199288", "0.19404609", "0.09079221", "0.09850658")
data<-data.frame(dose, POC)
#use the dr4pl pakcage to calculate curve and IC50 etc
model<-dr4pl(POC~dose, data)
summary.model <- summary(model)
summary.model$coefficients
#plot this
plot(dr4pl(POC~dose, data=data))
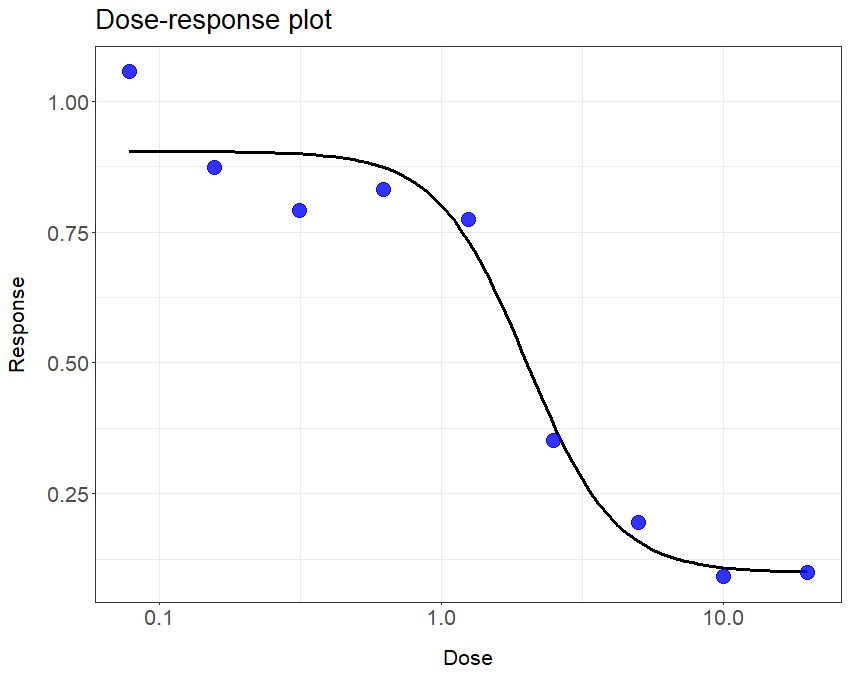
以上将生成我需要使用dr4pl的曲线类型,并给我IC50。但是,我如何在一幅图上绘制多个数据集/曲线?
理想情况下,我更愿意用ggplot2:plot+geom_point()绘制数据,并将dr4pl摘要作为+stat_smooth()模型添加到剂量响应行中,如果这有意义的话?但我不知道该怎么做。
如能提供任何帮助,将不胜感激。
回答 1
Stack Overflow用户
回答已采纳
发布于 2021-03-26 01:07:14
我可以得到大部分的方式,但不是所有的方式。主要步骤是为predict()对象编写一个dr4pl方法:
predict.dr4pl <- function (object, newdata=NULL, se.fit=FALSE, level, interval) {
xseq <- if (is.null(newdata)) object$data$Dose else newdata$x
pred <- MeanResponse(xseq, object$parameters)
if (!se.fit) {
return(pred)
}
qq <- qnorm((1+level)/2)
se <- sapply(xseq,
function(x) car::deltaMethod(object,
"UpperLimit + (LowerLimit - UpperLimit)/(1 + (x/IC50)^Slope)")[["Estimate"]])
return(list(fit=data.frame(fit=pred,lwr=pred-qq*se,
upr=pred+qq*se), se.fit=se))
}我包括了一种通过delta方法计算置信区间的有点麻烦的方法--这可能不太可靠(引导可能更好.)
它对您的数据工作正常(某种程度上)(将名称更改为dd,因为有时命名数据data (fortunes::fortune("dog"))很危险)。
dd <- data.frame(dose = c(0.078125,0.156250,0.312500,0.625000,1.25,
2.50,5.0,10.0,20.0),
POC = c(1.05637425, 0.87380081, 0.79171200,
0.83166848, 0.77361290, 0.35199288,
0.19404609, 0.09079221, 0.09850658))
library(dr4pl)
ggplot(dd, aes(dose,POC)) + geom_point() +
geom_smooth(method="dr4pl",se=TRUE) + coord_trans(x="log10")
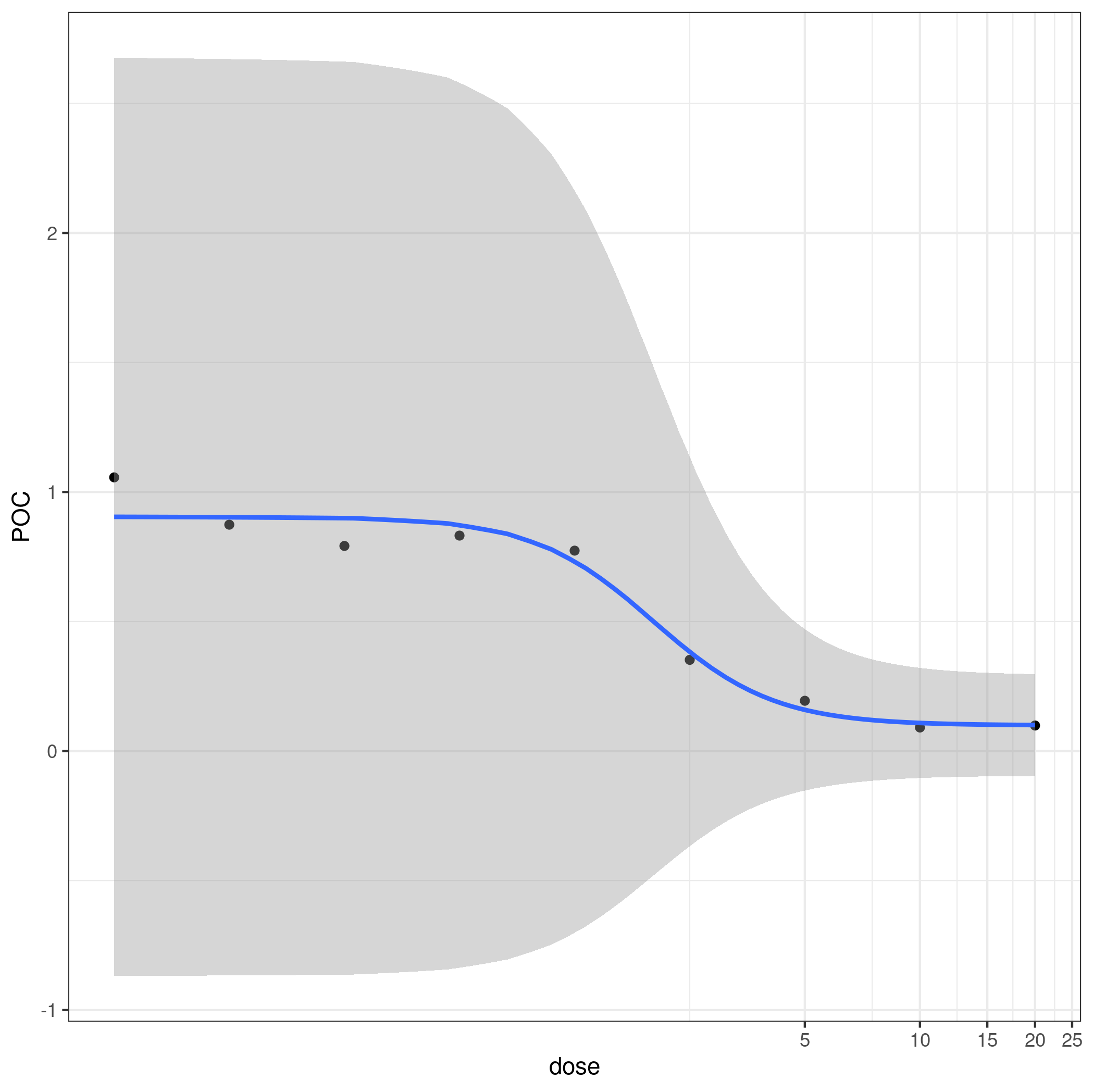
se=FALSE
dr4pl将x轴默认设置为10比例尺,但是标准的scale_x_log10()错误了,因为它是在拟合和预测之前应用的,所以如果轴是在非常宽的对数尺度上,那么使用coord_trans(x="log10")
-
coord_trans()就不会发挥那么好的作用--我尝试了上面的例子和软件包中的sample_data_1数据,但是没有起作用。
但恐怕我已经花了足够的时间在这上面了。
如果使用上面的predict方法分别在所需范围内生成所需的值,然后使用geom_line() + geom_ribbon()将信息添加到绘图中,则会更加健壮.
如果您愿意首先符合模型(geom_smooth之外),您可以这样做(这是使用来自dr4pl包的sample_data_1 -它来自于?dr4pl中的第一个示例)
model2 <- dr4pl(dose = sample_data_1$Dose,
response = sample_data_1$Response)
ggplot(sample_data_1, aes(Dose,Response)) + geom_point() +
stat_function(fun=function(x) predict(model2,newdata=data.frame(x=x))) +
scale_x_log10()它对x轴的缩放/不缩放顺序不那么敏感。
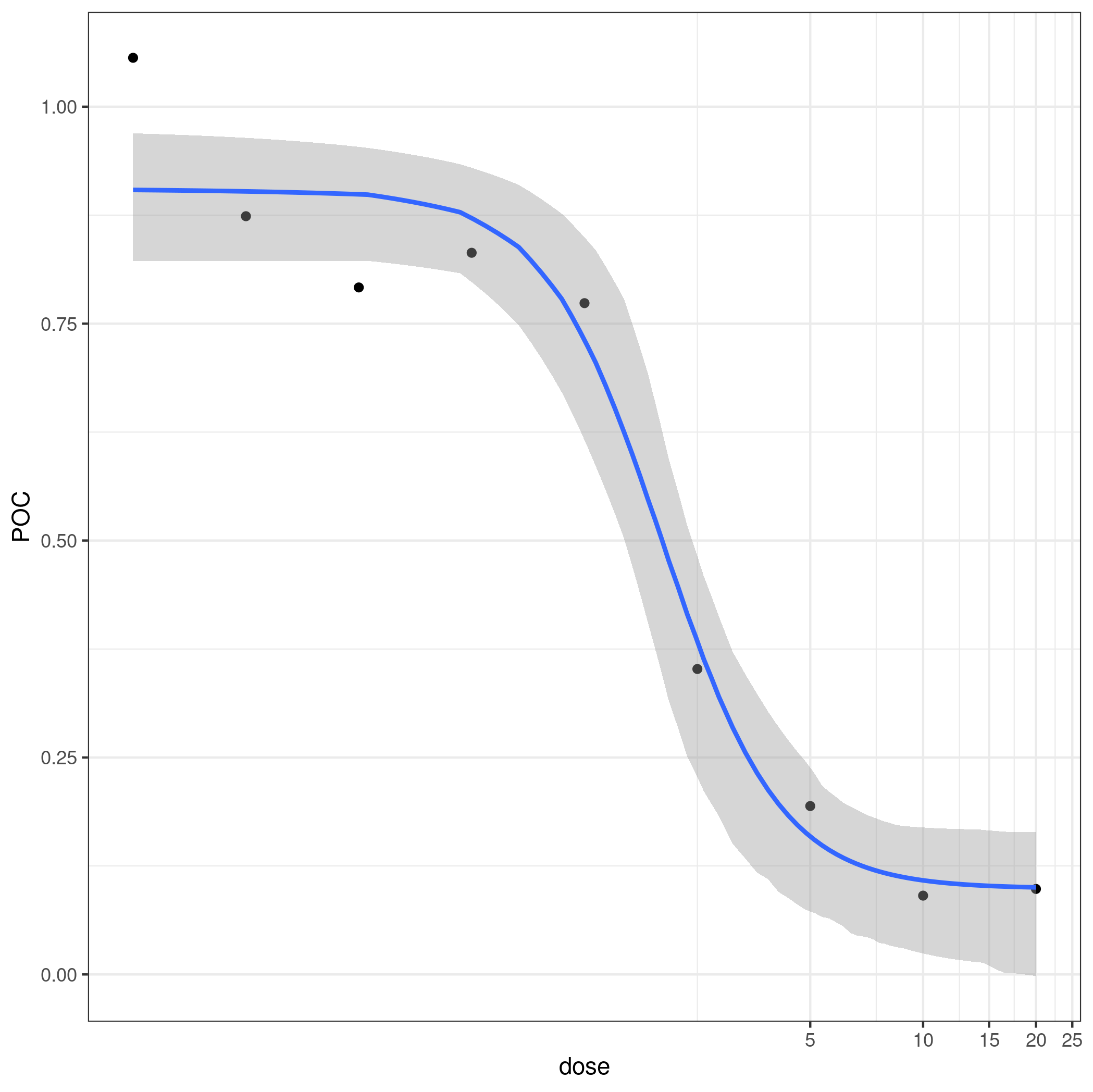
改进的但缓慢的引导CIs:
predictdf.dr4pl <- function (model, xseq, se, level, nboot=200) {
pred <- MeanResponse(xseq, model$parameters)
if (!se) {
return(base::data.frame(x=xseq, y=pred))
}
## bootstrap residuals
pred0 <- MeanResponse(model$data$Dose, model$parameters)
res <- pred0-model$data$Response
bootres <- matrix(nrow=length(xseq), ncol=nboot)
pb <- txtProgressBar(max=nboot,style=3)
for (i in seq(nboot)) {
setTxtProgressBar(pb,i)
mboot <- dr4pl(model$data$Dose,
pred0 + sample(res, size=length(pred0),
replace=TRUE))
bootres[,i] <- MeanResponse(xseq, mboot$parameters)
}
fit <- data.frame(x = xseq,
y=pred,
ymin=apply(bootres,1,quantile,(1-level)/2),
ymax=apply(bootres,1,quantile,(1+level)/2))
return(fit)
}
print(ggplot(dd, aes(dose,POC))
+ geom_point()
+ geom_smooth(method="dr4pl",se=TRUE) + coord_trans(x="log10")
)
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/66806526
复制相关文章
相似问题

