看上去像成组的酒馆
看上去像成组的酒馆
提问于 2021-10-13 09:55:25
我对我的分组条形图有一个问题,我想要可视化基因的表达,因为一些基因有很高的表达,所以我决定把ylim转换成不同的值,以便更好地可视化低值。然而,这些情节看起来是这样的,在第二张图片中,标有'y‘的条子被切断,在第二张图片中,限制设置为5000。有什么想法可以解释这是为什么,以及如何解决它?我使用了这段代码grouped_bars <-ggplot(data, aes(x=gene_name, y=Result, fill=Day))+geom_bar(stat="identity",colour="black", position="dodge")+ scale_fill_manual(values =c("blue","red")) + ylim(0, 5000)
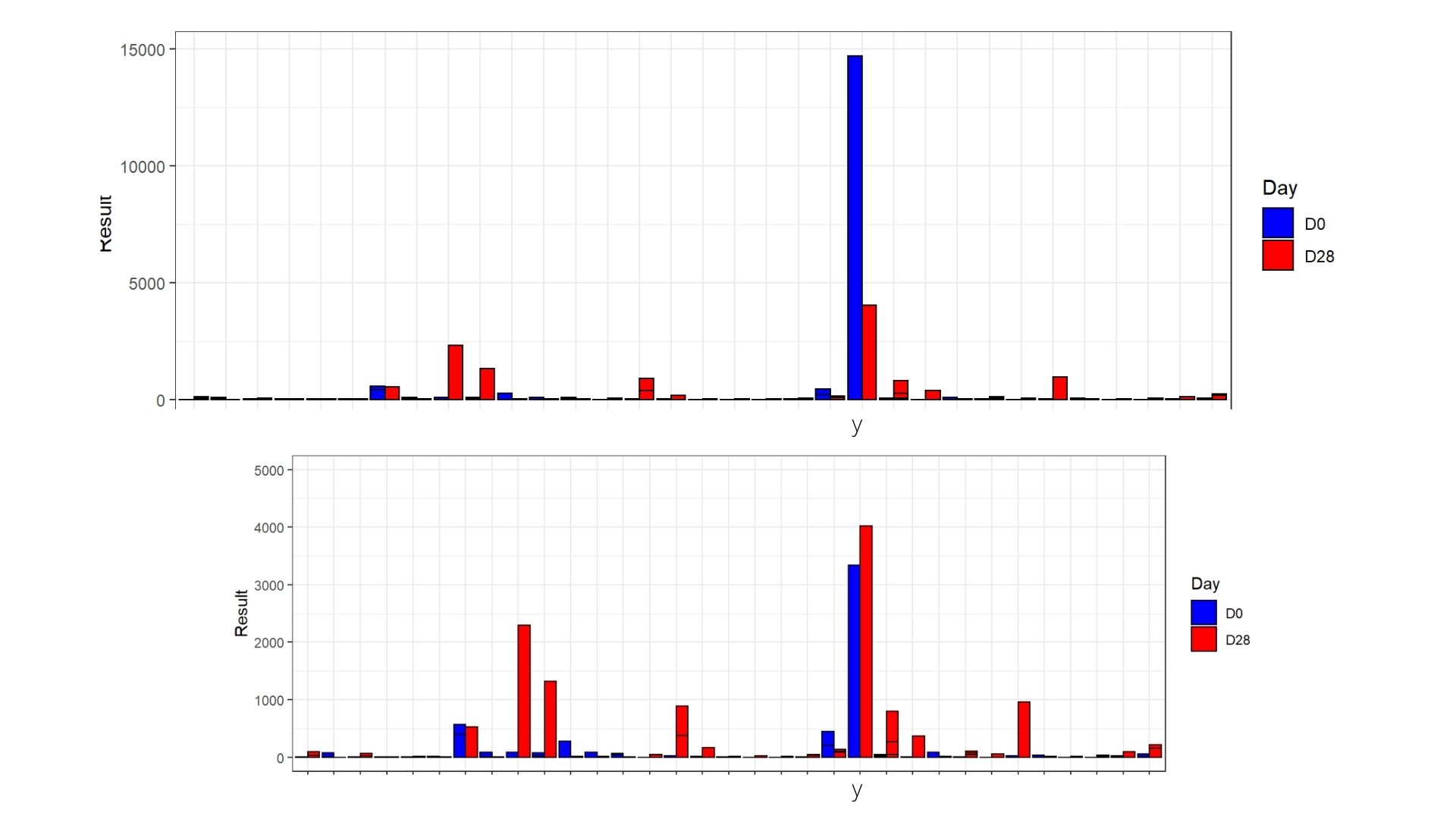
回答 1
Stack Overflow用户
回答已采纳
发布于 2021-10-13 15:39:02
使用coord_cartesian()而不是ylim()来避免你的酒吧迷路。
grouped_bars <- ggplot(data, aes(x=gene_name, y=Result, fill=Day)) +
geom_bar(stat="identity",colour="black", position="dodge") +
scale_fill_manual(values =c("blue","red")) +
coord_cartesian(ylim=c(0,5000))
grouped_bars页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/69553348
复制相关文章
相似问题

