在R中创建一个创建新向量的循环
在R中创建一个创建新向量的循环
提问于 2022-11-07 20:19:31
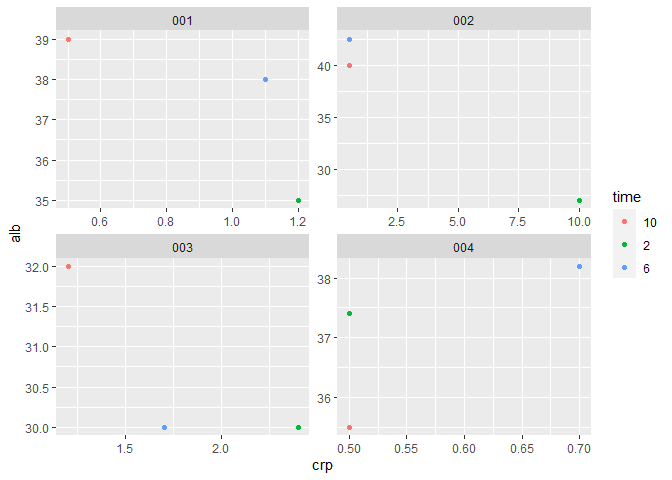
我有70个病人的数据集。在6个不同的数据点,获得了2个可能相互关联的实验室值。在这里您可以看到一些提取的数据。
id w2_crp w2_alb w6_crp w6_alb w10_crp w10_alb
001 1.2 35 1.1 38 0.5 39
002 10 27 0.5 42.5 0.5 40
003 2.4 30 1.7 30 1.2 32
004 0.5 37.4 0.7 38.2 0.5 35.5对于每个病人,我想在相应的时间点绘制x轴上的crp值和y轴上的白蛋白值。
我为10个第一个ID制作了这些向量:
vec1 <- pull(df, w2_crp)
vec2 <- pull(df, w2_alb)
...
crp1 <- (c(first(vec1)), (first(vec3)), (first(vec5))) 和白蛋白相似的载体,并且通常用plot_ly(df, x ~crp1, y ~alb1, type = "scatter", mode = "lines")作图,但这显然是非常乏味的。您有什么想法吗?如何用for循环来自动创建向量并将它们绘制成图呢?我试过了但经常出错..。我很感谢你的帮助!
回答 1
Stack Overflow用户
发布于 2022-11-07 23:28:00
我假设列名中的数字是时间点。如果是这样,你可以这样做:
library(tidyverse)
#example data
dat <- read_table("id w2_crp w2_alb w6_crp w6_alb w10_crp w10_alb
001 1.2 35 1.1 38 0.5 39
002 10 27 0.5 42.5 0.5 40
003 2.4 30 1.7 30 1.2 32
004 0.5 37.4 0.7 38.2 0.5 35.5")
#make each timepoint a row and each group a column
new_dat <- dat |>
pivot_longer(-id, names_pattern="\\w(\\d+)_(\\w+)",
names_to = c("time", "type")) |>
pivot_wider(names_from = type, values_from = value)
new_dat
#> # A tibble: 12 x 4
#> id time crp alb
#> <chr> <chr> <dbl> <dbl>
#> 1 001 2 1.2 35
#> 2 001 6 1.1 38
#> 3 001 10 0.5 39
#> 4 002 2 10 27
#> 5 002 6 0.5 42.5
#> 6 002 10 0.5 40
#> 7 003 2 2.4 30
#> 8 003 6 1.7 30
#> 9 003 10 1.2 32
#> 10 004 2 0.5 37.4
#> 11 004 6 0.7 38.2
#> 12 004 10 0.5 35.5
#plot data
new_dat|>
ggplot(aes(crp, alb, color = time))+
geom_point()+
facet_wrap(~id, scales = "free")
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/74352487
复制相关文章
相似问题

