光栅和形状文件不使用Geopandas、Rasterio和Contextily排列
我试图让一个DEM光栅与Python中的shapefile对齐,但是不管我做什么,它都不会出现。这是实验室练习,整个练习的其余部分依赖于这些排列,因为我将从栅格和多边形层中提取数据到点层。
我知道如何在ArcGIS中“手工”完成所有这些操作,但练习的重点是使用R或Python (教授用R做了一个示例,但我们可以使用哪种方法,过去几个月我一直在为一个工作项目学习Python )。在课堂笔记中,他说这两个文件都在EPSG 3847中,但是shapefile缺少CRS,所以我在地质公园中添加了CRS。
DEM似乎是EPSG 3006 (尽管它应该在3847),所以我尝试将它转换为EPSG 3847,但它仍然没有出现。于是,我试着用另一种方式将shapefile转换为EPSG3006,这也没有帮助。
import contextily as cx
import geopandas as gpd
import rasterio
from rasterio.plot import show
from rasterio.crs import CRS
from rasterio.plot import show as rioshow
import matplotlib.pyplot as plt #data files
abisveg = gpd.read_file(r'/content/drive/MyDrive/Stackoverflow/Sweden/abisveg_polygon.shp')
abisveg_3847 = abisveg.set_crs(epsg = 3847)
abisveg_3006 = abisveg_3847.to_crs(epsg = 3006)
src = rasterio.open(r'/content/drive/MyDrive/Stackoverflow/Sweden/nh_75_6.tif')
DEM = src.read() ### creating plot grid
fig = plt.figure(figsize = (20,20), constrained_layout = True)
gs = fig.add_gridspec(1,3)
ax1 = fig.add_subplot(gs[0,0])
ax2 = fig.add_subplot(gs[0,1], sharex = ax1, sharey = ax1)
ax3 = fig.add_subplot(gs[0,2], sharex = ax1, sharey = ax1)
### Plot 1 - Basemap Only
abisveg_3006.plot(ax = ax1, color = 'none')
cx.add_basemap(ax1, crs = 3006)
ax1.set_aspect('equal')
ax1.set_title("Basemap of AOI")
### Plot 2 - DEM
# abisveg_3847.plot(ax = ax2, color = 'none')
show(DEM, ax=ax2, cmap = "Greys")
cx.add_basemap(ax2, crs = 3006)
ax2.set_aspect('equal')
ax2.set_title('Digitial Elevation Model of AOI')
### Plot 3 - Vegetation Types
abisveg_3006.plot(ax = ax3, column = "VEGKOD", cmap = "viridis")
cx.add_basemap(ax3, crs = 3006)
ax3.set_aspect('equal')
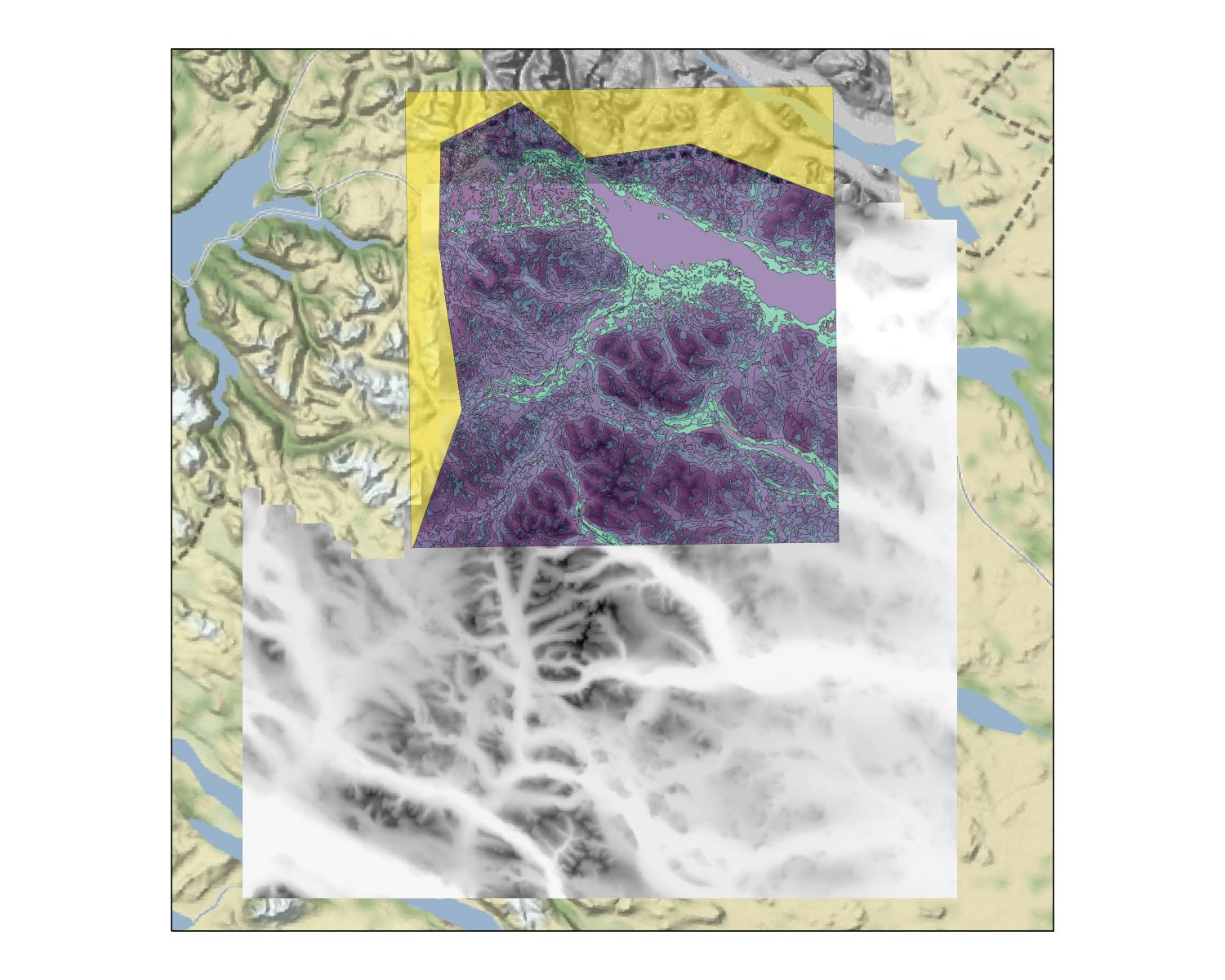
ax3.set_title("Vegetation Types") 3缺少DEM的面板地图:https://i.imgur.com/taG2U9Q.jpg
试图绘制Matplotlib中的文件没有工作,b/c它们根本不对齐。我正在为basemap使用上下文,并将basemap CRS设置为EPSG 3847 (或3006,取决于我使用的GIS文件的哪个版本)。无论投影如何,shapefile都会显示在正确的位置,但是Raster不会出现。奇怪的是,如果我在ArcGIS中打开所有的东西,它就会正确地排列起来。
如果我只是自己策划DEM,它就会出现,尽管我不知道它在哪里策划。
fig = plt.figure(figsize = (10,10), constrained_layout = True)
show(DEM, cmap = "Greys") DEM本身:https://i.imgur.com/KyYu7jc.jpg
我的代码在colab笔记本里:
https://colab.research.google.com/drive/1VAZ3dgf0QS2PPBOl8KJ2FXtB2oRj0qJ8?usp=share_link
档案在这里:
https://drive.google.com/drive/folders/1t-xvpIcLOIR9uYXOguJ7KyKqt7wuYSNc?usp=share_link
回答 1
Stack Overflow用户
发布于 2022-11-14 10:19:34
你可以试一试.它使用matplotlib/cartopy绘制并处理将数据和形状重新投影到绘图-crs的过程。
from pathlib import Path
from eomaps import Maps
import geopandas as gpd
p = Path(r"path to the data folder")
# read shapefile
abisveg = gpd.read_file(p / 'abisveg_polygon.shp').set_crs(epsg = 3847)
# create a map in epsg=3006
m = Maps(crs=3006, figsize=(10, 8))
# add stamen-terrain basemap
m.add_wms.OpenStreetMap.add_layer.stamen_terrain()
# plot shapefile (zorder=2 to be on top of the DEM)
m.add_gdf(abisveg, column=abisveg.VEGKOD, cmap="viridis", ec="k", lw=0.2, alpha=0.5, zorder=2)
# plot DEM
m2 = m.new_layer_from_file.GeoTIFF(p / "nh_75_6.tif", cmap="Greys", zorder=1)
m.ax.set_extent((589913.0408156103, 713614.6619114348, 7495264.310799116, 7618965.93189494),
Maps.CRS.epsg(3006))
https://stackoverflow.com/questions/74350387
复制相似问题

