如何利用DipLib测量分割图像的平均厚度
我试图测量平均厚度的分割和标记的图像。根据@CrisLuengo的建议,由于我未能成功地使用opencv,所以我转而使用diplib。我在这里找到了一个测量零件厚度的好例子,Measuring the distance between two lines using DipLib (PyDIP)。
问题:我可以让这段代码正常工作,并为我的图像的一个片段找到一个估计值,但是第二个片段的代码正在返回错误。以下是我所做的事:
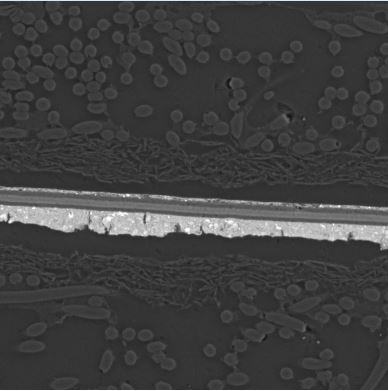
在导入图像并进行一些预处理之后,我最终得到了这个图像:

在这里,我对三种平均厚度感兴趣:
长而窄的白色部分的
- 厚度,顶部的
- 厚度,
黑色区域的厚度,中厚白色部分的厚度
为了做到这一点,我首先标记了图像,并选择了前2大区域(这是图像的顶部和底部白色部分)。
label_image=measure.label(opening1, connectivity=opening1.ndim)
props= measure.regionprops_table (label_image, properties=['label', "area", "coords"])
slc=label_image
rps=regionprops(slc)
areas=[r.area for r in rps]
id=np.argsort(props["area"])[::-1]
new_slc=np.zeros_like(slc)
for i in id[0:2]:
new_slc[tuple(rps[i].coords.T)]=i+1这将产生带有两个标签的标记图像:
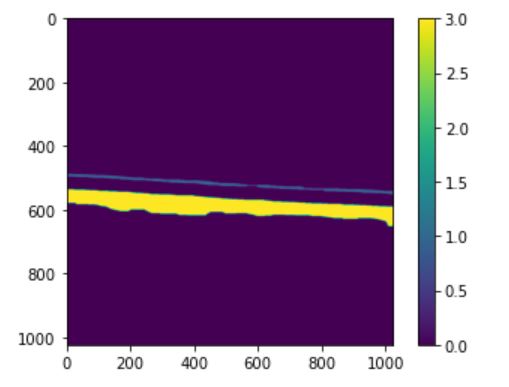
由于这里引入的方法只适用于一幅图像,所以我将我的部分分开了。换句话说,我将把重点放在每一个标有标签的部分:
第一个厚白色部件:
slc=label_image
rps=regionprops(slc)
areas=[r.area for r in rps]
id=np.argsort(props["area"])[::-1]
new_slc=np.zeros_like(slc)
for i in id[0:1]:
new_slc[tuple(rps[i].coords.T)]=i+1
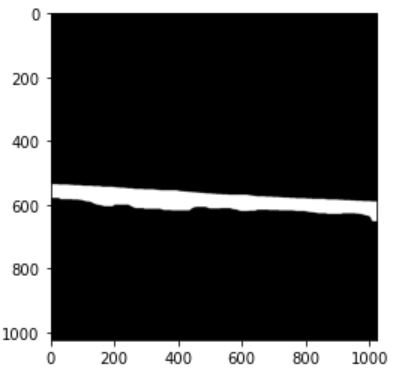
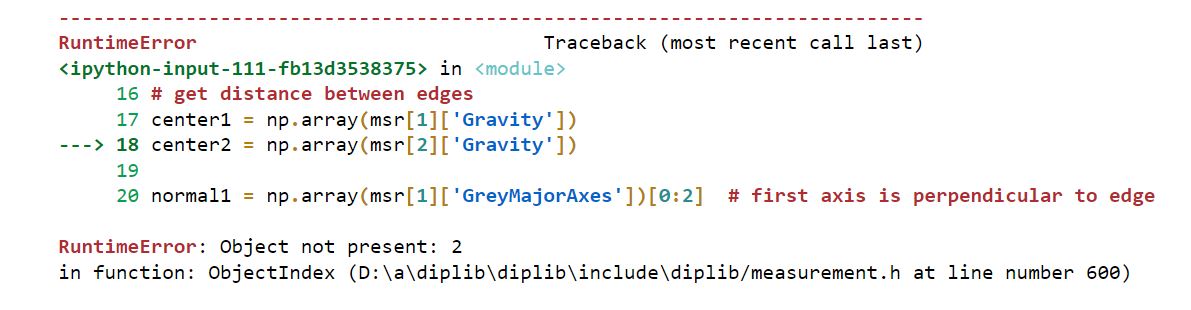
然后运行代码,它返回15.33μm厚度(与实际厚度14.66μm相比,这是一个很好的估计)。它还返回了这个图像。
我不知道如何解释这张图像,但看起来算法是试图显示符合边界的线,现在我想对薄的白色顶部部分做同样的事情。为了做到这一点,我首先选择最上面的白色部分:
rps=regionprops(slc)
areas=[r.area for r in rps]
id=np.argsort(props["area"])[::-1]
new_slc=np.zeros_like(slc)
for i in id[1:2]:
new_slc[tuple(rps[i].coords.T)]=i+1
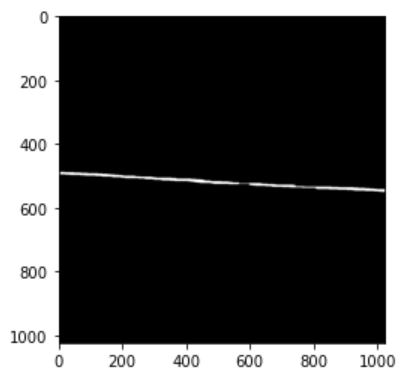
然后我运行了这里解释的算法:Measuring the distance between two lines using DipLib (PyDIP)
但是,它返回一个错误。
有人能告诉我,为什么算法不适用于我图像的第二部分?有什么区别,为什么我会犯错?
关于预处理的更新
====================
median=cv2.medianBlur(img,13)
ret, th = cv2.threshold(median, 0 , 255, cv2.THRESH_BINARY+cv2.THRESH_OTSU)
kernel=np.ones((3,15),np.uint8)
closing1 = cv2.morphologyEx(th, cv2.MORPH_CLOSE, kernel, iterations=2)
kernel=np.ones((1,31),np.uint8)
closing2 = cv2.morphologyEx(closing1, cv2.MORPH_CLOSE, kernel)
label_image=measure.label(closing2, connectivity=closing2.ndim)
props= measure.regionprops_table (label_image, properties=['label'])
kernel=np.ones((1,13),np.uint8)
opening1= cv2.morphologyEx(closing2, cv2.MORPH_OPEN, kernel, iterations=2)
label_image=measure.label(opening1, connectivity=opening1.ndim)
props= measure.regionprops_table (label_image, properties=['label', "area", "coords"])原图:下面我展示了我的原始图像的低质量,所以你可以更好地理解为什么我会做所有的预处理。
回答 1
Stack Overflow用户
发布于 2022-09-23 06:03:47
对于细行,来自其他Q&A的程序不能工作,因为沿这条线的两条边太近了,程序无法将两者识别为单独的对象。
对于这样一条很细的线,你可以用更粗的线做一些不可能做到的事情:只要测量它的长度和面积,宽度就是这两条线的比例:
# `label_image` is as in the OP
# `id` is the label ID for the thin line
msr = dip.MeasurementTool.Measure(label_image.astype(np.uint32), features=['Size','Feret'])
area = msr[id]['Size'][0]
length = msr[id]['Feret'][0]
width = area / length请注意,如果不立即对图像进行二值化,则应该能够获得更精确的值。链接Q&A使用灰度输入图像来确定边缘的位置,比二值化后更精确。
https://stackoverflow.com/questions/73807919
复制相似问题

