拟合零膨胀泊松,在R中作图
拟合零膨胀泊松,在R中作图
提问于 2022-08-19 15:05:31
我有以下数据
data<-c(1L, 4L, 5L, 10L, 13L, 8L, 3L, 5L, 13L, 9L, 5L, 10L, 9L, 4L,
4L, 13L, 10L, 10L, 7L, 7L, 3L, 1L, 11L, 4L, 5L, 9L, 10L, 3L,
2L, 7L, 8L, 4L, 5L, 6L, 3L, 4L, 13L, 7L, 8L, 6L, 5L, 3L, 10L,
4L, 8L, 8L, 2L, 9L, 5L, 2L, 8L, 7L, 6L, 6L, 6L, 4L, 3L, 9L, 11L,
6L, 7L, 7L, 3L, 4L, 18L, 14L, 8L, 9L, 5L, 3L, 7L, 3L, 8L, 3L,
9L, 3L, 4L, 7L, 7L, 5L, 8L, 7L, 10L, 9L, 9L, 11L, 8L, 3L, 9L,
10L, 11L, 9L, 12L, 13L, 9L, 15L, 11L, 13L, 3L, 24L, 11L, 13L,
14L, 14L, 5L, 10L, 6L, 10L, 8L, 9L, 13L, 5L, 8L, 8L, 6L, 17L,
11L, 11L, 8L, 2L, 14L, 6L, 1L, 7L, 5L, 3L, 12L, 6L, 10L, 7L,
15L, 9L, 7L, 3L, 9L, 11L, 3L, 5L, 14L, 7L, 3L, 20L, 17L, 14L,
7L, 11L, 11L, 2L, 4L, 9L, 5L, 10L, 7L, 10L, 13L, 7L, 18L, 13L,
18L, 20L, 16L, 9L, 5L, 13L, 16L, 11L, 9L, 7L, 12L, 13L, 21L,
9L, 7L, 13L, 4L, 7L, 5L, 13L, 19L, 17L, 8L, 7L, 4L, 18L, 14L,
8L, 8L, 16L, 13L, 9L, 14L, 8L, 20L, 7L, 12L, 14L, 8L, 16L, 10L,
9L, 20L, 5L, 7L, 8L, 16L, 11L, 10L, 12L, 20L, 5L, 2L, 21L, 16L,
18L, 0L, 16L, 4L, 6L, 16L, 6L, 15L, 15L, 10L, 8L, 13L, 22L, 14L,
5L, 8L, 11L, 14L, 7L, 9L, 7L, 7L, 8L, 5L, 12L, 6L, 20L, 10L,
17L, 9L, 7L, 13L, 9L, 13L, 15L, 18L, 10L, 8L, 10L, 12L, 16L,
16L, 11L, 13L, 8L, 8L, 20L, 16L, 11L, 14L, 18L, 10L, 8L, 17L,
24L, 8L, 15L, 16L, 9L, 10L, 22L, 15L, 16L, 16L, 20L, 16L, 7L,
12L, 10L, 16L, 16L, 17L, 16L, 13L, 4L, 14L, 14L, 18L, 11L, 4L,
3L, 10L, 19L, 9L, 9L, 10L, 4L, 9L, 9L, 5L, 6L, 13L, 7L, 4L, 2L,
7L, 13L, 6L, 4L, 3L, 6L, 5L, 2L, 9L, 6L, 10L, 9L, 3L, 2L, 7L,
12L, 14L, 12L, 12L, 2L, 4L, 7L, 5L, 7L, 9L, 5L, 6L, 6L, 9L, 10L,
6L, 11L, 4L, 6L, 3L, 5L, 3L, 5L, 4L, 10L, 7L, 4L, 6L, 9L, 11L,
6L, 10L, 3L, 1L, 9L, 9L, 11L, 8L, 3L, 5L, 7L, 6L, 8L, 8L, 9L,
4L, 2L, 5L, 7L, 13L, 6L, 12L, 3L, 9L, 7L, 4L, 6L, 8L, 11L, 9L,
4L, 5L, 10L, 11L, 17L, 15L, 3L, 0L, 0L, 0L, 0L, 0L, 1L, 0L, 0L,
0L, 0L, 1L, 1L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 1L, 0L,
0L, 0L, 0L, 1L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L,
0L, 0L, 0L, 0L, 0L, 0L, 0L, 1L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L,
0L, 0L, 0L, 0L, 0L, 0L, 1L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L,
1L, 0L, 0L, 0L, 0L, 0L, 1L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L,
0L, 0L, 1L, 0L, 0L, 0L, 0L, 0L, 1L, 0L, 0L, 1L, 1L, 0L, 0L, 0L,
0L, 0L, 0L, 0L, 0L, 2L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 1L,
0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 2L, 0L, 0L, 1L, 0L, 0L, 0L, 0L,
0L, 1L, 1L, 0L, 0L, 0L, 0L, 0L, 1L, 0L, 1L, 2L, 1L, 2L, 0L, 1L,
0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 1L, 0L, 0L, 0L,
0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L,
3L, 16L, 17L, 6L, 6L, 9L, 6L, 12L, 6L, 13L, 6L, 5L, 9L, 6L, 14L,
2L, 17L, 4L, 10L, 6L, 1L, 15L, 8L, 8L, 5L, 7L, 7L, 8L, 12L, 2L,
3L, 7L, 11L, 6L, 9L, 10L, 11L, 11L, 4L, 12L, 1L, 7L, 6L, 3L,
8L, 11L, 7L, 6L, 5L, 5L, 11L, 7L, 7L, 6L, 7L, 5L, 7L, 10L, 5L,
4L, 7L, 5L, 9L, 7L, 14L, 10L, 4L, 9L, 5L, 10L, 12L, 14L, 6L,
5L, 12L, 5L, 3L, 8L, 8L, 4L, 9L, 9L, 12L, 2L, 8L, 5L, 4L, 5L,
1L, 4L, 4L, 7L, 6L, 8L, 10L, 13L, 9L, 4L, 8L, 8L, 9L, 12L, 4L,
7L, 6L, 5L, 5L, 7L, 2L, 5L, 10L, 0L, 4L, 6L, 5L, 3L, 8L, 2L,
1L, 1L, 6L, 6L, 1L, 2L, 5L, 9L, 10L, 7L, 10L, 3L, 12L, 7L, 4L,
1L, 5L, 6L, 6L, 5L, 4L, 1L, 5L, 0L, 8L, 6L, 4L, 1L, 7L, 5L, 3L,
8L, 3L, 0L, 3L, 2L, 0L, 6L, 10L, 0L, 8L, 3L, 0L, 1L, 1L, 5L,
7L, 0L, 1L, 0L, 3L, 1L, 9L, 2L, 8L, 1L, 0L, 0L, 5L, 1L, 0L, 2L,
1L, 0L, 7L, 1L, 2L, 0L, 0L, 4L, 4L, 10L, 0L, 6L, 4L, 3L, 0L,
4L, 1L, 3L, 1L, 0L, 0L, 0L, 5L, 0L, 6L, 6L, 3L, 5L, 0L, 4L, 0L,
2L, 3L, 5L, 2L, 4L, 3L, 1L, 1L, 0L, 2L, 0L, 3L, 0L, 3L, 4L, 4L,
7L, 0L, 0L, 1L, 9L, 0L, 3L, 0L, 4L, 0L, 3L, 4L, 5L, 0L, 0L, 4L,
3L, 0L, 1L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 1L, 0L, 1L,
0L, 0L, 1L, 0L, 0L, 1L, 0L, 1L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L,
0L, 0L, 1L, 0L, 0L, 0L, 1L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L, 0L,
0L, 0L, 0L, 1L, 1L, 0L, 1L, 0L, 0L, 1L, 0L, 1L, 0L, 0L, 0L, 1L,
0L, 0L, 0L, 1L, 0L, 0L, 1L, 2L, 0L, 0L, 0L, 2L, 0L, 0L, 0L, 0L,
1L, 0L, 0L, 1L, 1L, 0L, 0L, 0L, 0L, 1L, 1L, 0L, 0L, 0L, 0L, 0L,
0L, 0L, 0L, 1L, 1L, 0L, 0L, 0L, 0L, 1L, 0L, 0L, 1L, 2L, 0L, 0L,
0L, 0L, 2L, 0L, 1L, 1L, 0L, 0L, 0L, 0L, 13L, 10L, 13L, 10L, 11L,
8L, 27L, 8L, 12L, 20L, 15L, 9L, 10L, 3L, 8L, 13L, 16L, 13L, 12L,
13L, 10L, 14L, 14L, 10L, 10L, 7L, 13L, 12L, 12L, 23L, 7L, 12L,
6L, 7L, 10L, 8L, 13L, 16L, 10L, 11L, 18L, 7L, 15L, 18L, 10L,
9L, 15L, 4L, 3L, 9L, 12L, 2L, 6L, 4L, 4L, 8L, 4L, 7L, 11L, 9L,
7L, 9L, 15L, 7L, 7L, 14L, 15L, 6L, 3L, 7L, 6L, 22L, 7L, 8L, 6L,
12L, 7L, 11L, 10L, 6L, 10L, 6L, 5L, 16L, 11L, 11L, 6L, 9L, 10L,
4L, 14L, 7L, 6L, 4L, 9L, 4L, 7L, 10L, 11L, 8L, 6L, 7L, 3L, 8L,
8L, 12L, 7L, 13L, 5L, 4L, 10L, 6L, 8L, 7L, 11L, 3L, 3L, 5L, 4L,
4L, 11L, 3L, 3L, 3L, 3L, 7L, 4L, 5L, 3L, 5L, 1L, 5L, 2L, 5L,
6L, 6L, 4L, 3L, 6L, 7L, 3L, 8L, 1L, 3L, 5L, 9L, 9L, 10L, 6L,
9L, 7L, 5L, 5L, 10L, 6L, 9L, 2L, 6L, 6L, 1L, 6L, 4L, 5L, 3L,
3L, 3L, 3L, 3L, 2L, 6L, 1L, 5L, 3L, 4L, 9L, 3L, 8L, 5L, 7L, 5L,
10L, 5L, 4L, 0L, 8L, 6L, 4L, 6L, 7L, 4L, 3L, 1L, 3L, 3L, 6L,
5L, 7L, 3L, 7L, 2L, 2L, 6L, 4L, 3L, 3L, 2L, 2L, 4L, 2L, 5L, 5L,
7L, 3L, 5L, 2L, 2L, 1L, 5L, 1L, 3L, 2L, 5L, 3L, 1L, 4L, 0L, 1L,
4L, 3L, 2L, 2L, 2L, 6L, 3L, 4L, 2L, 2L, 8L, 4L, 3L, 6L, 6L, 2L,
4L, 11L, 3L, 4L, 4L, 5L, 5L, 1L, 5L, 2L, 7L, 3L, 2L, 4L, 2L,
3L, 6L, 3L, 11L, 7L, 5L, 9L, 5L, 6L, 5L, 9L, 6L, 5L, 7L, 1L,
14L, 7L, 7L, 7L, 2L, 5L, 5L, 9L, 2L, 9L, 2L, 6L, 2L, 9L, 4L,
3L, 4L, 9L, 7L, 6L, 5L, 4L, 5L, 6L, 4L, 5L, 2L, 5L, 4L, 7L, 3L,
9L, 6L, 9L, 7L, 2L, 7L, 6L, 7L, 3L, 4L, 8L, 3L, 8L, 10L, 3L,
3L, 5L, 4L, 8L, 6L, 5L, 4L, 5L, 1L, 6L, 6L, 8L, 9L, 5L, 10L,
1L, 8L, 7L, 7L, 6L, 5L, 1L, 5L, 8L, 11L, 2L, 6L, 7L, 6L, 5L,
20L, 8L, 10L, 7L, 5L, 2L, 5L, 3L, 17L, 6L, 5L, 0L, 1L, 1L, 9L,
1L)我运行了一个ZINB模型,我知道它最适合我的数据。我想在一个图表上演示这个分布是我最好的选择。我正在使用fitdist
library(fitdistrplus)
library(gamlss)
nb<-fitdist(data, "nbinom")
pois<-fitdist(data, "pois")
zinb<-fitdist(data, 'ZANBI',start = list(mu = 4, sigma = 0.2))
par(mfrow = c(2, 2))
plot.legend <- c("Negative binomial", "Poisson", "ZINB")我的问题是,正如我想证明nbinom和pois不是最合适的一样,我不能用零膨胀的泊松ZIP来做这件事。
我正在使用gamlss
zip<-fitdist(data, 'ZIP',start = list(mu = 7.09, sigma = 4.5))这里我使用了here中建议的值,考虑到mean(data[data != 0])和var(data[data != 0])。我总是得到:
Error in fitdist(data, "ZIP", start = list(mu = 7.09, sigma = 4.5)) :
the function mle failed to estimate the parameters,
with the error code 100
In addition: Warning messages:
1: In fitdist(data, "ZIP", start = list(mu = 7.09, sigma = 4.5)) :
The dZIP function should return a zero-length vector when input has length zero and not raise an error
2: In fitdist(data, "ZIP", start = list(mu = 7.09, sigma = 4.5)) :
The pZIP function should return a zero-length vector when input has length zero and not raise an error我如何绘制我的价值观的ZIP来证明不是最合适的呢?
回答 1
Stack Overflow用户
回答已采纳
发布于 2022-08-20 15:56:27
关于ZIP fit的下列论点对我有用:
- A start
sigma<1. - -Mead优化器
- A(下、上)界分别设置为
(0, Inf)和(0, 1)、H 211f 212
在您的data数组上运行以下代码的结果如下,这证实了零膨胀负二项式是最适合的(基于AIC和BIC)。
library(fitdistrplus)
library(gamlss)
nb<-fitdist(data, "nbinom")
pois<-fitdist(data, "pois")
zinb<-fitdist(data, 'ZANBI',start = list(mu = 4, sigma = 0.2))
zip<-fitdist(data, 'ZIP', start = list(mu = 7.09, sigma = 0.5), discrete=TRUE,
optim.method="Nelder-Mead", lower = c(0, 0), upper = c(Inf, 1))
print(nb)
print(pois)
print(zinb)
print(zip)
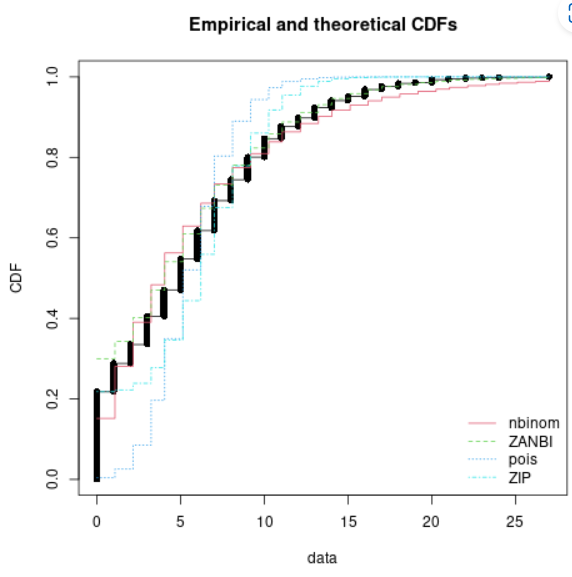
cdfcomp(list(nb, zinb, pois, zip))
gofstat(list(nb, zinb, pois, zip))唯一让我担心的是,ZIP拟合的估计参数的标准误差是NA.
部分输出
Fitting of the distribution ' nbinom ' by maximum likelihood
Parameters:
estimate Std. Error
size 1.007110 0.05297338
mu 5.548579 0.16643396
Fitting of the distribution ' pois ' by maximum likelihood
Parameters:
estimate Std. Error
lambda 5.548313 0.06522914
Fitting of the distribution ' ZANBI ' by maximum likelihood
Parameters:
estimate Std. Error
mu 6.8886199 0.1549058
sigma 0.3401722 0.0266448
Fitting of the distribution ' ZIP ' by maximum likelihood
Parameters:
estimate Std. Error
mu 7.0869552 NA
sigma 0.2171502 NA
Goodness-of-fit criteria
1-mle-nbinom 2-mle-ZANBI 3-mle-pois 4-mle-ZIP
Akaike's Information Criterion 7302.831 7141.004 10169.16 7981.985
Bayesian Information Criterion 7313.177 7151.350 10174.33 7992.331
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/73418769
复制相关文章
相似问题

