Python加权分位数为R wtd.quantile()
我想将R包Hmisc::wtd.quantile()转换为python。
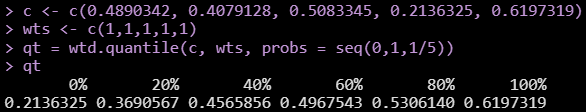
以下是R中的示例:
我以this为参考,逻辑似乎与R不同:
# First function
def weighted_quantile(values, quantiles, sample_weight = None,
values_sorted = False, old_style = False):
""" Very close to numpy.percentile, but supports weights.
NOTE: quantiles should be in [0, 1]!
:param values: numpy.array with data
:param quantiles: array-like with many quantiles needed
:param sample_weight: array-like of the same length as `array`
:return: numpy.array with computed quantiles.
"""
values = np.array(values)
quantiles = np.array(quantiles)
if sample_weight is None:
sample_weight = np.ones(len(values))
sample_weight = np.array(sample_weight)
assert np.all(quantiles >= 0) and np.all(quantiles <= 1), 'quantiles should be in [0, 1]'
if not values_sorted:
sorter = np.argsort(values)
values = values[sorter]
sample_weight = sample_weight[sorter]
# weighted_quantiles = np.cumsum(sample_weight)
# weighted_quantiles /= np.sum(sample_weight)
weighted_quantiles = np.cumsum(sample_weight)/np.sum(sample_weight)
return np.interp(quantiles, weighted_quantiles, values)
weighted_quantile(values = [0.4890342, 0.4079128, 0.5083345, 0.2136325, 0.6197319],
quantiles = np.arange(0, 1 + 1 / 5, 1 / 5),
sample_weight = [1,1,1,1,1])
>> array([0.2136325, 0.2136325, 0.4079128, 0.4890342, 0.5083345, 0.6197319])# Second function
def weighted_percentile(data, weights, perc):
"""
perc : percentile in [0-1]!
"""
data = np.array(data)
weights = np.array(weights)
ix = np.argsort(data)
data = data[ix] # sort data
weights = weights[ix] # sort weights
cdf = (np.cumsum(weights) - 0.5 * weights) / np.sum(weights) # 'like' a CDF function
return np.interp(perc, cdf, data)
weighted_percentile([0.4890342, 0.4079128, 0.5083345, 0.2136325, 0.6197319], [1,1,1,1,1], np.arange(0, 1 + 1 / 5, 1 / 5))
>> array([0.2136325 , 0.31077265, 0.4484735 , 0.49868435, 0.5640332 ,
0.6197319 ])两个人都和R不一样有什么想法吗?
回答 1
Stack Overflow用户
发布于 2022-07-12 23:22:21
我是Python文盲,但据我所见,经过一些快速检查后,我可以告诉你以下几点。
这里使用统一(抽样)权重,因此也可以直接使用quantile()函数。毫不奇怪,它给出的结果与具有相同权重的wtd.quantile()相同:
x <- c(0.4890342, 0.4079128, 0.5083345, 0.2136325, 0.6197319)
n <- length(x)
x <- sort(x)
quantile(x, probs = seq(0,1,0.2))
# 0% 20% 40% 60% 80% 100%
# 0.2136325 0.3690567 0.4565856 0.4967543 0.5306140 0.6197319R quantile()函数以“教科书”的方式得到分位数,即通过确定指数I与i= q(n+1)一起使用。就你而言:
seq(0,1,0.2)*(n+1)
# 0.0 1.2 2.4 3.6 4.8 6.0当然,由于您有5个值/obs,并且您想要的是五分位数,所以索引不是整数。但是,您知道,例如,第一个五分之一(i = 1.2)位于OB-1和OB-2之间。更准确地说,它是两个观测值的线性组合(“权重”是从指数的值中得出的):
0.2*x[1] + 0.8*x[2]
# 0.3690567您也可以根据索引对所有的五分位数进行相同的操作:
q <-
c(min(x), ## 0: actually, the first obs
0.2*x[1] + 0.8*x[2], ## 1.2: quintile lies between obs 1 and 2
0.4*x[2] + 0.6*x[3], ## 2.4: quintile lies between obs 2 and 3
0.6*x[3] + 0.4*x[4], ## 3.6: quintile lies between obs 3 and 4
0.8*x[4] + 0.2*x[5], ## 4.8: quintile lies between obs 4 and 5
max(x) ## 6: actually, the last obs
)
q
# 0.2136325 0.3690567 0.4565856 0.4967543 0.5306140 0.6197319您可以看到,您得到的正是quantile()和wtd.quantile()的输出。
如果我们不考虑0.2*x[1] + 0.8*x[2],而是考虑以下几点:
0.5*x[1] + 0.5*x[2]
# 0.3107726我们得到第二个Python函数的输出。似乎你的第二个函数在结合这两个观测时考虑了均匀的“权重”(很明显,这里我不是在讨论抽样权重)。这个问题(至少对于第二个Python函数来说是这样)。我知道这些只是洞察力,但我希望它们能有所帮助。
编辑:请注意,这两者之间的差异是不必要的,这是python代码的一个“问题”。有不同的分位数估计器(及其加权版本),python函数可以依赖与Hmisc::wtd.quantile()不同的估计器。我认为后者使用了Harrell-Davis分位数估计量的加权版本。如果您真的想实现这个,您应该检查Hmisc::wtd.quantile()的源代码,并尝试将其“直接”转换为Python。
https://stackoverflow.com/questions/72957948
复制相似问题

