用R将对数似然写成函数(θ是什么?)
用R将对数似然写成函数(θ是什么?)
提问于 2022-05-31 15:09:20
我从我的模型中得到了下面的日志可能性,我正试图将它写成R中的函数。
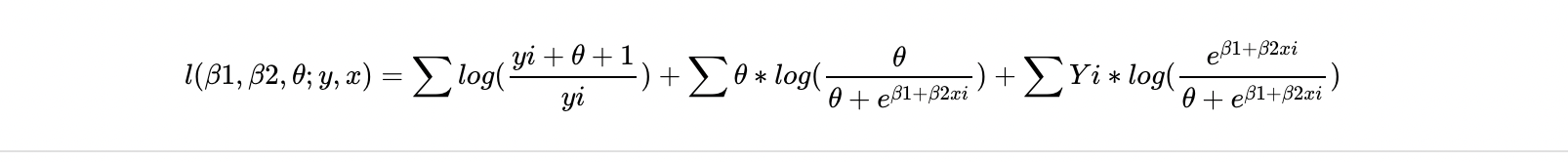
我的问题是我不知道如何用函数来写θ。我在这方面做了几次尝试,如下所示,任何关于这些建议是否接近正确的建议都是值得赞赏的。
函数与θ一起编写为θ
#my likelihood function
mylikelihood = function(beta) {
#log-likelihood
result = sum(log(dengue$cases + theta + 1 / dengue$cases)) +
sum(theta*log(theta / theta + exp(beta[1]+beta[2]*dengue$time))) +
sum(theta * log(exp(beta[1]+beta[2]*dengue$time / dengue$cases + exp(beta[1]+beta[2]*dengue$time))))
#return negative log-likelihood
return(-result)
}我下一次尝试用我的数据集中的Xi替换thetas,这里是(登革热$time)
#my likelihood function attempt 2
mylikelihood = function(beta) {
#log-likelihood
result = sum((log(dengue$Cases + dengue$Time + 1 / dengue$Cases))) +
sum(dengue$Time*log(dengue$time / dengue$Time + exp(beta[1]+beta[2]*dengue$Time))) +
sum(dengue$Cases * log(exp(beta[1]+beta[2]*dengue$Time / dengue$Cases +
exp(beta[1]+beta[2]*dengue$Time))))
#return negative log-likelihood
return(-result)
}数据
head(dengue)
Cases Week Time
1 148 36 1
2 275 37 2
3 205 38 3
4 133 39 4
5 123 40 5
6 138 41 6这些都接近正确吗?如果不是的话,我的错在哪里?
更新为日志可能来自何处;
模型;
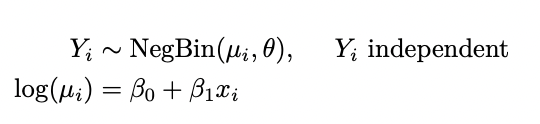
具有均值和色散参数的负二项分布(θ)具有pmf;
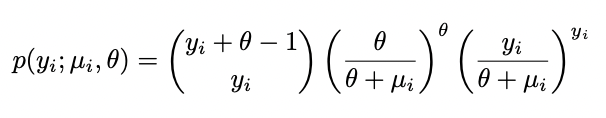
回答 1
Stack Overflow用户
回答已采纳
发布于 2022-05-31 17:40:46
基本问题是,您必须将beta (问题的一个组件的截距和斜率)和theta作为单个参数向量的一部分传递。我修正了括号位置的其他问题,并对表达式进行了一些重新组织。
代码中还有几个更重要的错误。
- 第一个项是而不是分数,它是二项式系数。(即,您应该使用
lchoose(),如下所示) - 您在第一个术语中将a +1更改为a-1。
nll <- function(pars) {
beta <- pars[1:2]
theta <- pars[3]
##log-likelihood
yi <- dengue$Cases
xi <- dengue$Time
ri <- exp(beta[1]+beta[2]*xi)
result <- sum(lchoose(yi + theta - 1,yi)) +
sum(theta*log(theta / (theta + ri))) +
sum(yi * log(ri/(theta+ri)))
##return negative log-likelihood
return(-result)
} 读取数据
dengue <- read.table(row.names = 1, header = TRUE, text = "
Cases Week Time
1 148 36 1
2 275 37 2
3 205 38 3
4 133 39 4
5 123 40 5
6 138 41 6
") 拟合
猜测(1,1,1)的起始参数有点危险--了解参数的含义并猜测生物上合理的值可能更有意义--但这似乎是可以的。
nll(c(1,1,1))
optim(par = c(1,1,1), nll) 由于我们没有限制θ是正的,所以我们会收到一些关于取负数日志的警告,但是这些可能是无害的(例如,参见here)。
替代方案
R有很多内置的机器来安装负二项式模型(我应该知道你在做什么!)
MASS::glm.nb自动为您设置一切,您只需指定预测变量(它使用对数链接并添加一个截距,因此指定~Time将使平均值等于exp(beta0 + beta1*Time))。
library(MASS)
glm.nb(Cases ~ Time, data = dengue)bbmle的自动化程度稍低,但更灵活(在这里,我在日志标度上安装了theta,以避免尝试任何负值)
library(bbmle)
mle2(Cases ~ dnbinom(mu = exp(logmu), size = exp(logtheta)),
parameters = list(logmu ~ Time),
data = dengue,
start = list(logmu = 0, logtheta = 0))所有这三种方法(修正的负对数似然函数+ optim,MASS::glm.nb,bbmle::mle2)都得到了相同的结果.
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/72450237
复制相关文章
相似问题

