抽样点图(R)
抽样点图(R)
提问于 2022-05-17 12:55:54
在我的项目中,在南非海岸的贝蒂湾进行了60个取样点的取样。这些地点处于不同的深度,代表着不同的生境。我对空间数据的编程非常陌生,所以我非常感谢任何帮助。
我试着遵循这个页面中的代码:https://www.r-bloggers.com/2019/10/make-a-map-of-your-study-site-with-tmap
当我想要绘制地图的时候,所有的事情都在进行,然后错误地说:错误:物体海岸线既不是来自sf级,也不是来自恒星、空间、栅格,也不是SpatRaster。
代码中写着land <- st_read(dsn ="LandPoly") i编码了Coastline <- st_read(dsn ="RSAProvinces") Coastline <- st_is_valid(Coastline, NA_on_exception = TRUE, reason = FALSE)。RSA省是我在网上下载的一个shapefile。
我希望的是我的研究区域的地图,它的边界是MPA (我有一个shapefile ),取样点的深度有一个颜色梯度(浅蓝到深蓝色,越深),以及三个不同的栖息地的不同形状。我试着用ggplot和地图“世界”来绘制海岸线,但我的面积太小了,不够详细。
有什么建议吗?
回答 1
Stack Overflow用户
发布于 2022-05-20 11:23:46
使用Biomes数据集,您可以执行以下操作
library(tidyverse)
library(sf)
df <- st_read("RSA_biome.shp")
df %>%
ggplot() +
geom_sf(aes(fill = BIOME), lwd = 0) +
scale_fill_brewer(palette = "Set3")你会收到
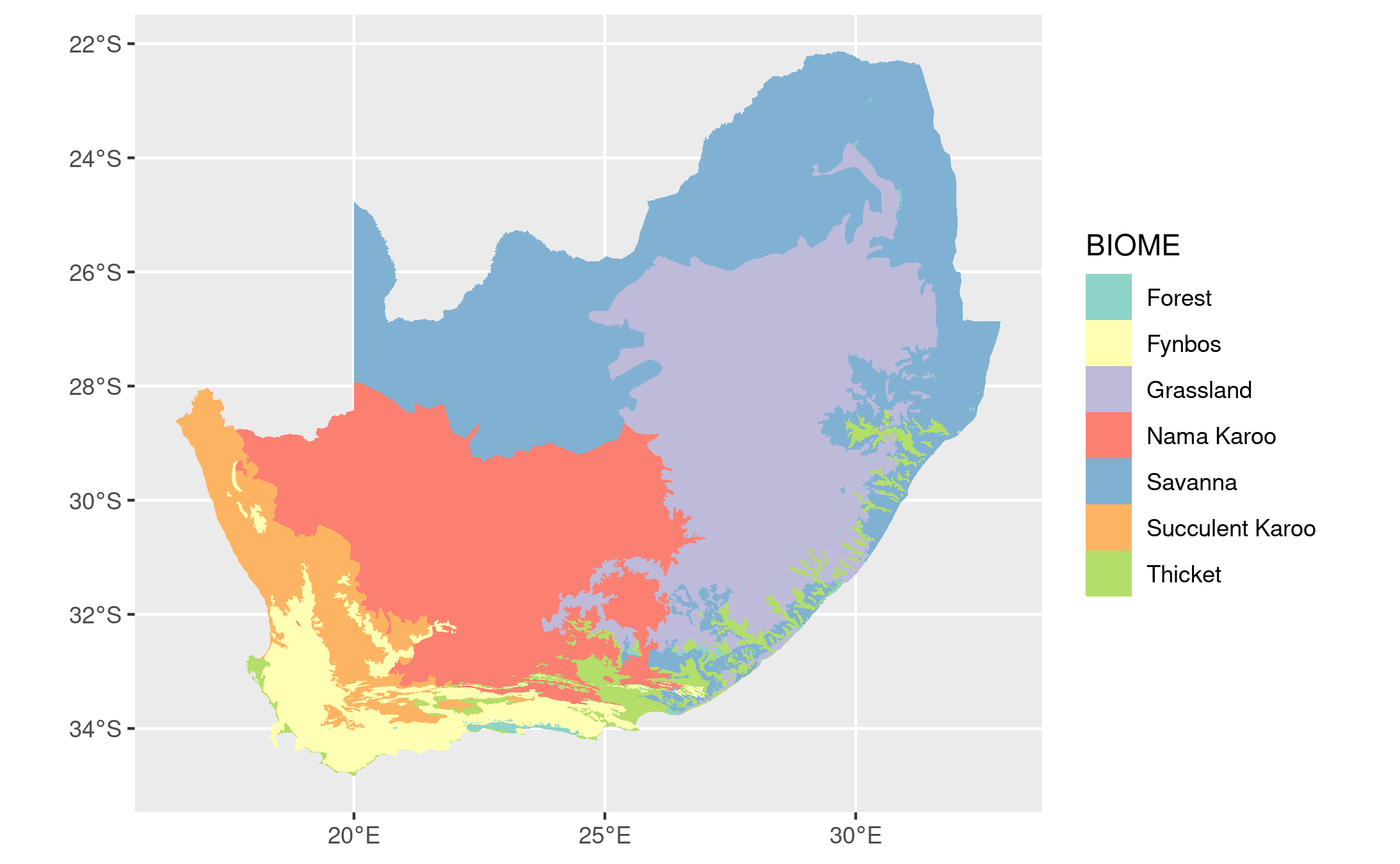
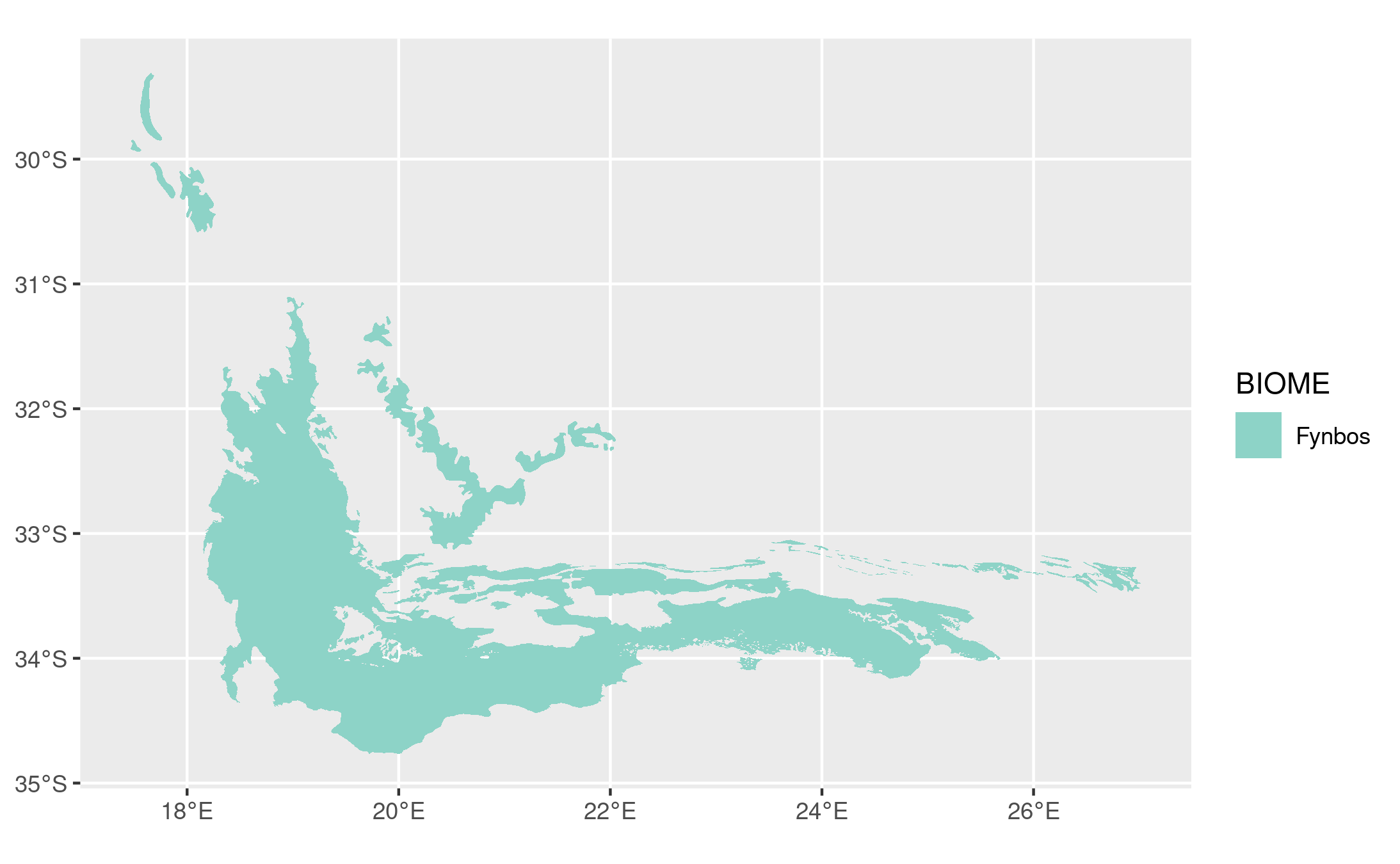
当然,你也可以过滤一个特定的区域,如在生物群落列中定义的,然后再绘图。
df %>%
filter(BIOME == "Fynbos") %>%
ggplot() +
geom_sf(aes(fill = BIOME), lwd = 0) +
scale_fill_brewer(palette = "Set3")
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/72274466
复制相关文章
相似问题

