系统适配3 3SLS测试过识别限制
系统适配3 3SLS测试过识别限制
提问于 2022-03-29 01:38:29
目前,我很难找到一种很好的方法来执行Hansen/Sargan测试,在三阶段最小二乘模型(3 3SLS)中,在面板数据中使用R.I在不同的网络中进行一整天的挖掘,并且无法找到一种方法来描述R中的测试,使用众所周知的systemfit包。
目前,我的代码很简单。
violence_c_3sls <- Crime ~ ln_GDP +I(ln_GDP^2) + ln_Gini
income_c_3sls <-ln_GDP ~ Crime + ln_Gini
gini_c_3sls <- ln_Gini ~ ln_GDP + I(ln_GDP^2) + Crime
inst <- ~ Educ_Gvmnt_Exp + I(Educ_Gvmnt_Exp^2)+ Health_Exp + Pov_Head_Count_1.9
system_c_3sls <- list(violence_c_3sls, income_c_3sls, gini_c_3sls)
fitsur_c_3sls <-systemfit(system_c_3sls, "3SLS",inst=inst, data=df_new, methodResidCov = "noDfCor" )
summary(fitsur_c_3sls)但是,添加更多的工具来创建一个标识过高的系统并不能在Hansen/Sargan测试的输出中产生结果,因此我假设测试应该在输出之外执行,并且可能与systemfit类对象相关联。
提前谢谢。
回答 1
Stack Overflow用户
发布于 2022-11-29 19:11:46
利用g方程、l外生变量和k回归方程,对3 3SLS进行了Sargan检验。
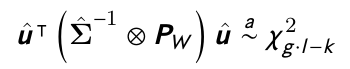
其中u是叠加残差,\Sigma是估计的剩余协方差,P_W是外生变量上的投影矩阵。参见戴维森& MacKinnon ETM的CH12.4。
从systemfit中计算Sargan测试应该如下所示:
sargan.systemfit=function(results3sls){
result <- list()
u=as.matrix(resid(results3sls)) #model residuals, n x n_eq
n_eq=length(results3sls$eq) # number of equations
n=nrow(u) #number of observations
n_reg=length(coef(results3sls)) # total number of regressors
w=model.matrix(results3sls,which='z') #Matrix of instruments, in block diagonal form with one block per equation
#Need to aggregate into a single block (in case different instruments used per equation)
w_list=lapply(X = 1:n_eq,FUN = function(eq_i){
this_eq_label=results3sls$eq[[eq_i]]$eqnLabel
this_w=w[str_detect(rownames(w),this_eq_label),str_detect(colnames(w),this_eq_label)]
colnames(this_w)=str_remove(colnames(this_w),paste0(this_eq_label,'_'))
return(this_w)
})
w=do.call(cbind,w_list)
w=w[,!duplicated(colnames(w))]
n_inst=ncol(w) #w is n x n_inst, where n_inst is the number of unique instruments/exogenous variables
#estimate residual variance (or use residCov, should be asymptotically equivalent)
var_u=crossprod(u)/n #var_u=results3sls$residCov
P_w=w%*%solve(crossprod(w))%*%t(w) #Projection matrix on instruments w
#as.numeric(u) vectorizes the residuals into a n_eq*n x 1 vector.
result$statistic <- as.numeric(t(as.numeric(u))%*%kronecker(solve(var_u),P_w)%*%as.numeric(u))
result$df <- n_inst*n_eq-n_reg
result$p.value <- 1 - pchisq(result$statistic, result$df)
result$method = paste("Sargan over-identifying restrictions test")
return(result)
}页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/71655500
复制相关文章
相似问题

