Plink -反向补码
Plink -反向补码
提问于 2021-12-20 04:49:40
我是第一次使用Plink,并且正在检查我的数据与一些以前的基因型样本(这些是相同的样本,所以基因型应该匹配)。
我的数据几乎是正确的,就像它正确地调用了homs和hets一样,但是对于一些SNP,我的数据有相反的补充。例如:
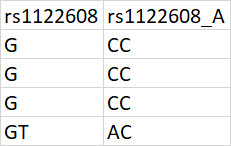
在plink中我需要什么命令,我需要告诉它在需要时调用反向补语吗?
回答 1
Stack Overflow用户
发布于 2021-12-22 23:30:48
我想我已经找到了问题的根源,如果其他人在同一问题上偶然发现这篇文章。
我用的是Illumina SNP芯片。显然,在基因序列定义的基因型数据后处理上存在一定的差异。这两个链接很好地解释了它:http://gengen.openbioinformatics.org/en/latest/tutorial/coding/ https://academic.oup.com/bioinformatics/article/33/15/2399/3204987
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/70417482
复制相关文章
相似问题

