Python的PCA :特征向量不是正交的
Python的PCA :特征向量不是正交的
提问于 2021-12-18 12:39:38
我正在用Python进行主成分分析(PCA)。出于理解力的考虑,我想自己实施它。为此,我根据给定的协方差矩阵创建随机数据,以便处理不同的值和主成分的行为。所以这个脚本只是为了理解和澄清PCA。
我的理解是,主成分(即协方差矩阵的特征向量)总是相互正交的。这也是维基百科的图片:
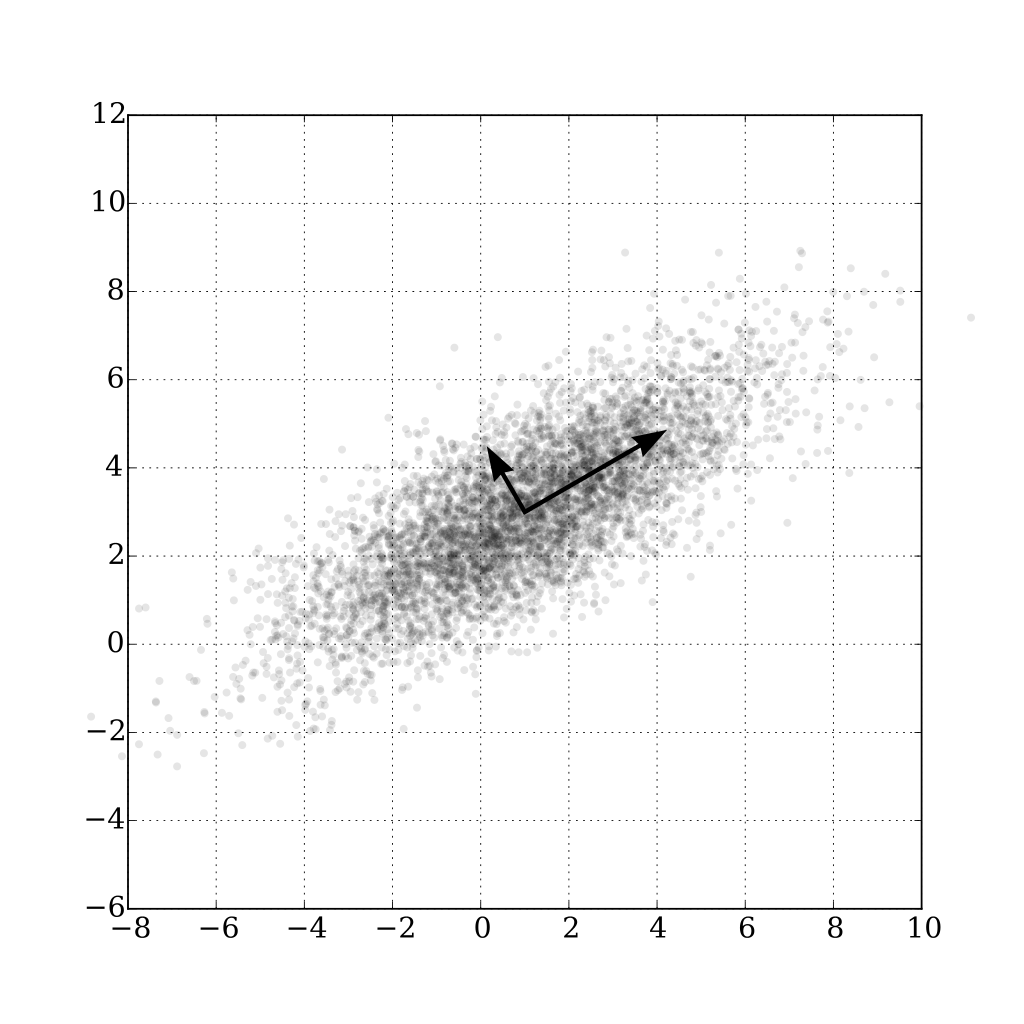
维基百科图片的描述(来源):
多元高斯分布的主成分分析以(1,3)为中心,在( 0.878,0.478 )方向的标准偏差为3,在正交方向上的标准差为1。所示的向量是由相应特征值的平方根标度的(对称的,正半定的)协方差矩阵的单位特征向量。就像在一维情况下一样,平方根被取下来,因为标准差比方差更容易可视化。
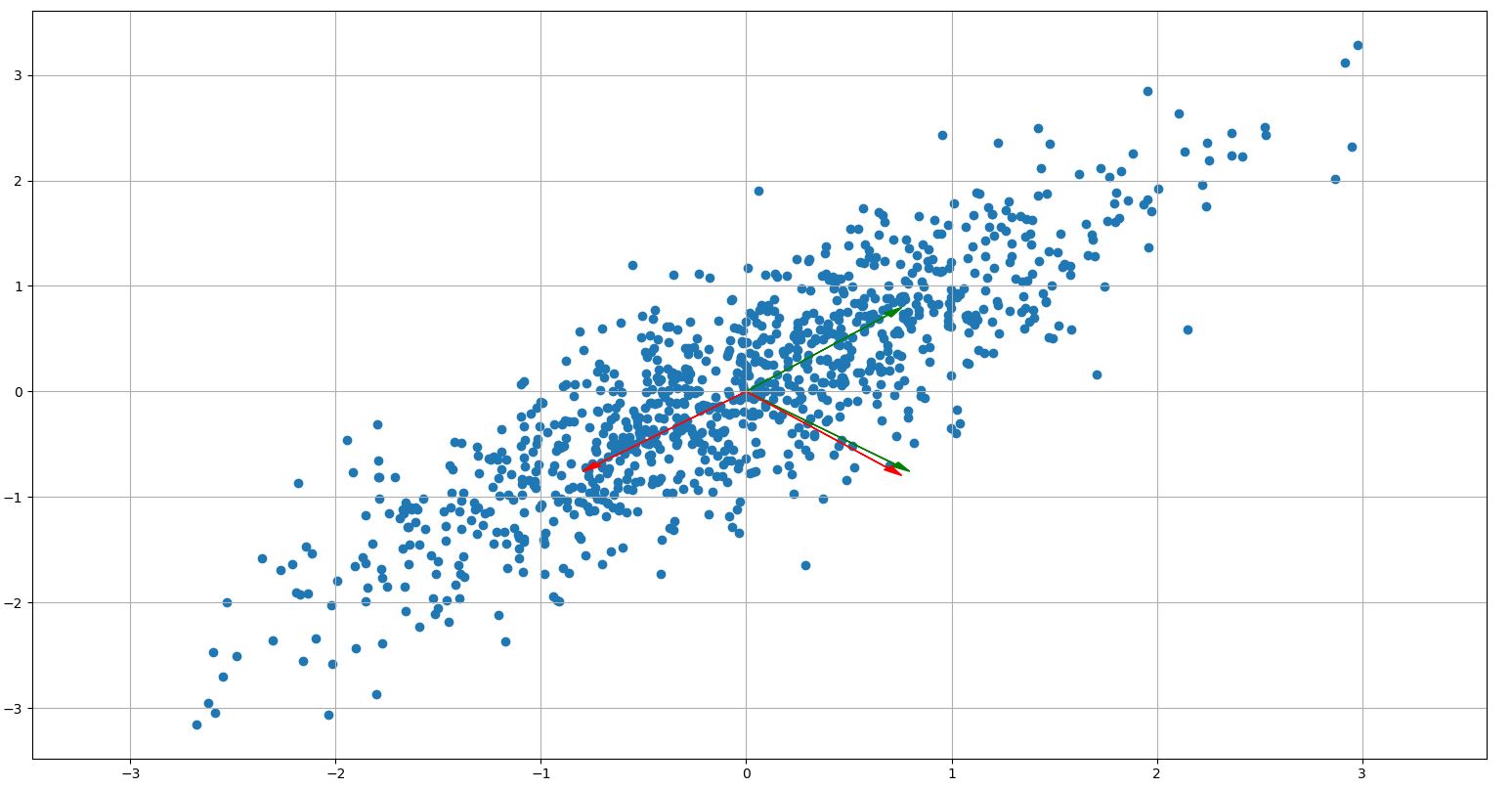
所以我认为,对于我的情况,如果我画出我从随机数据中得到的特征向量,也是正交的。但事实并非如此。他们的方向总是大致不同的。60度,而不是我所期望的90度。如果我使用sklearn库中的PCA,也会发生这种情况。请看下面的图片,红色是学习PCA的特征向量,绿色是我自己代码中的特征向量。
我的Python脚本:
from matplotlib import pyplot as plt
import numpy as np
from sklearn.decomposition import PCA
def normalize(data: np.array, mean=None, std=None):
"""
Normalize a pandas dataframe with respect to their stochastical moment. If mean and/or std is not passed they are
calculated beforeheand.
:param data: Data to be normalized
:param mean: A mean value (optional)
:param std: A standard deviation (optional)
:return: normalized dataframe, mean value(s), standard deviation(s)
"""
if mean is None:
mean = data.mean(axis=0).reshape(1, -1)
if std is None:
std = data.std(axis=0).reshape(1, -1)
res = data - mean / std
return res, mean, std
# Press the green button in the gutter to run the script.
if __name__ == '__main__':
datacount = 1000
# create data based on given covariance matrix
cov = np.array([[1, 0.85], [0.85, 1]])
rand1 = np.random.multivariate_normal([1, 3], cov, datacount)
# normalize, calculate covariance matrix and its eigenvectors and eigenvalues
rand1, mean, std = normalize(rand1)
cov = np.cov(rand1.T)
eig_values, eig_vectors = np.linalg.eig(cov)
# sort eig_values by importance and use this to also sort the vectors
idx = np.argsort(eig_values, axis=0)[::-1]
sorted_eig_vectors = eig_vectors[:, idx]
# plot data
plt.figure()
plt.scatter(rand1[:, 0], rand1[:, 1])
# set both axis limits to the maximum/minimum of the axis scalesv
ax = plt.gca()
xlimits = np.array(ax.get_xlim())
ylimits = np.array(ax.get_ylim())
axmax = np.max([np.max(xlimits), np.max(ylimits)])
axmin = np.min([np.min(xlimits), np.min(ylimits)])
ax.set_xlim([axmin, axmax])
ax.set_ylim([axmin, axmax])
# use PCA from sklearn for comparison
pca = PCA(n_components=2)
pca = pca.fit(rand1)
# Plot the eigenvectors
# Beware! Eigenvectors are oriented in rows in sklearn PCA and column-oriented in np.linalg.eig()!
for i in range(2):
plt.arrow(0, 0, pca.components_[0, i], pca.components_[1, i], color="g",
head_width=0.05, head_length=0.1)
for i in range(2):
plt.arrow(0, 0, eig_vectors[i, 0], eig_vectors[i, 1], color="r",
head_width=0.05, head_length=0.1)
# plt.annotate(text='', xy=(1, 1), xytext=(0, 0), arrowprops=dict(arrowstyle='<->'))
plt.grid()
plt.figure()
# Transform data to new subspace
eig_scores = np.dot(rand1, sorted_eig_vectors[:, :2]).T
# plot PCAs in subspace
plt.scatter(eig_scores[0], eig_scores[1])
# set both axis limits to the maximum/minimum of the axis scales
ax = plt.gca()
xlimits = np.array(ax.get_xlim())
ylimits = np.array(ax.get_ylim())
axmax = np.max([np.max(xlimits), np.max(ylimits)])
axmin = np.min([np.min(xlimits), np.min(ylimits)])
ax.set_xlim([axmin, axmax])
ax.set_ylim([axmin, axmax])
plt.grid()
plt.show()
# Are Eigenvectors orthogonal?
print(np.dot(eig_vectors[:, 0], eig_vectors[:, 1]) == 0) # yields True
print(np.dot(pca.components_[0, :], pca.components_[1, :]) == 0) # yields True奇怪的是,最后两条线,我检查这两种方法的特征向量是否是正交的,总是得到真,表明向量实际上是正交的。
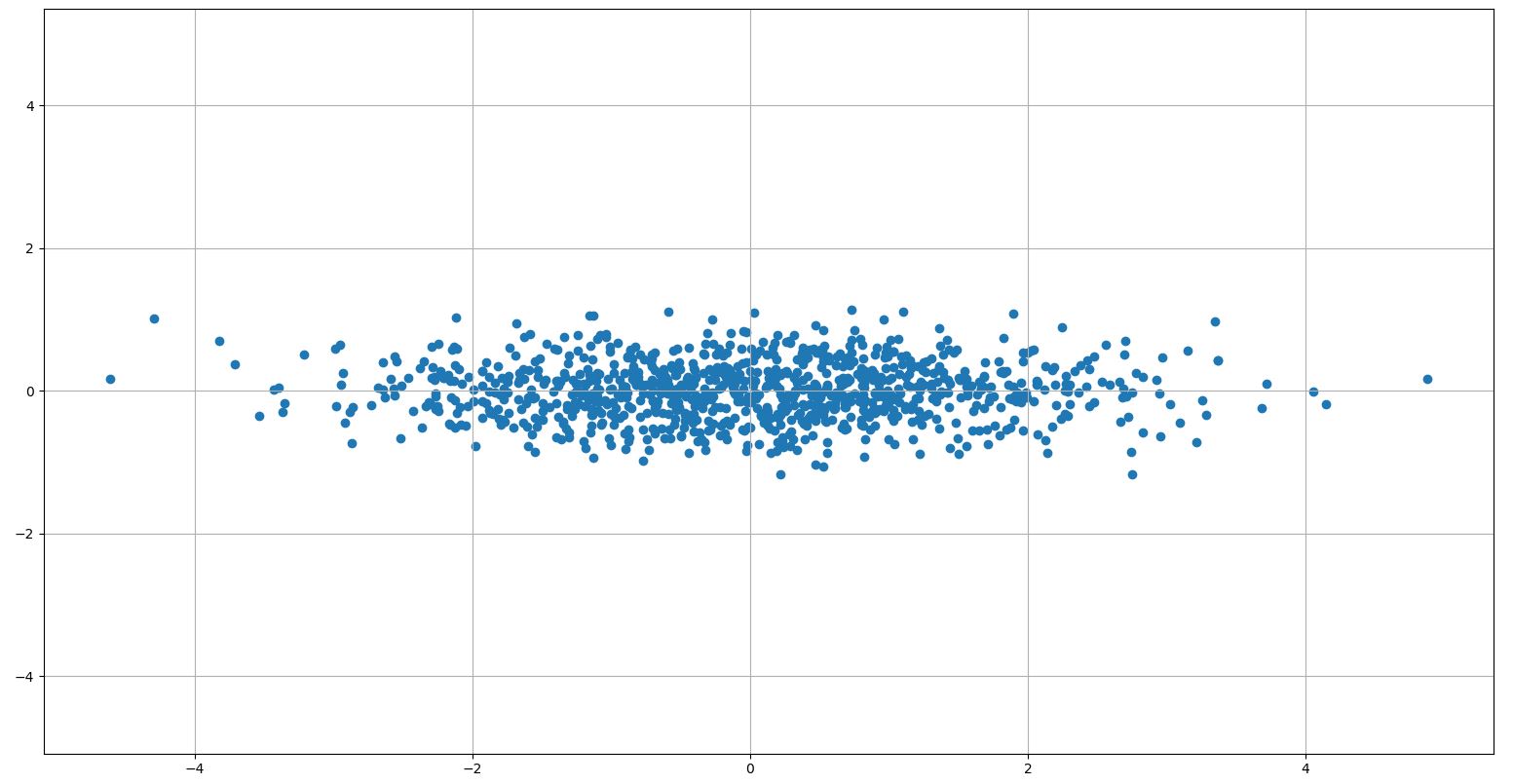
此外,将数据转换为新的子空间也很好,结果如下:
我遗漏了什么?我的期望是假的吗?或者我的Python脚本中有bug?
回答 1
Stack Overflow用户
回答已采纳
发布于 2021-12-18 13:10:43
你检查过它们是正交的,而且它们是正交的,但在情节中,你说它们不是。矢量绘制正确吗?它们是:
array([[ 0.707934 , -0.70627859],
[ 0.70627859, 0.707934 ]])从数字上看似乎是这样的。
问题是,你试图测量你的显示器上的角度,在那里两个轴有不同的比例。
只需添加plt.axis('equal')
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/70403502
复制相关文章
相似问题

