根红苗正的GWAS软件:GEMMA
根红苗正的GWAS软件:GEMMA
邓飞
发布于 2026-03-12 18:09:07
发布于 2026-03-12 18:09:07
大家好,我是邓飞。
跑GWAS项目,几百个样本,几万个位点,rMVP、GAPIT都可以用,如果是几千万个位点,几千个样本,GEMMA运算速率更高,占用内存和运行时间都比较理想,下面介绍一下这个软件。

GEMMA名称来源:
- G:Genome-wide
- E:Efficient
- MM:Mixed-model
- A:Association
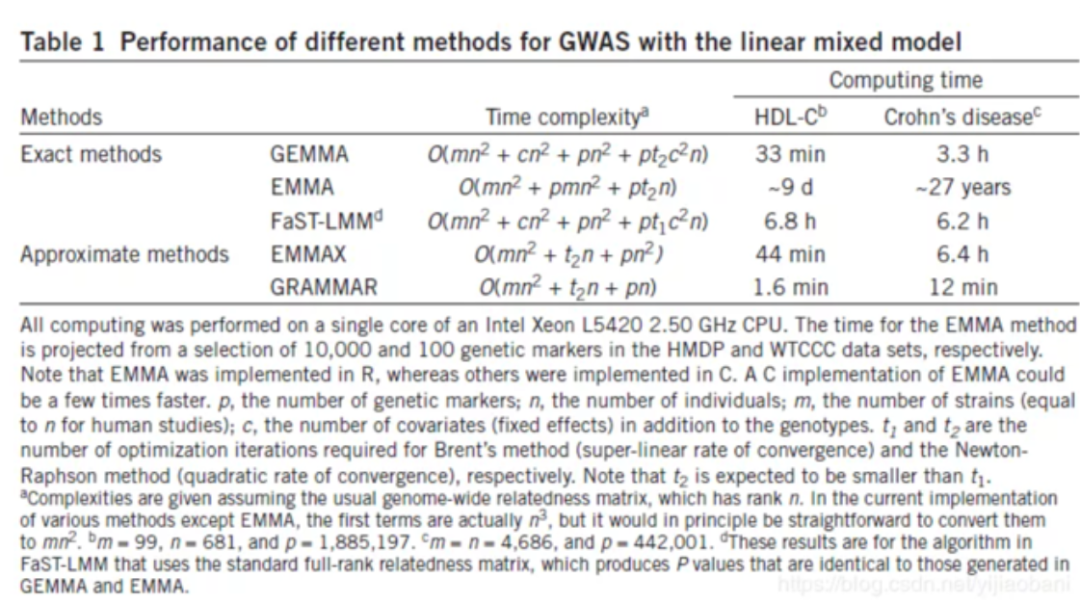
GEMMAX主要特点:快
就是它跑3.3h,其它软件跑27年的那种!!!
GEMMA语法特点
相对于plink的语法,GEMMA语法更简练,一个杠,一个字母。比如:
- 表型数据:-p
- 协变量:-c,而plink的语法的是两个杠接一个单词,比如表型数据:--pheno;协变量:--covar
GEMMA支持plink的二进制文件:
- 读取plink文件:-bfile
GEMMA生成G矩阵:
gemma-0.98.1-linux-static-bfilec-gk 2 -pp.txtGEMMA分析MLM模型:
gemma-0.98.1-linux-static -bfile c -k output/result.sXX.txt -lmm 1 -p p.txt结果查看:
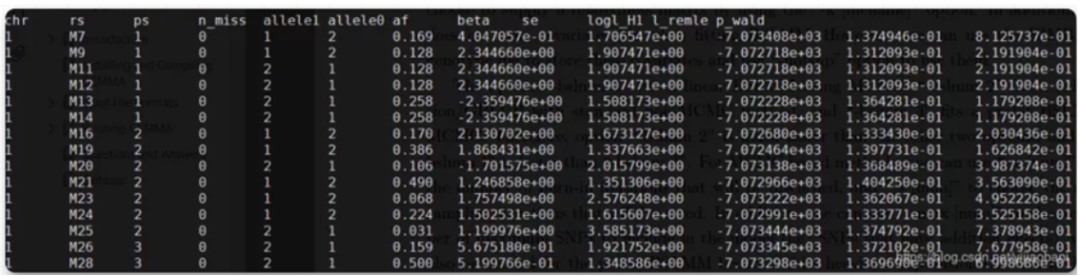
干货来了:
GEMMA软件默认是没有PVE的(snp解释表型变异百分比),根据PVE的公式:

分子分母都有MAF*(1-MAF),可以删除,剩下的公式为:
PVE = 2* beta^2 /( 2*beta^2 + 2*N*se^2)
这里写了一个代码脚本,输入结果文件和样本个数,就可以生成pve的结果和显著性位点。
代码如下:
$ cat ~/bin/add_pve_from_gemma_result_and_tiqu_sig.R
#! /home/dengfei/bin/Rscript
args = commandArgs(T)
if(length(args) == 0){
cat("\n\n\tRscript add_pve_from_gemma_result_and_tiqu_sig.R result.assoc.txt N,geaam的gwas结果, N为分析的样本数\n
结果生成文件:添加pve的文件:result.assoc_add_pve.txt,还有显著性文件:result_signals.csv\n")
quit("no")
}
library(data.table)
library(tidyverse)
N = as.numeric(args[2])
# d1 = fread("output/result.assoc.txt")
dd = fread(args[1])
head(dd)
dd$pve = 2*dd$beta^2/(2*dd$beta^2+dd$se^2 * 2 * (N-dd$n_miss))
head(dd)
fwrite(dd,"result.assoc_add_pve.txt",sep=" ",quote=F)
# 导出显著性的SNP位点
dat1 = dd %>% dplyr::select(SNP = rs, CHROM = chr, POS = ps,REF=allele1, ALT=allele0, maf = af,Effect = beta, SE=se, pvalue = p_wald,pve) %>% drop_na(pvalue)
head(dat1)
p_th = 1/nrow(dat1)
dat2 = dat1 %>% filter(pvalue <p_th)
fwrite(dat2,"result_signals.csv")
代码调用说明:
$ add_pve_from_gemma_result_and_tiqu_sig.R
Rscript add_pve_from_gemma_result_and_tiqu_sig.R result.assoc.txt N,geaam的gwas结果, N为分析的样本数
结果生成文件:添加pve的文件:result.assoc_add_pve.txt,还有显著性文件:result_signals.csv
代码调用演示:
结果文件:
result.assoc_add_pve.txt
result_signals.csv资源推荐:
1,快来领取 | 飞哥的GWAS分析教程
2,飞哥汇总 | 入门数据分析资源推荐
3,数量遗传学,分享几本书的电子版
4,R语言学习看最新版的电子书不香嘛?
5,书籍及配套代码领取--统计遗传分析导论
6,飞哥的学习圈子
本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2025-12-18,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读

