进化树分析直接上传数据,很快的
进化树分析直接上传数据,很快的
邓飞
发布于 2026-03-12 17:46:43
发布于 2026-03-12 17:46:43
大家好,我是邓飞。
之前计划写群体结构三剑客的博文,写了两篇了:
群体遗传三剑客第一剑:主成分分析PCA
群体遗传三剑客第二篇:Admixture群体结构分析
线上直接上传数据做进化树:
https://asreml.cn/population-genetics/phylogenetic
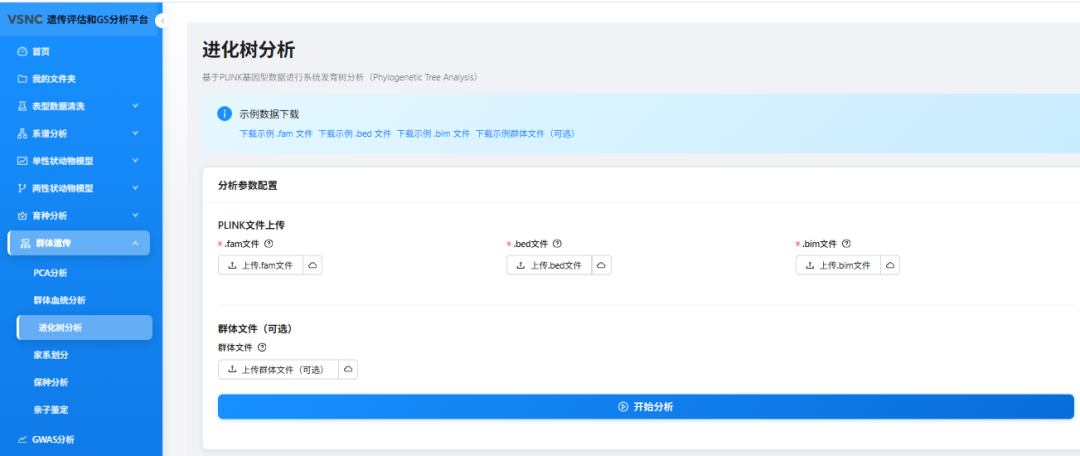
准备数据:plink的二进制文件,如果有分组数据也可以准备。

上传对应格式的数据:
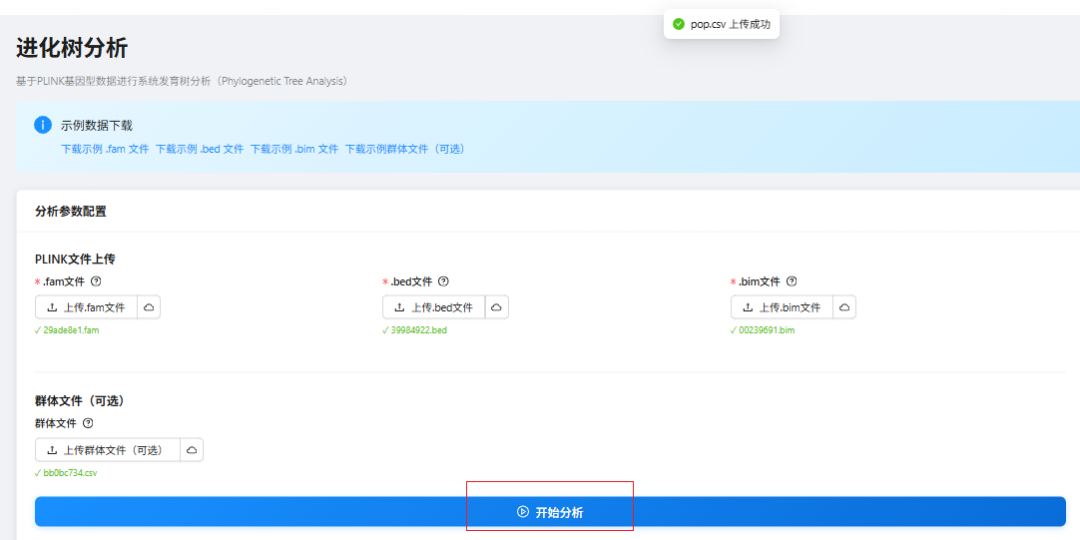
查看结果:
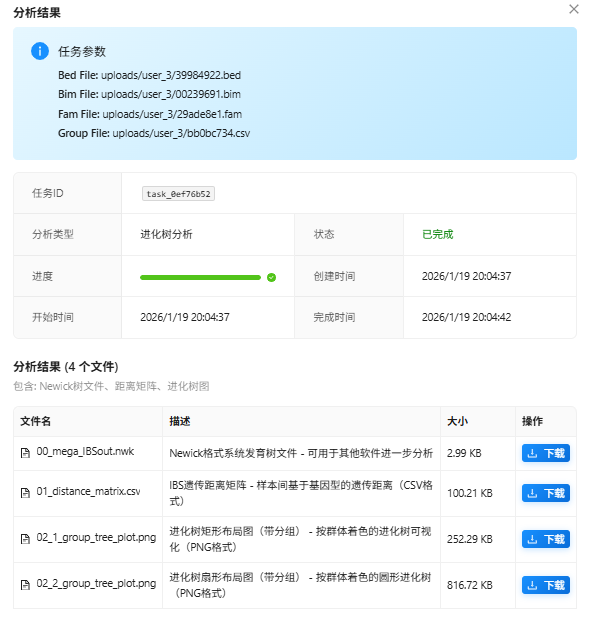
结果中有原始的nwk文件,还有遗传距离文件以及两个图,下载到本地:
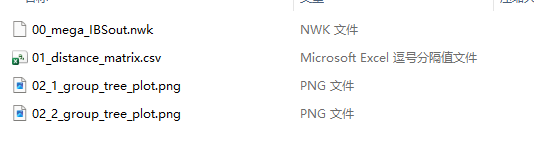
结果:
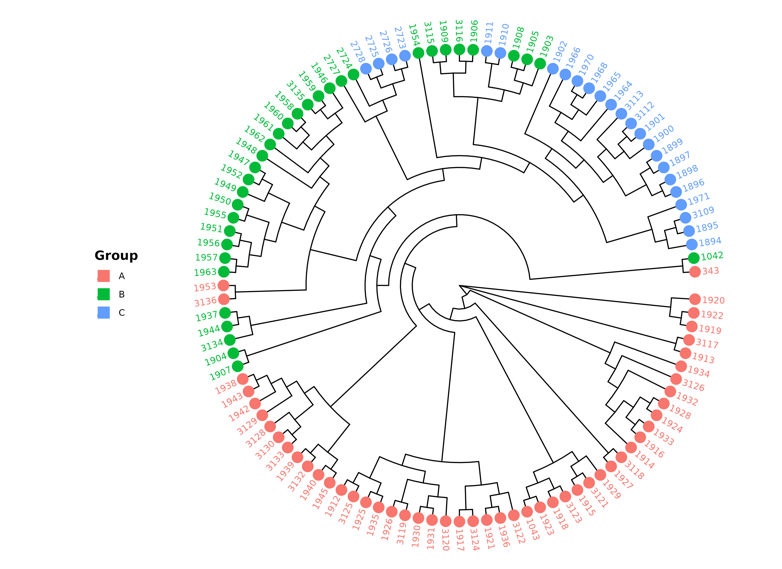
效果很好。
如果想要自己分析,操作方法如下:
软件:MEGA和ggtree。注意,MEGA这里用的是Linux版本的命令行megacc,ggtree是R包,主要用于可视化。
软件介绍:
MEGACC 是 MEGA 的命令行版本,能在无图形界面的环境里进行进化分析,软件地址:https://www.megasoftware.net/
ggtree是Y叔开发的R包,主要用于进化树结果的可视化,软件地址:https://bioconductor.org/packages/release/bioc/html/ggtree.html
plink格式的数据进化树分析步骤:
1,计算亲缘关系距离矩阵
plink --file aa --allow-extra-chr--chr-set60--distance1-ibs square flat-missing --genome--out IBSdis2,整理结果
将id结果和亲缘关系结果分别整理为megacc支持的格式:
id名称格式:
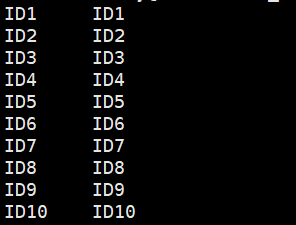
亲缘关系矩阵格式:

3,将上面的两个文件整理为megacc支持的格式
上面是ID信息,下面是半三角的关系矩阵:

4,使用megacc计算进化树,得到nwk文件
megacc -a infer_NJ_distances.mao -d ibs_dismatrix.meg -o mega_IBSout5,使用ggtree绘制进化树
library(ggtree)
tree = read.tree("mega_IBSout.nwk")
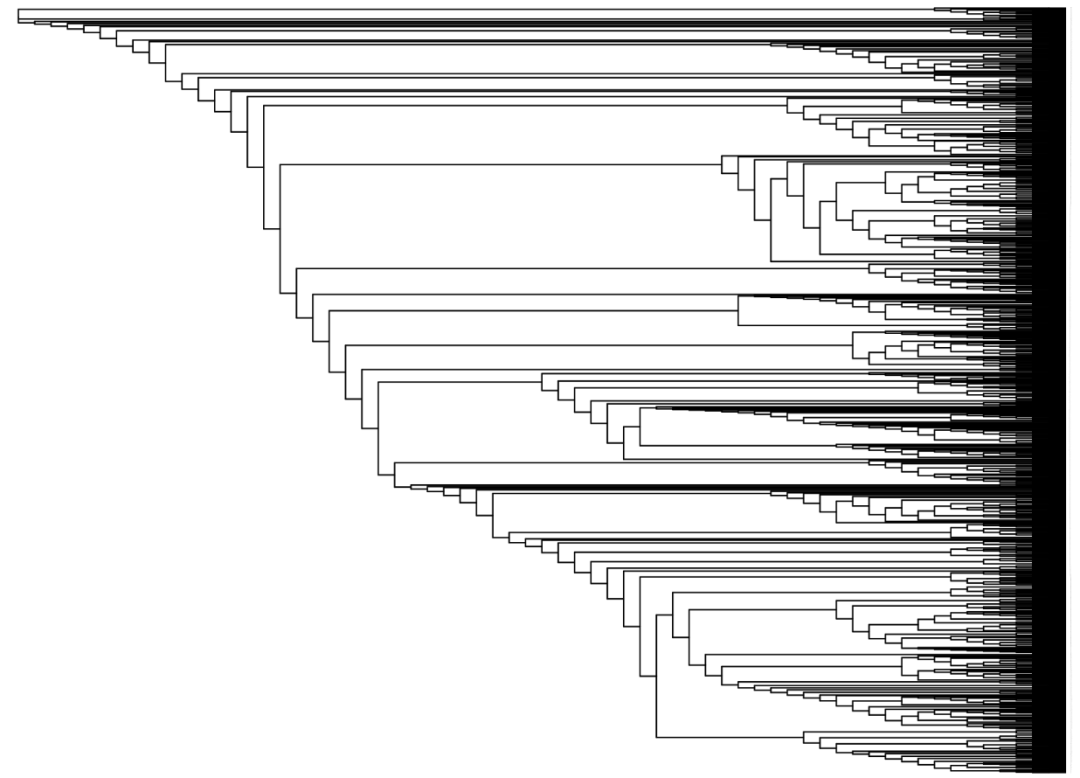
# 正常的图
tiff("tree1_plot.tiff",width = 12, height = 8, units = "in",compression = "lzw",res=300)
ggtree(tree, ladderize = FALSE, branch.length = "none") + geom_tiplab2(size=.1) + theme(legend.position = "right")
dev.off()
# 圆圈图
tiff("tree2_plot.tiff",width = 12, height = 8, units = "in",compression = "lzw",res=300)
ggtree(tree, layout="fan", ladderize = FALSE, branch.length = "none") + geom_tiplab2(size=.3) + theme(legend.position = "right")
dev.off()
结果:

也可以添加分组信息:

两者是一致的。
使用网址:https://asreml.cn
本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2026-01-19,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读
目录

