Proc. Natl. Acad. Sci. | 预训练DNA语言模型实现植物基因组跨物种建模
Proc. Natl. Acad. Sci. | 预训练DNA语言模型实现植物基因组跨物种建模

DrugAI
发布于 2026-01-06 11:00:01
发布于 2026-01-06 11:00:01
DRUGONE
在多样且复杂的植物基因组中解析功能与适应性效应的能力,亟需具有可迁移性的模型。研究人员提出PlantCaduceus,这是一种植物DNA语言模型,通过同时建模双链DNA,在16种被子植物基因组上进行预训练,能够学习进化保守性序列模式。在仅使用少量拟南芥标注数据进行微调后,PlantCaduceus便可准确预测翻译起始/终止位点及剪接供体/受体位点,并展现出跨物种迁移能力,成功泛化至与拟南芥分化约1.6亿年的玉米。该模型在玉米剪接供体预测任务中比现有最佳模型性能提升1.45倍,在翻译起始位点预测中提升达7.23倍。其预测有害突变的表现也可与最先进的蛋白质语言模型媲美。PlantCaduceus预测为有害的突变,其群体中次等等位基因频率比基于多序列比对的方法低三倍。此外,该模型还能准确识别拟南芥和玉米中的致病变异。PlantCaduceus是一个通用的DNA语言模型,有望加速植物基因组学研究及育种实践。

过去20年中已有超过1000个植物基因组发表,预计未来将有大幅增长。要推进植物基因组学与育种,亟需在转录与翻译层面全面理解基因组中的功能元件与适应性影响。然而,植物基因组在大小、组成和结构上具有显著差异,甚至在近缘物种中亦如此。尽管模型植物如拟南芥、水稻和玉米已建立丰富的基因组资源,但要对所有植物构建类似资源代价极高,不具现实性,因此亟需具备跨物种泛化能力的建模工具,挖掘保守序列特征。
传统监督深度学习模型在理解DNA序列功能方面取得进展,但其依赖大规模标注数据,这在植物基因组学中往往难以获取。此外,模型物种上训练的模型难以迁移至其他物种。相比之下,语言模型可通过无监督预训练学习序列结构并实现迁移能力。蛋白质语言模型已经在结构预测、变异效应识别等方面取得成功。相比仅作用于编码区的蛋白质模型,DNA语言模型可覆盖全基因组信息,尤其是非编码区的变异对植物性状与人类疾病影响也逐渐受到重视。
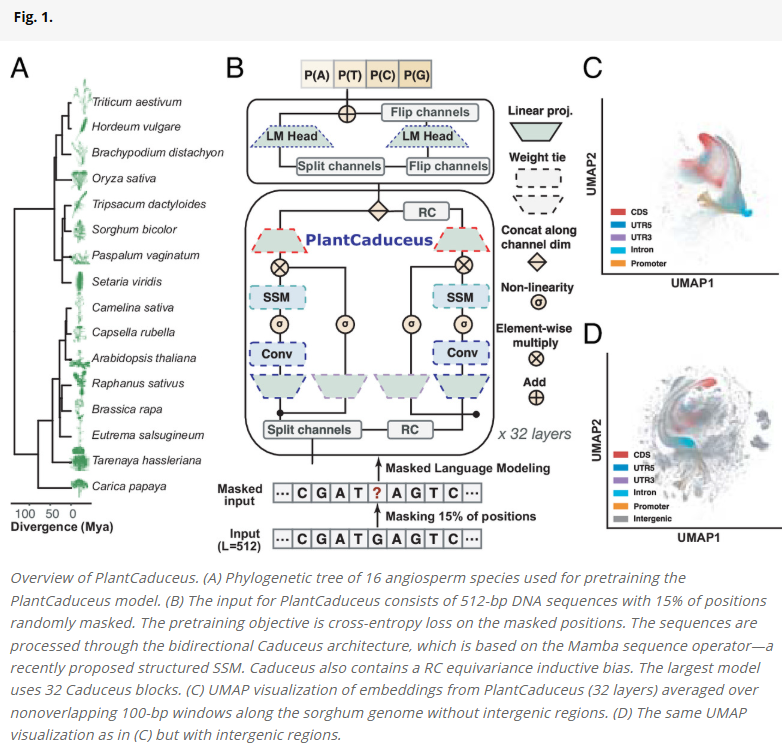
不过DNA语言建模面临挑战:如重复序列丰富、非编码区保守性低、需考虑双链结构与互补序列方向等。为此,研究人员提出PlantCaduceus模型,在16个被子植物基因组上进行训练,采用支持双向建模与互补对称性的Caduceus架构,并对非编码区与重复序列进行采样策略控制,从而提升建模精度。
结果
PlantCaduceus:一个基于16个被子植物基因组的预训练DNA语言模型
研究人员构建了PlantCaduceus模型,使用Caduceus架构,在16个进化距离广泛的植物基因组上预训练,涵盖1.6亿年演化跨度。模型输入为512 bp窗口,使用掩码语言建模任务进行训练。针对重复序列与基因组大小差异问题,通过对非重复区域进行加权与采样,避免模型过拟合简单重复序列,聚焦于功能相关的编码区和非重复区。研究人员训练了多种深度的模型(20至32层),参数数量从2000万到2.25亿不等。通过可视化嵌入空间,发现即使未进行监督训练,模型也能清晰区分编码与非编码区域。
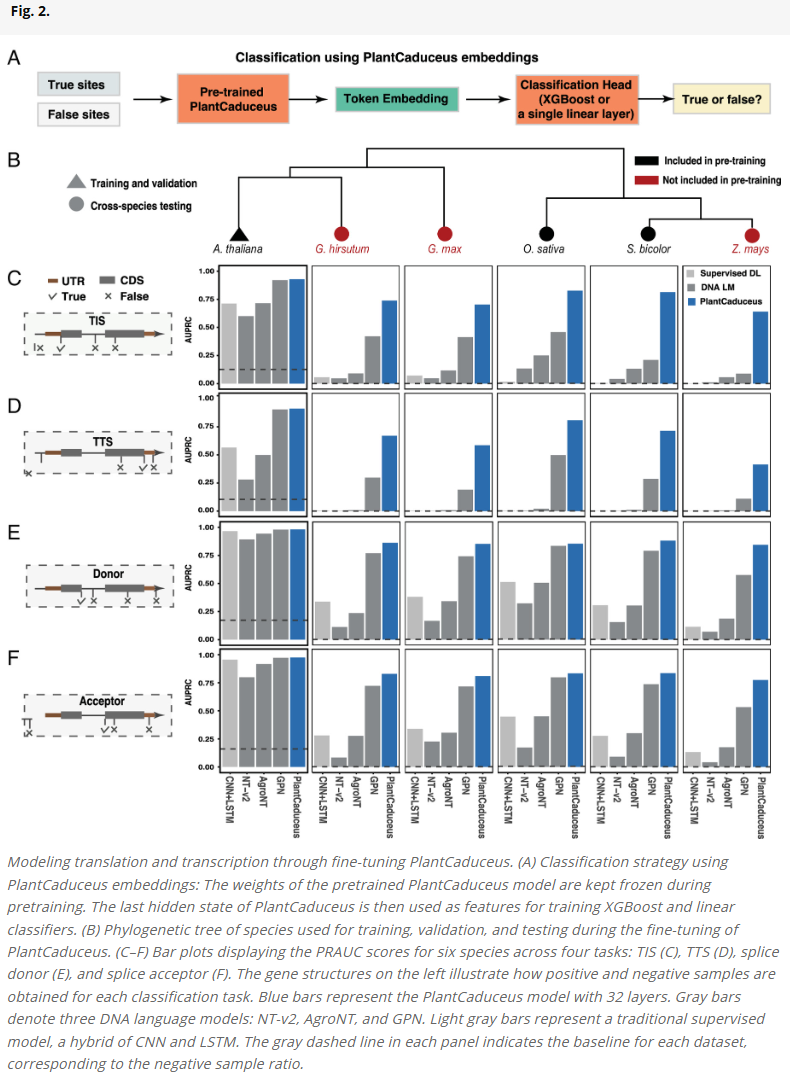
提高转录与翻译相关位点的预测精度与跨物种迁移能力
研究人员设计了四个基因注释任务(翻译起始位点、翻译终止位点、剪接供体与受体位点)来评估模型在转录与翻译建模中的表现。在拟南芥上训练后,模型在包括水稻、高粱、大豆、棉花和玉米等其他物种中保持出色性能,优于GPN、AgroNT等模型,且显著优于传统监督模型CNN+LSTM。在跨物种迁移中,PlantCaduceus的表现最为稳定(平均AUPRC为0.764),即使目标物种未参与预训练也不受影响,展示出极强的泛化能力。
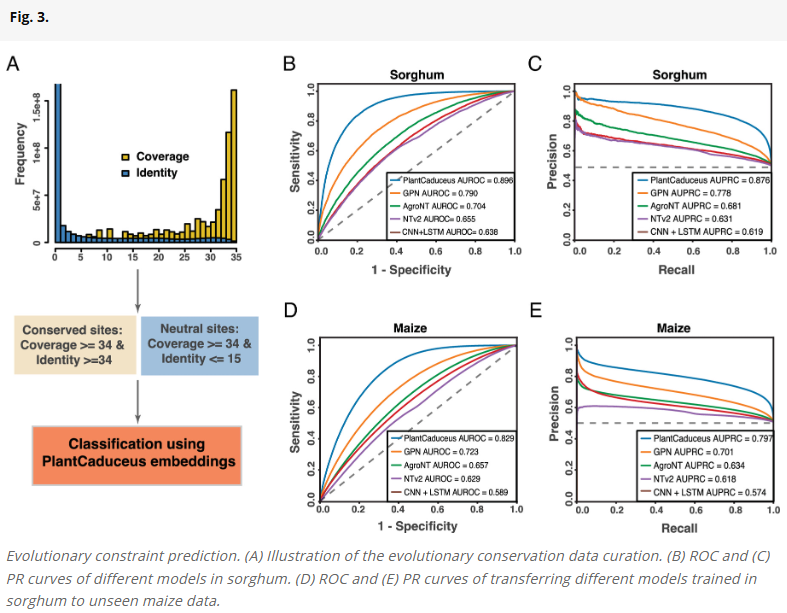
进化保守性预测任务中的跨物种能力
研究人员在高粱中利用多物种比对数据标注进化保守位点,并训练模型进行保守性预测。即便在未进行监督训练的零样本情境下,PlantCaduceus也可通过参考等位基因的预测概率反映序列保守性。进一步通过XGBoost对提取的嵌入特征进行微调,PlantCaduceus在保守性预测中优于GPN、AgroNT等模型,并且在非编码区域表现尤为出色。此外,将在高粱中训练的模型迁移至玉米数据上,也获得了优异的跨物种预测结果。
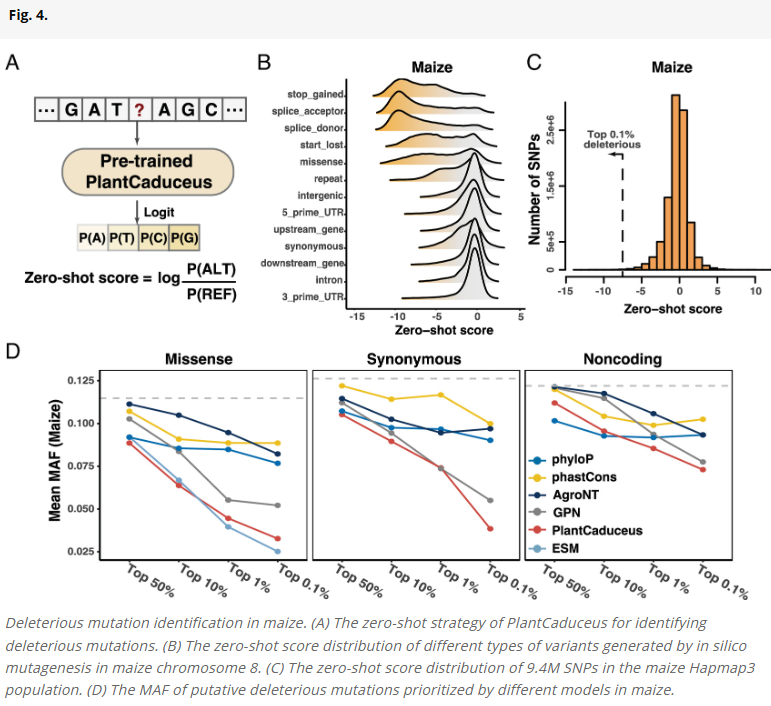
零样本变异效应预测识别多个物种中的有害突变
PlantCaduceus通过预测参考与替代等位基因之间的对数似然差值,计算“零样本分数”,用于衡量突变的保守性。在玉米与高粱中,研究人员观察到在剪接、终止密码子等功能关键区域的突变拥有更负的分数,指示其潜在危害性。在真实人群群体中,这些被预测为有害的突变也表现出更低的等位基因频率,优于phyloP、phastCons等传统方法以及其他语言模型。此外,PlantCaduceus还能准确识别拟南芥中的已知因表型突变的致病位点以及玉米中“甜玉米”基因座Su1处的致因突变。
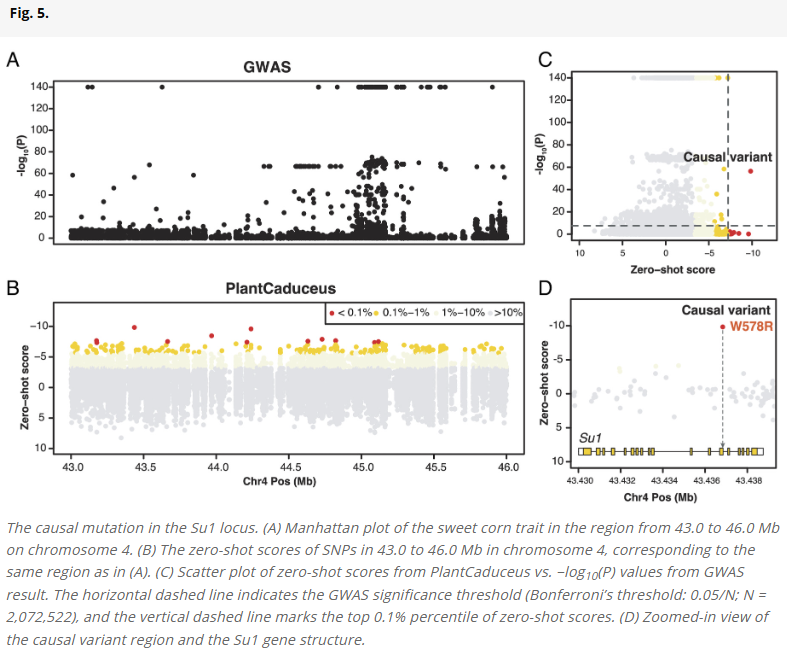
讨论
PlantCaduceus通过在16种进化距离广泛的植物基因组上进行预训练,学习了DNA序列的语言规律与保守性特征,展现出强大的跨物种预测能力。在基因注释、变异效应评估及保守性建模任务中均取得了超越现有模型的性能。相较于需要大量标注数据的监督模型,PlantCaduceus更具实用性,特别是在非模式物种研究中。
研究人员进一步发现,训练数据中物种的系统发育多样性对模型泛化能力起着关键作用。与使用48个植物物种预训练的AgroNT相比,PlantCaduceus采用了更合理的token化策略、排除了低保守性区域,并保持了更高的计算效率,从而在单点预测任务中表现更优。
PlantCaduceus在无需多序列比对的前提下,也可高效识别有害突变,捕捉调控元件,具有显著实用价值。未来,研究人员计划将预训练范围扩展至裸子植物,延长输入序列窗口,以便捕捉长程调控效应,并进一步优化重复序列的处理策略,从而推动其在植物基因组研究与作物改良中的应用前景。
整理 | DrugOne团队
参考资料
J. Zhai,A. Gokaslan,Y. Schiff,A. Berthel,Z. Liu,W. Lai,Z.R. Miller,A. Scheben,M.C. Stitzer,M.C. Romay,E.S. Buckler, & V. Kuleshov, Cross-species modeling of plant genomes at single-nucleotide resolution using a pretrained DNA language model, Proc. Natl. Acad. Sci. U.S.A. 122 (24) e2421738122,
https://doi.org/10.1073/pnas.2421738122 (2025).
本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2025-08-07,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读

