Circos安装避坑指南:从“依赖地狱”到Conda一键通关
Circos安装避坑指南:从“依赖地狱”到Conda一键通关
天意生信云
发布于 2025-12-24 15:36:16
发布于 2025-12-24 15:36:16
今天不更流程啦~更一篇软件安装教程!
提到 Circos 这个软件,做基因组圈图的朋友一定不陌生。它以精美的可视化效果著称,但与其强大功能齐名的,还有它那令人望而生畏的安装难度。
最近在帮一位服务器用户部署环境时,我再次遇到了Circos的挑战。这位用户最初发给我一篇网上的安装教程(https://www.jianshu.com/p/15b65ae2e671),希望能照着操作。然而,实际过程远比想象中曲折。今天就把这两个多小时的排雷过程记录下来,希望能帮大家节省时间,少走弯路。
按照现有教程尝试
该教程首先尝试了conda安装,但是,软件安装好之后,GD模块missing。
conda install -c bioconda circos -y
# 测试是否所有的module都安装好了
circos -module
# 所有都显示OK则成功
ok 0.39 Font::TTF::Font
missing 2.68 GD
missing 0.2 GD::Polyline
既然 Conda 自动安装缺失了 GD 模块,按照那篇参考教程的思路,下一步就是手动安装。在我采用手动安装方式的时候发现:
对于Perl GD 模块的安装,必须先安装libgd
那在安装libgd的之前,需要安装freetype、libpng、jpeg、zlib等等依赖包
等我安装好这些依赖包,开始安装libgd的时候,发现还有隐含的依赖,这种“套娃式”的依赖关系,不仅繁琐,而且极易因为版本冲突(Dependency Conflict)导致系统环境变得混乱。在这个过程中,我不仅消耗了大量精力,bug 却越修越多.....
Conda安装依赖
最后我抱着尝试的心态,选择用conda继续安装:
# 在circos环境中使用conda安装GD和相关依赖
conda activate circos
conda install -c conda-forge perl-gd
# 或者
conda install -c bioconda perl-gd
结果就是:成功了!
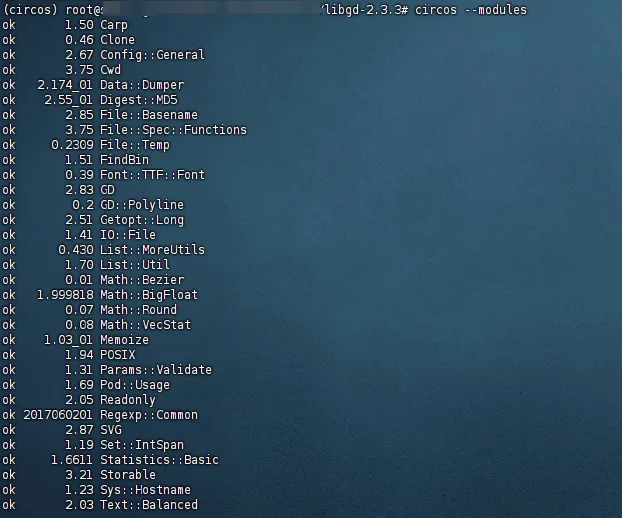
当你在安装 Circos 遇到 GD missing 报错时,不要轻易尝试手动编译源码安装(除非你是Linux编译高手)。直接使用 conda install -c conda-forge perl-gd 即可完美补全缺失的依赖。
这条命令虽然简单,却是用大量试错时间换来的经验,希望这个思路能为你的科研之路扫清一个小障碍。
本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2025-11-28,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读

