人工智能、机器学习和深度学习在植物育种中的应用介绍
人工智能、机器学习和深度学习在植物育种中的应用---中篇
介绍
近年来,由于人工智能(AI)技术的进步,特别是机器学习(ML)和深度学习(DL)技术的推动,植物育种领域经历了一场范式转变。这些尖端技术改变了我们对植物生物学的理解。从解码植物防御的复杂分子机制到自动化疾病检测和优化营养水平,AI正在重塑植物育种。AI辅助的组学技术提供了对植物-病原体相互作用的新见解,并促进了应激反应基因的识别。
本篇参考专题(https://doi.org/10.3389/fpls.2024.1420938)介绍了几篇关于计算机技术在植物科学中的应用的论文。
利用机器学习、深度学习应用于植物科学的主要研究-ML
ML算法,如随机森林(RF)和XGBoost,在估算作物产量和识别理想基因型方面表现出色。Pugh等人展示了使用无人机获取的高通量表型数据预测花生产量并提高育种效率的ML模型的有效性。通过应用地上性状来估算地下产量,他们的方法克服了传统表型组学中的限制。
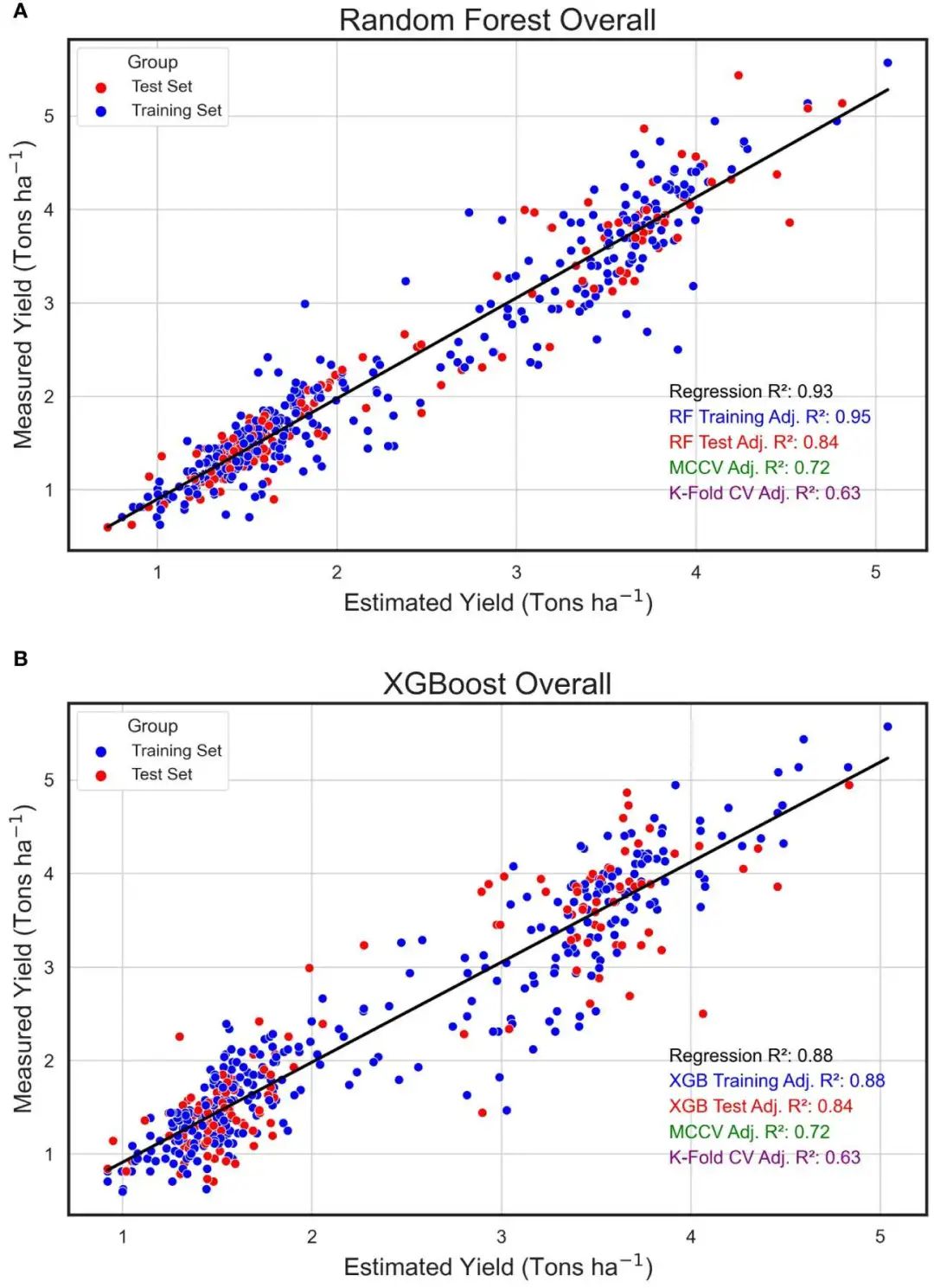
如图是机器学习模型预测的地块级产量值(吨/公顷)与将两年的研究结果结合起来后在田间测量的实际产量(测量产量)之间的线性回归。使用的机器学习模型包括随机森林(RF,A)和 XGBoost(XGB,B)。
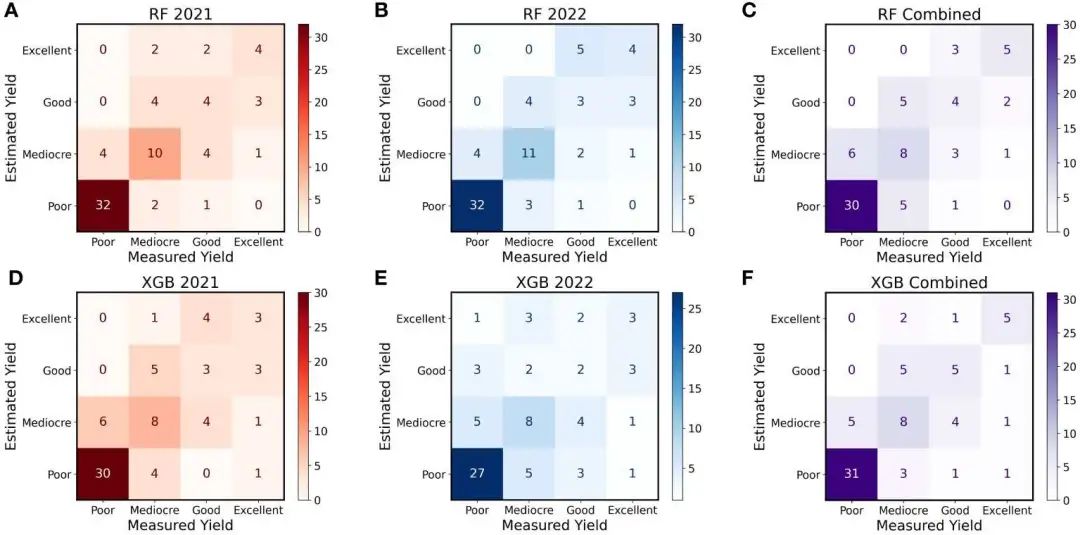
花生产量估算和测量的混淆矩阵。这些混淆矩阵显示在 2021 年和 2022 年期间使用随机森林 (RF) 和 XGBoost (XGB) 模型对产量进行正确和错误分类的数量。从左到右依次为 2021 年的 RF (A)、2022 年的 RF (B)、合并年份的 RF (C)、2021 年的 XGB (D)、2022 年的 XGB (E)和合并年份的 XGB (F)。
在这方面,Li等人强调了无人机遥感和植被指数在冬小麦产量预测中的进展,但强调了有效特征选择以提高模型性能的必要性。他们的发现证明了Cubist模型的优越性,显示了PCRF-RFE方法的有效性,并为未来的产量预测和特征选择研究提供了宝贵的见解。
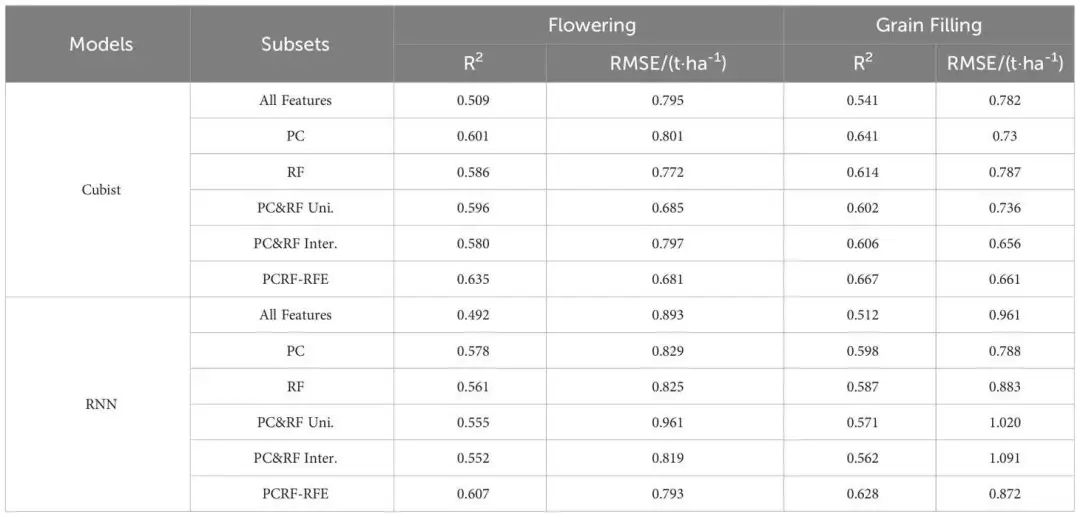
分别基于花期和灌浆期全部特征、利用主成分法和RF重要性法筛选出的特征子集以及提出的PCRF-RFE方法筛选出的特征子集,构建Cubist和RNN产量预测模型,预测模型精度如表中所示。基于花期PCRF-RFE方法筛选出的特征子集构建的Cubist产量预测模型精度最好。
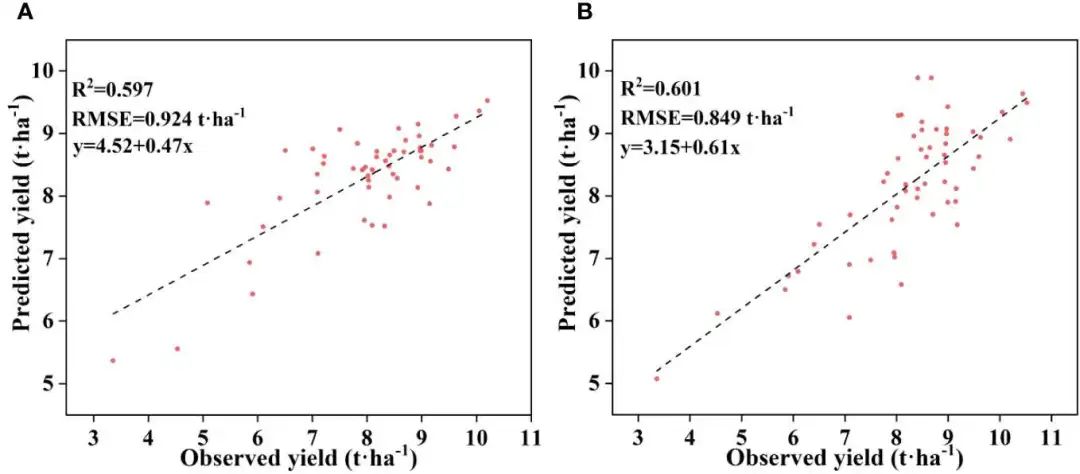
最佳模型Cubist产量预测模型的观测产量和预测产量分布。(A)开花期,(B)灌浆期。
Mousavi等人通过整合土壤和环境因素与ML预测小麦产量,解决了产量预测的挑战。通过整合土壤属性、地形特征和植被指数,他们的研究应用RF和人工神经网络(ANNs)绘制实际小麦产量,展示了ML在优化农业生产中的潜力。
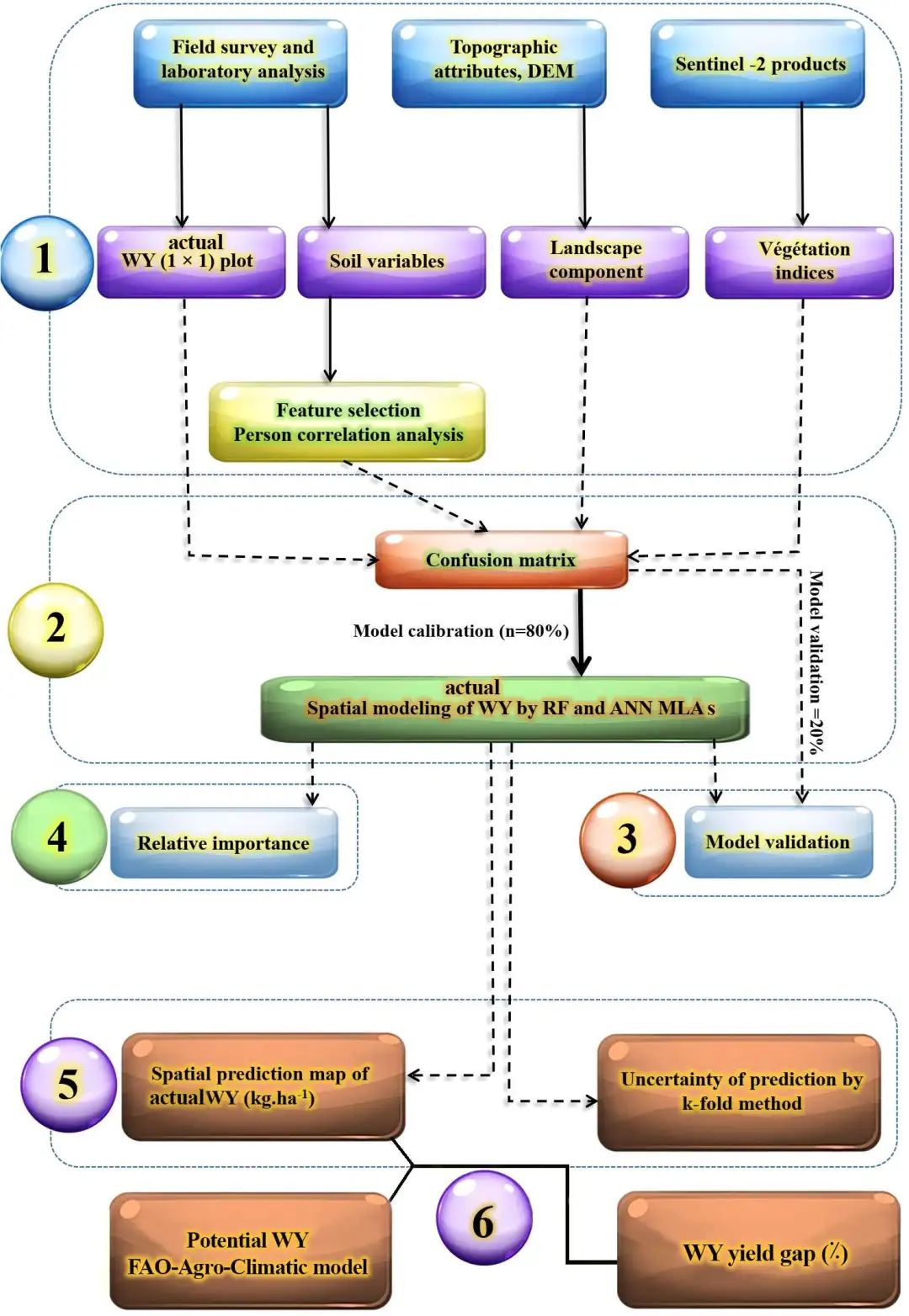
使用 RF 和 ANN MLA 对 WY 进行空间建模流程图
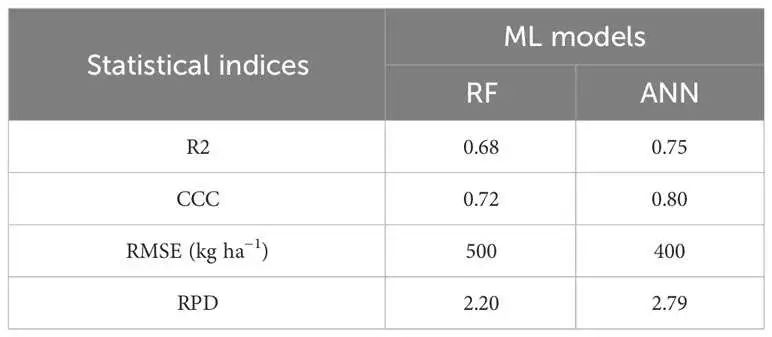
RF和ANN模型应用于实际WY预测的模型预测性能统计。
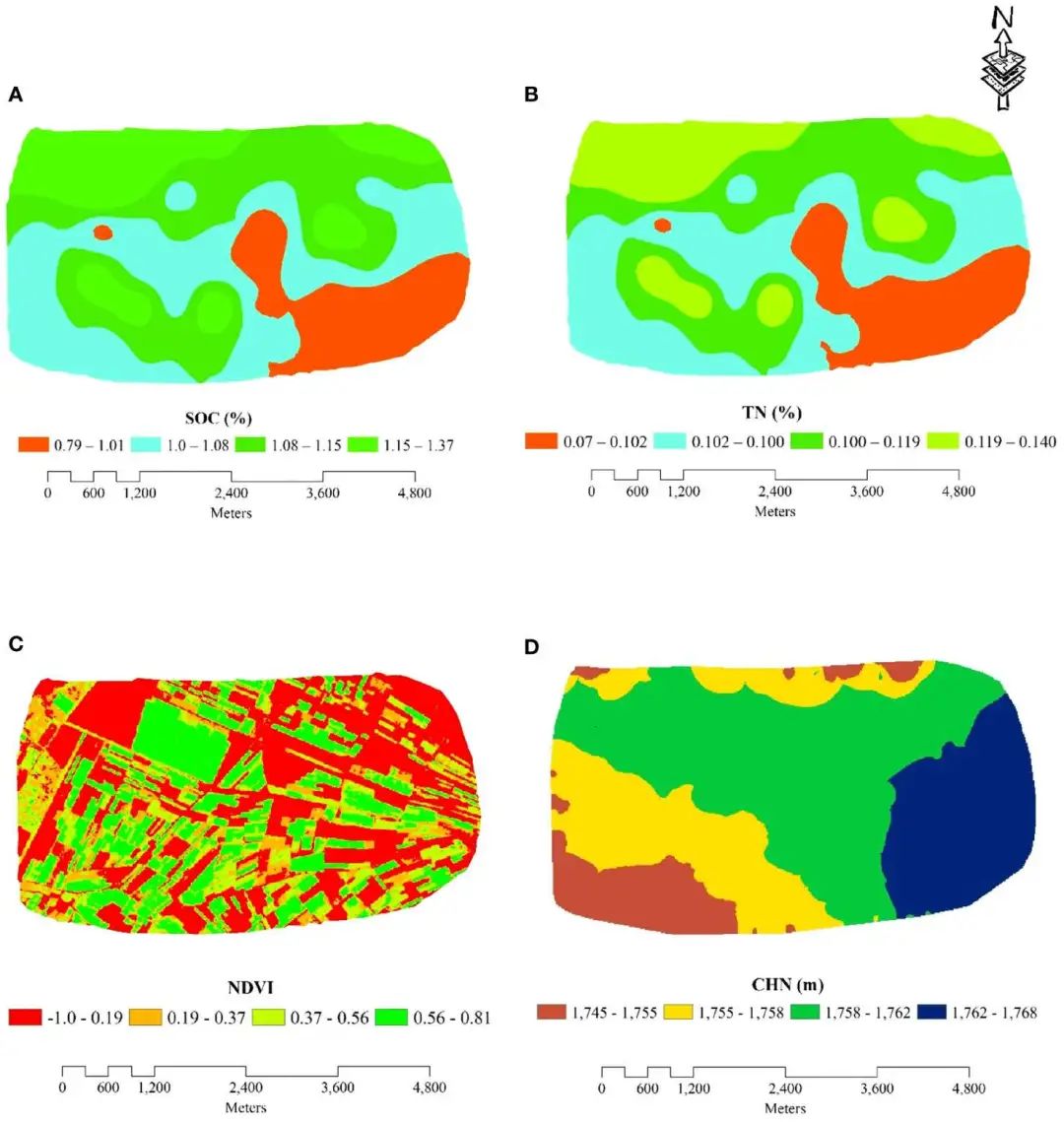
鉴于 ANN 模型在预测实际 WY 方面表现优异,因此基于 ANN 的输出讨论了 RI 结果。展示了基于RI分析的四个重要协变量。
利用机器学习、深度学习应用于植物科学的主要研究-DL
DL方法,特别是卷积神经网络(CNNs),在植物育种中的图像分析方面取得了革命性进展。Davidson等人提出了一项突破性研究,探索了CNNs在自动分析成熟体细胞胚胎方面的潜力,这是植物繁殖中的关键过程。通过使用CNN进行体细胞胚胎的语义和实例分割,他们的研究证实了神经网络方法在划分形态区域和计数子叶方面的精度和效率,与之前的技术相比提供了前所未有的准确性和效率。通过实现精确的形态特征分割和计数,AI辅助方法为进一步分析体细胞胚胎和提高农业和林业中的作物生产力和可持续性开辟了途径。
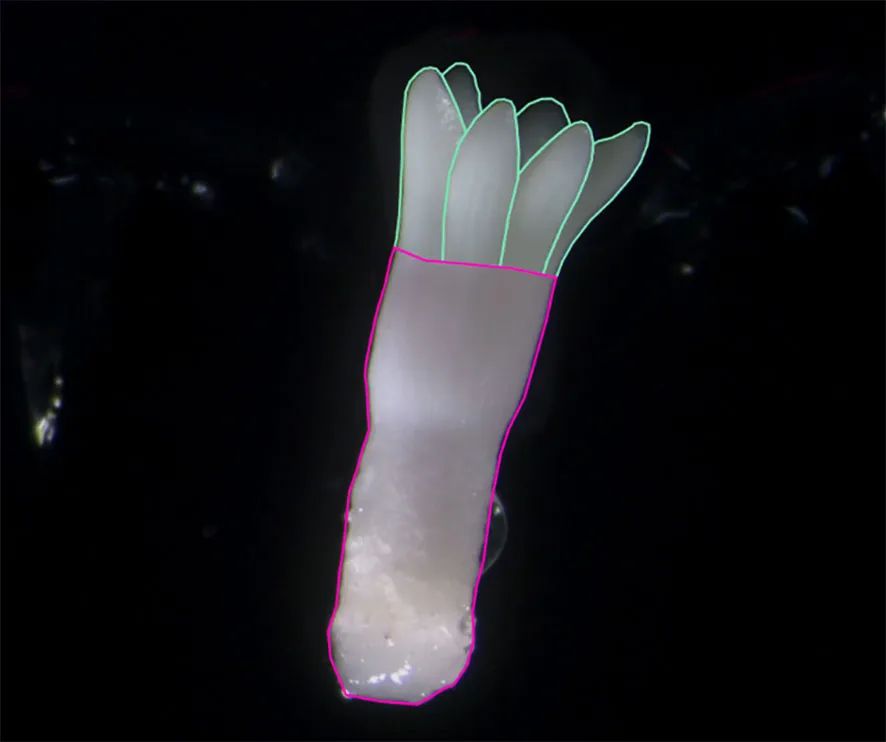
辐射松体细胞胚的注释图像
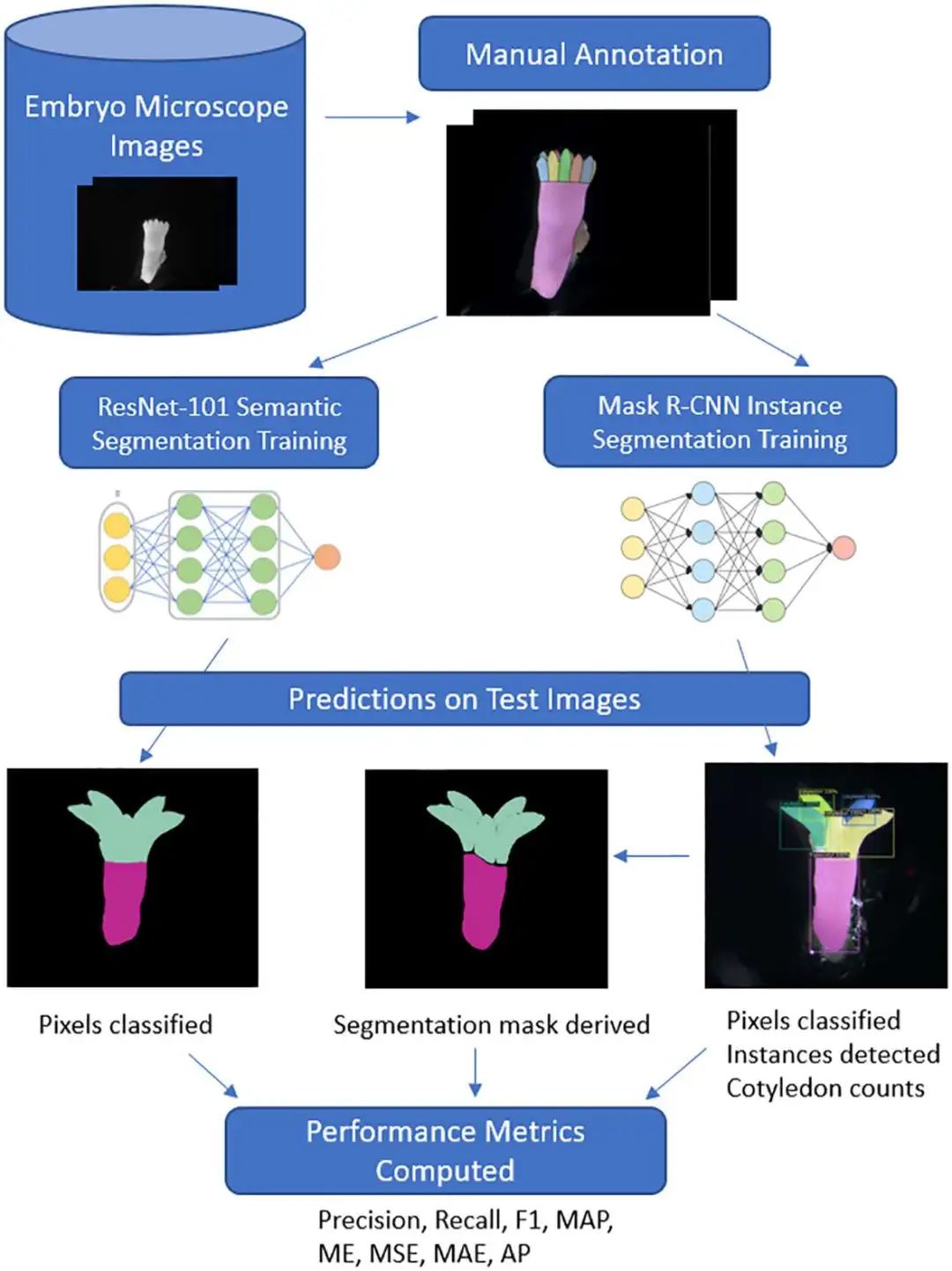
松树体细胞胚分割的深度学习工作流程。
DL模型具有优化农业实践和提高作物管理策略的潜力。YOLO(You Only Look Once)架构以其实时目标检测能力而闻名,广泛应用于植物图像分析中的目标检测(Liu等,2024)。Li等人展示了CFNet-VoV-GCSP-LSKNet-YOLOv8s模型在具有挑战性的环境条件下准确识别棉花害虫和疾病的有效性。模型的卓越性能为害虫和疾病爆发的实时监测和早期干预提供了有希望的解决方案,从而减轻了产量损失并减少了对化学干预的依赖。这篇文章宣告了棉花植物育种新时代的到来,其中尖端的AI、ML和DL技术汇聚在一起,以显著的精度和效率解决长期存在的挑战。
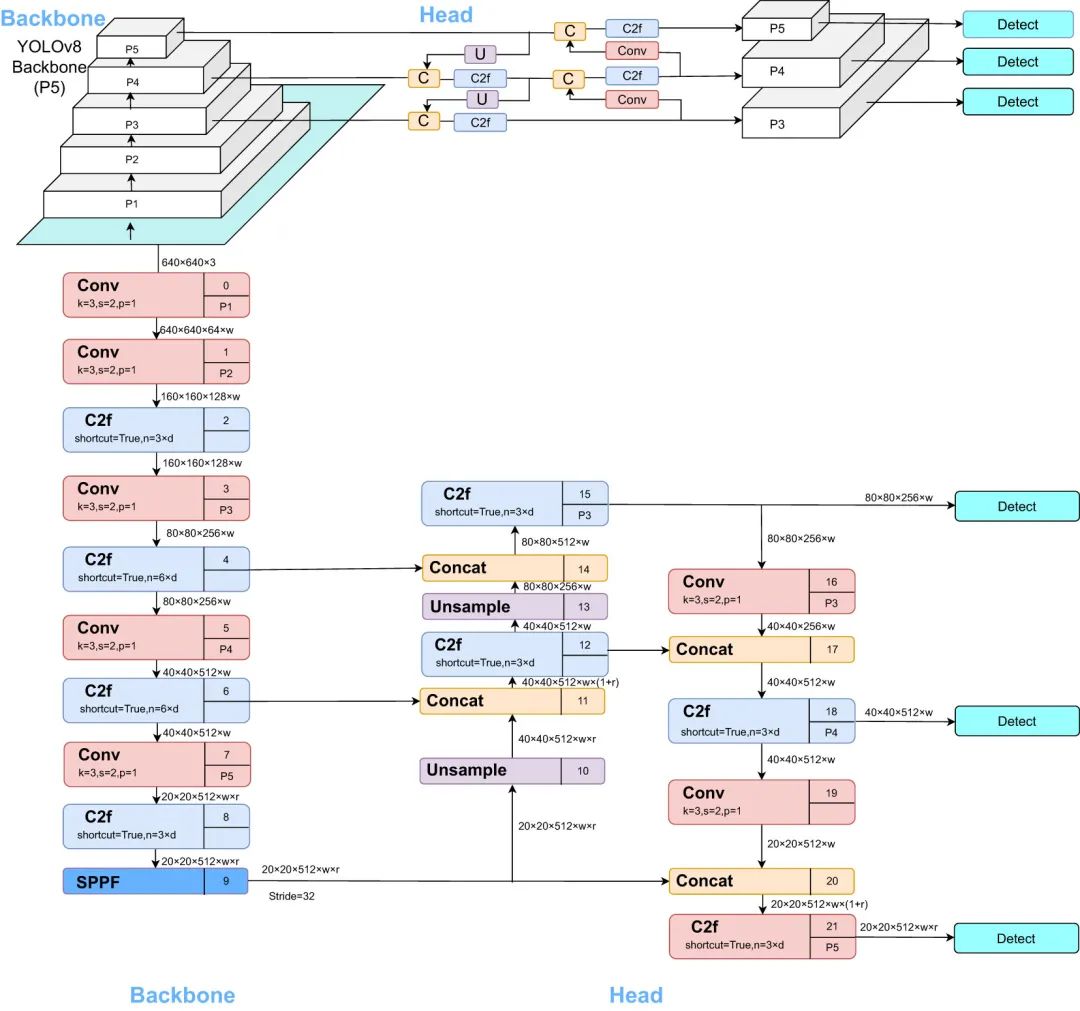
YOLOv8s网络架构
通过提供害虫和疾病识别与控制的坚实技术基础,CFNet-VoV-GCSP-LSKNet-YOLOv8s模型成为农业可持续性追求中的一个变革者。
总结
总体而言,从解码复杂的组学数据到自动化表型性状分析和疾病检测,AI、ML和DL技术提供了独特的机会,革新育种实践,开发抗逆和高产作物品种,并在应对日益严重的环境挑战中贡献全球粮食安全。对植物育种中AI应用的持续投资是解锁农业全部潜力的关键,并有利于确保后代繁荣和可持续未来。
感兴趣可以阅读下面相关参考文献
Eftekhari, M., Ma, C., & Orlov, Y. L. (2024). Editorial: Applications of artificial intelligence, machine learning, and deep learning in plant breeding. Frontiers in plant science, 15, 1420938. https://doi.org/10.3389/fpls.2024.1420938
Pugh, N. A., Young, A., Ojha, M., Emendack, Y., Sanchez, J., Xin, Z., & Puppala, N. (2024). Yield prediction in a peanut breeding program using remote sensing data and machine learning algorithms. Frontiers in plant science, 15, 1339864. https://doi.org/10.3389/fpls.2024.1339864
Li Z, Zhou X, Cheng Q, Zhai W, Mao B, Li Y, Chen Z. An integrated feature selection approach to high water stress yield prediction. Front Plant Sci. 2023 Dec 4;14:1289692. doi: 10.3389/fpls.2023.1289692. PMID: 38111876; PMCID: PMC10726204.
Mousavi, S. R., Jahandideh Mahjenabadi, V. A., Khoshru, B., & Rezaei, M. (2024). Spatial prediction of winter wheat yield gap: agro-climatic model and machine learning approaches. Frontiers in plant science, 14, 1309171. https://doi.org/10.3389/fpls.2023.1309171
Davidson, S. J., Saggese, T., & Krajňáková, J. (2024). Deep learning for automated segmentation and counting of hypocotyl and cotyledon regions in mature Pinus radiata D. Don. somatic embryo images. Frontiers in plant science, 15, 1322920. https://doi.org/10.3389/fpls.2024.1322920
Li, R., He, Y., Li, Y., Qin, W., Abbas, A., Ji, R., Li, S., Wu, Y., Sun, X., & Yang, J. (2024). Identification of cotton pest and disease based on CFNet- VoV-GCSP -LSKNet-YOLOv8s: a new era of precision agriculture. Frontiers in plant science, 15, 1348402. https://doi.org/10.3389/fpls.2024.1348402
本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2024-10-27,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读
目录

