两蛋白间的分子对接—2
原创两蛋白间的分子对接—2
1 与Chatgpt之间的对话
需要进行的是SFN和HDAC6两蛋白分子的对接,思路是
Uniprot数据库中检索SFN与HDAC6蛋白质,挑选分别率最佳的构象。SFN对应PDB数据库中3IQU,HDAC6对应PDB数据库中5B8D。使用HDOCK进行分子对接,挑选最佳对接结果导入PYMOL进行可视化。
这是我上一篇分子对接帖子的实现思路,但是是有问题的,在 选择构象的时候,未关注到结构的完整性,在分子对接前需要对分子进行处理,如去除多余配体,水分子等,再进行分子对接 。
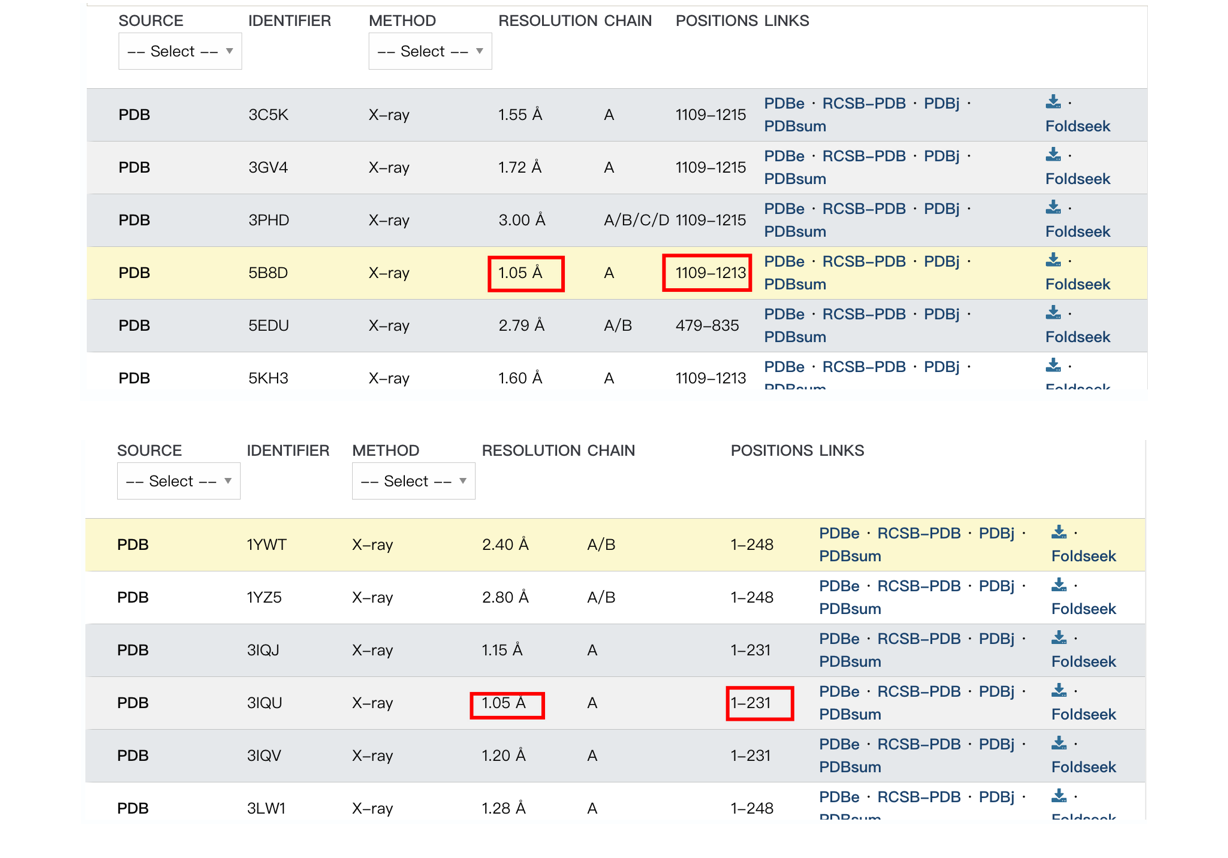
以下记录和chatgpt的对话:



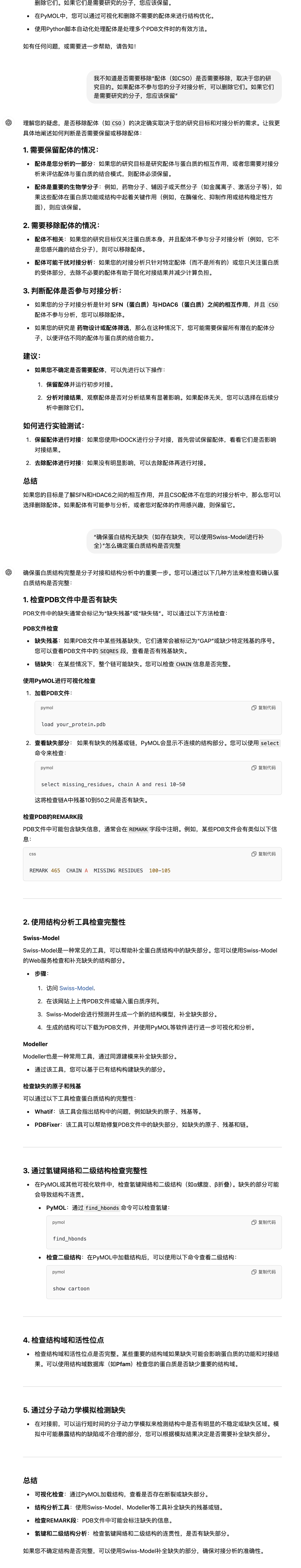



2 优化后的分析流程
具体看最后一条与chatgpt之间的对话
现在的分析流程是下载AF-Q9UBN7-F1、AF-P31947-F1 的PDB文件,不需要去除水分子和多余配体,因为AlphaFold预测的结构中不含有。使用HDOCK进行分子对接,HDAC6结构为受体,SFN为配体。
对接结果
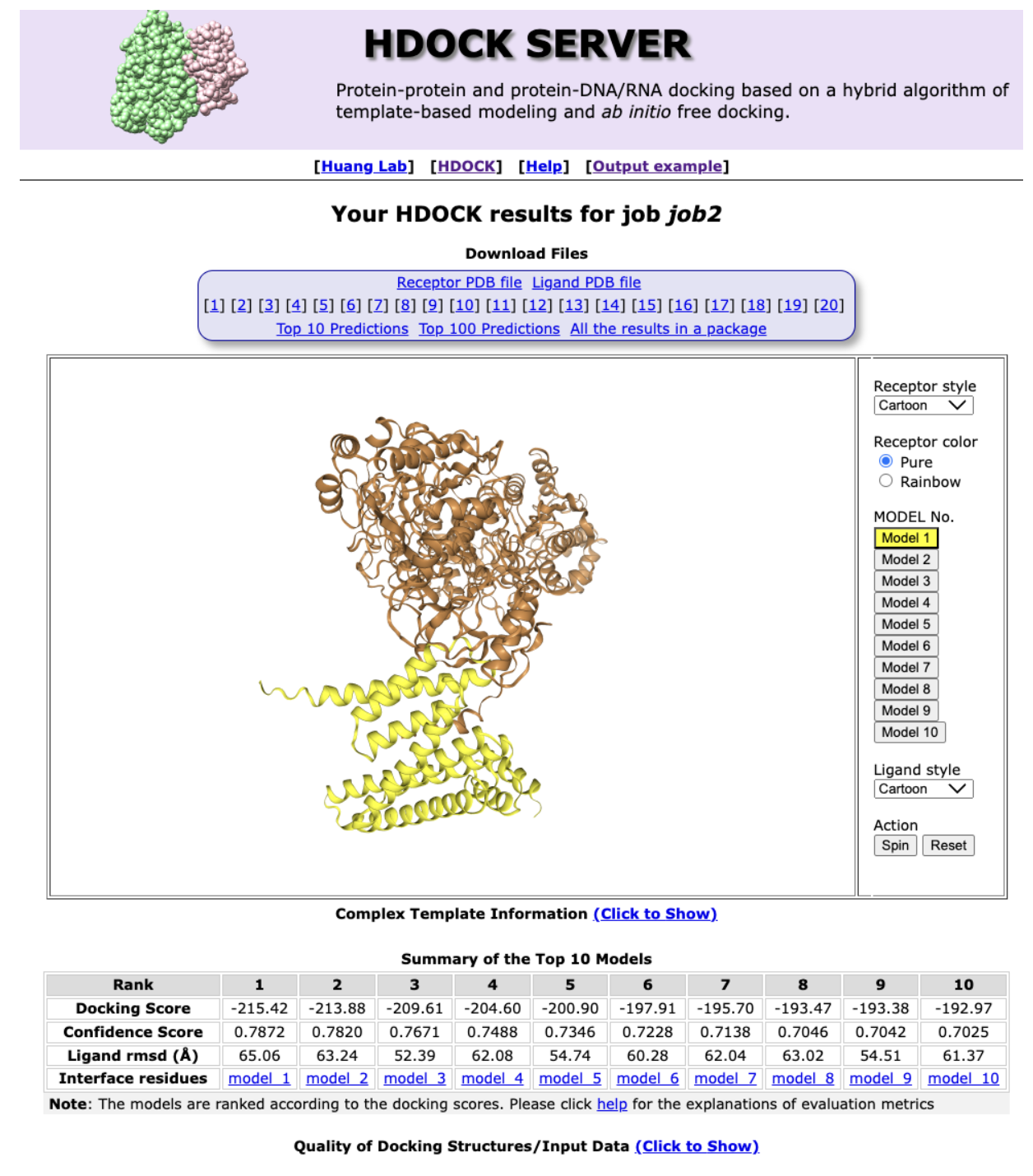
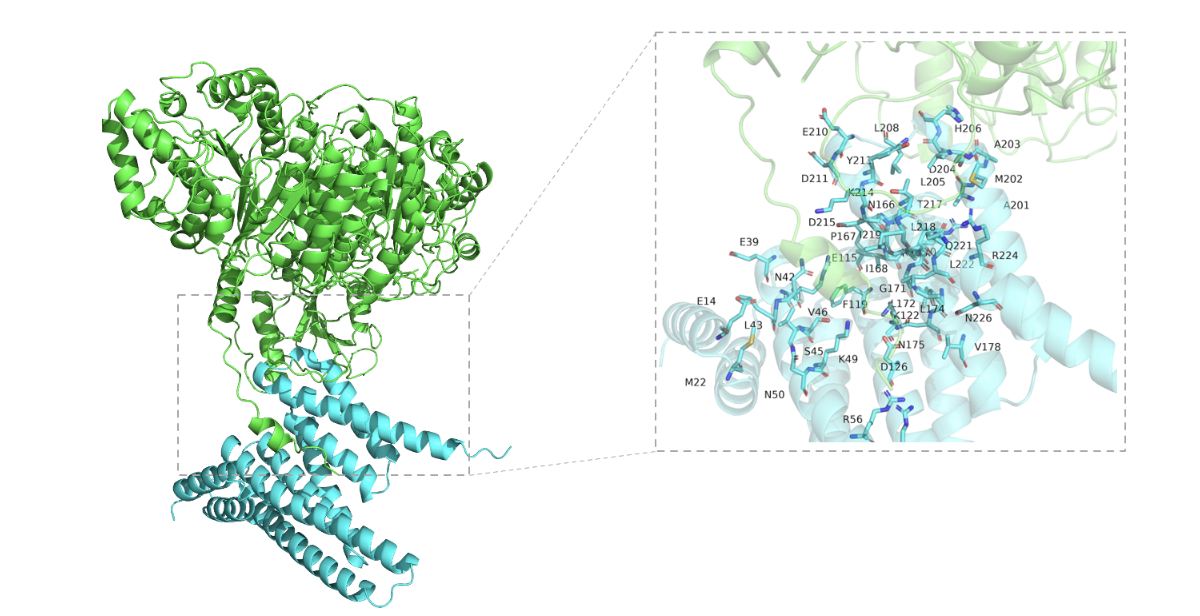
3 导入pymol进行可视化
将RANK1 导入pymol进行可视化,主要操作是现实受体的5A活性口袋,然后把对应的棍状结构和氨基酸残基显示即可。
原创声明:本文系作者授权腾讯云开发者社区发表,未经许可,不得转载。
如有侵权,请联系 cloudcommunity@tencent.com 删除。
原创声明:本文系作者授权腾讯云开发者社区发表,未经许可,不得转载。
如有侵权,请联系 cloudcommunity@tencent.com 删除。
评论
登录后参与评论
推荐阅读
目录


