生信星球 学习小组Day3笔记--Linux的软件安装 高小能
原创生信星球 学习小组Day3笔记--Linux的软件安装 高小能
原创用户10633522
修改于 2023-06-29 09:27:51
修改于 2023-06-29 09:27:51
Conda — linux的软件管理专家
认识 Conda
Conda 是 linux 系统中最方便快捷的下载器,两个版本:建议安装miniconda版
安装 Conda
- 浏览器搜索“miniconda 清华”,点击进入,下划找到 miniconda 网址
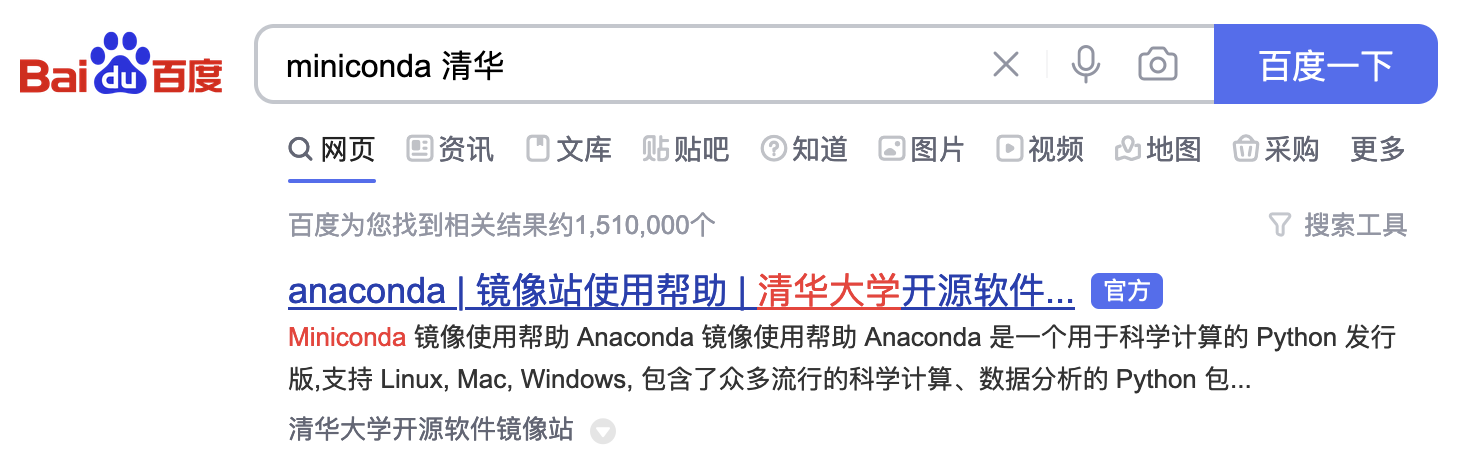
搜索

找到 miniconda 网址
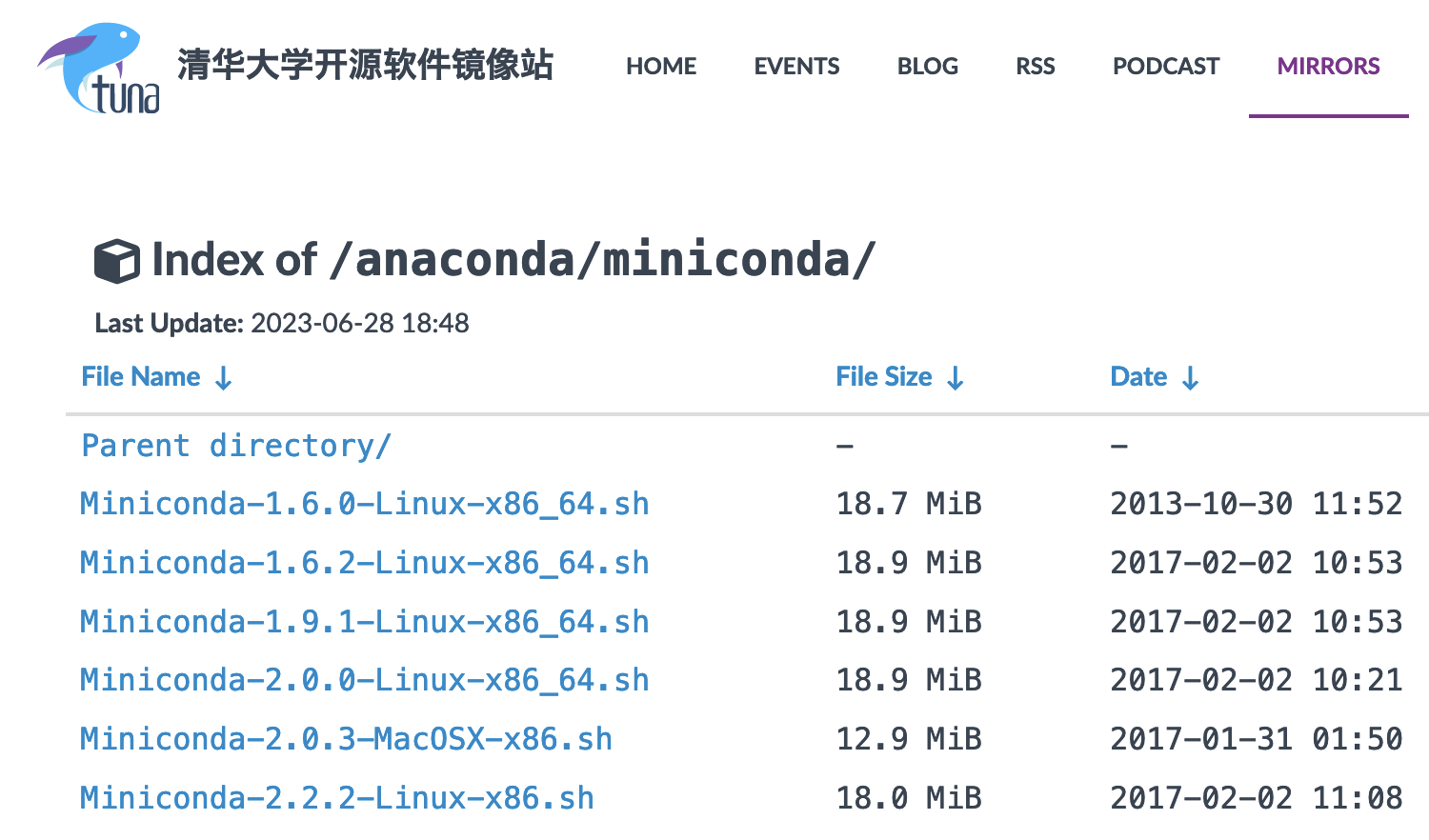
版本列表
- 查看自己的服务器是多少位的:
uname -a

查看服务器信息
- 在自己的服务器新建一个文件夹,专门存放软件
mkdir biosoft进入文件夹cd biosoft - 右键最新版本的 miniconda 链接,复制链接,在服务器页面用 wget 命令➕链接
wget https://mirrors.tuna.tsinghua.edu.cn/anaconda/miniconda/Miniconda3-py39_23.3.1-0-Linux-x86_64.sh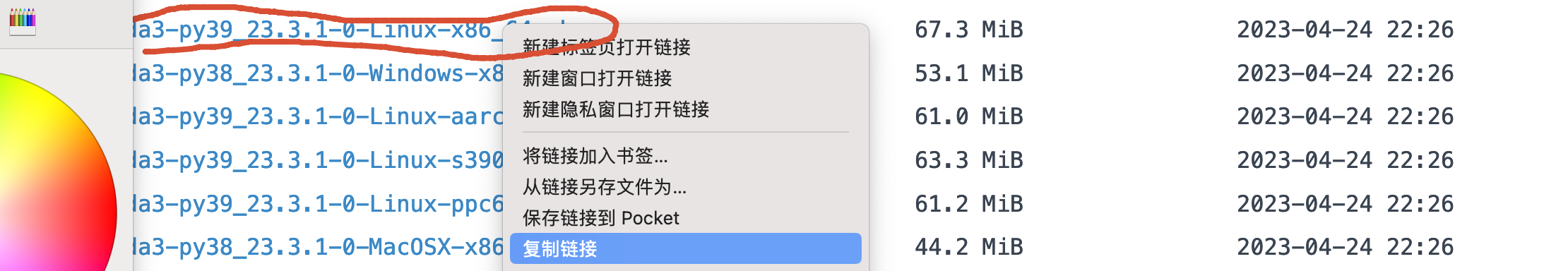 复制链接
复制链接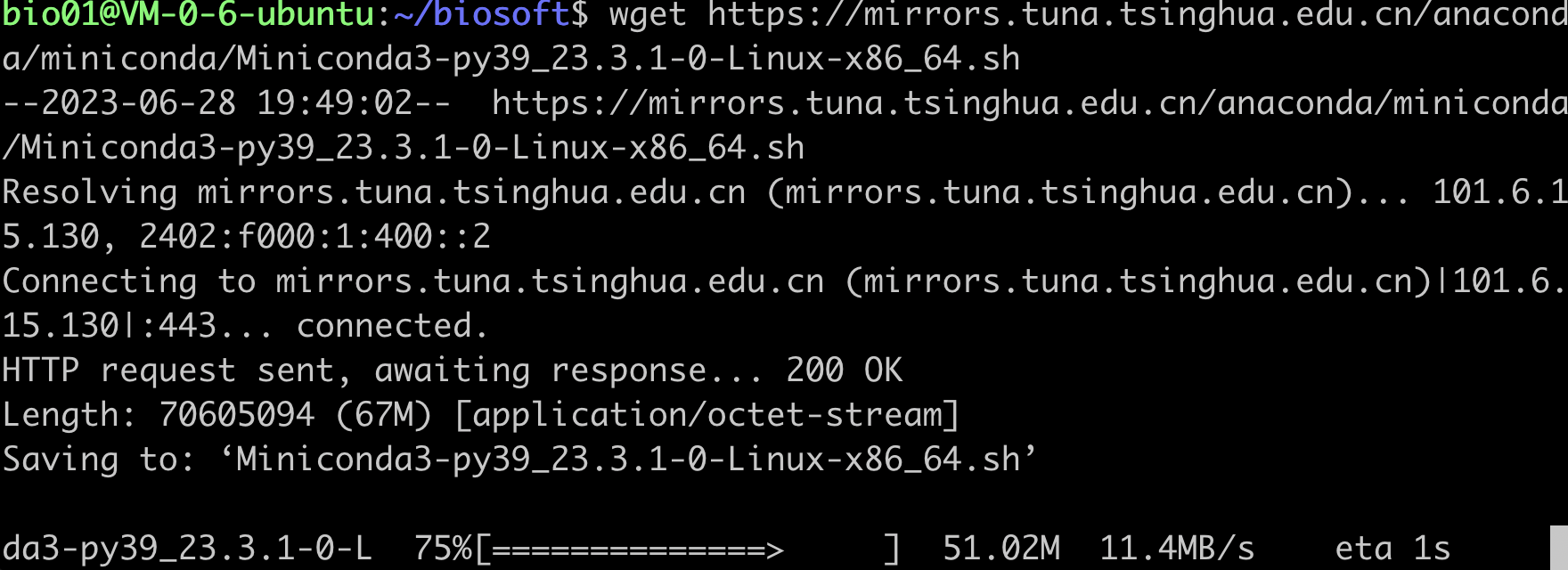 下载 miniconda
下载 miniconda - 安装 miniconda,
ll命令能看到刚才下载的文件 输入bash Miniconda3-latest-Linux-x86_64.sh
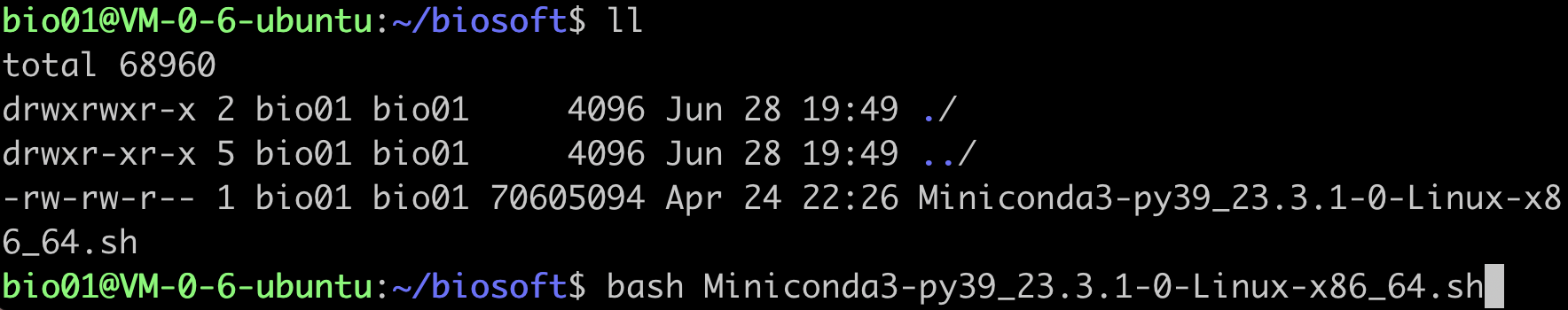
安装
- 一直按 enter 键,直到出现下图,输入
yes,按enter,接着 enter

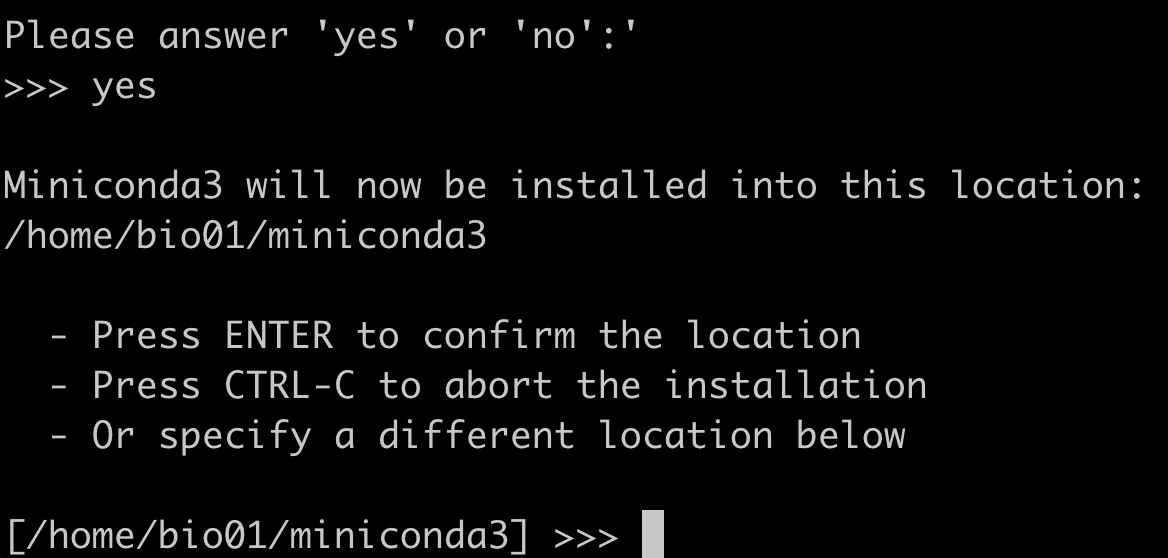
接着 enter
yes
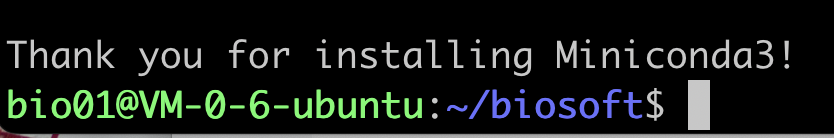
成功!
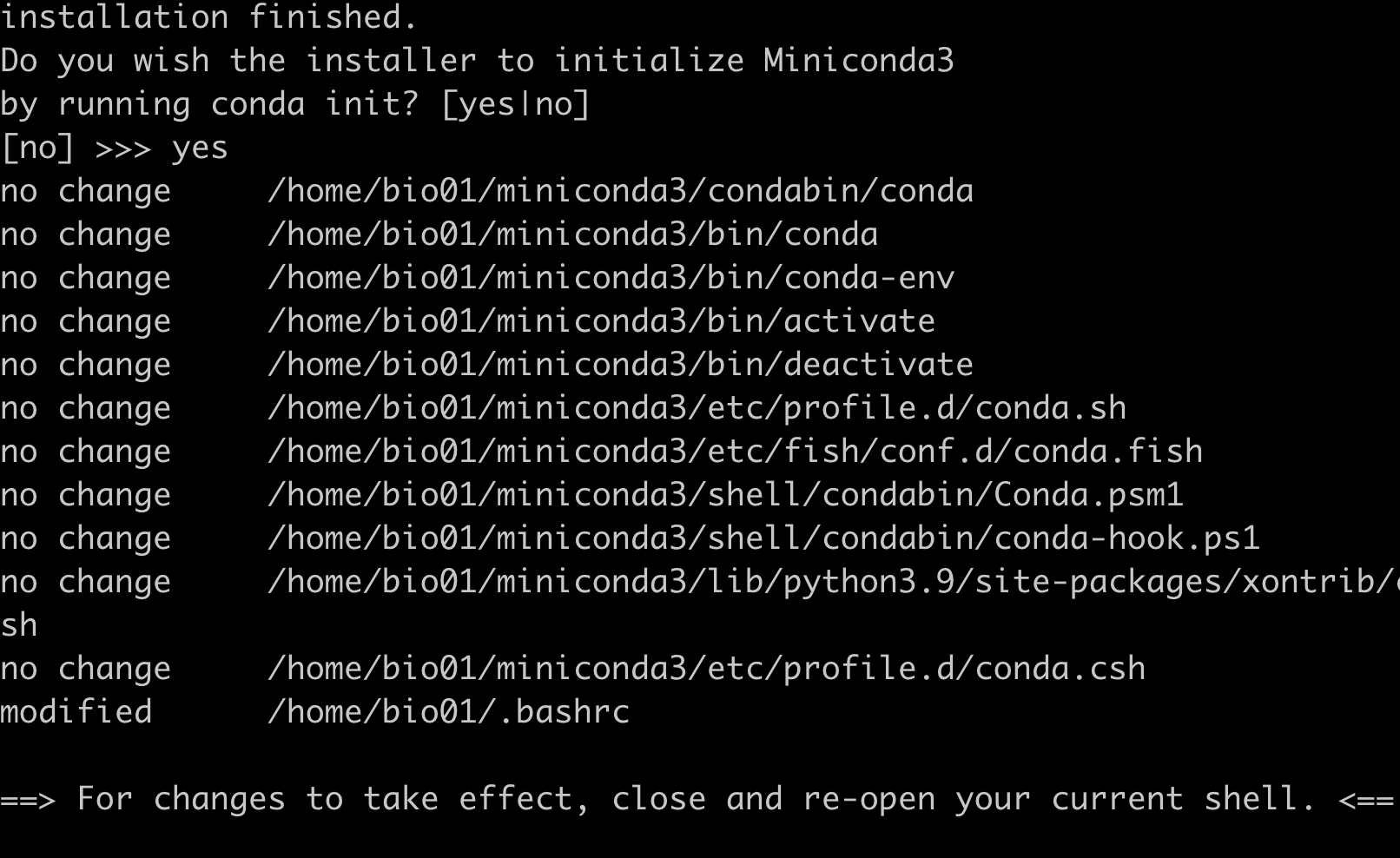
- 最后还要激活
source ~/.bashrc然后输入conda,出现满屏信息,大功告成!
大功告成!
添加镜像
所谓镜像网站,相当于主网站的副本,conda在国外,我们在国内下载软件速度会很慢,因此配置镜像,从镜像网站下载,可以加快下载速度。
复制下边的代码,添加我们常用的镜像网站
# 使用中科大的镜像
conda config --add channels https://mirrors.bfsu.edu.cn/anaconda/cloud/bioconda/
conda config --add channels https://mirrors.bfsu.edu.cn/anaconda/cloud/conda-forge/
conda config --add channels https://mirrors.bfsu.edu.cn/anaconda/pkgs/free/
conda config --add channels https://mirrors.bfsu.edu.cn/anaconda/pkgs/main/
conda config --set show_channel_urls yes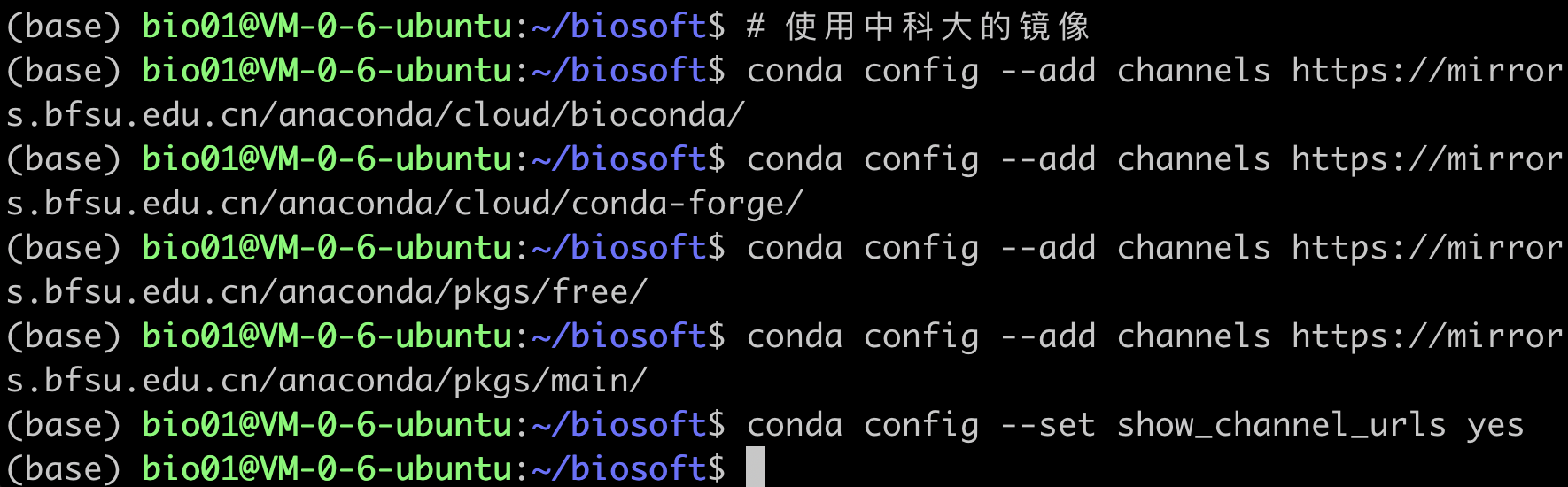
添加镜像
使用 conda
1 查看当前服务器上安装的所有软件列表 conda list
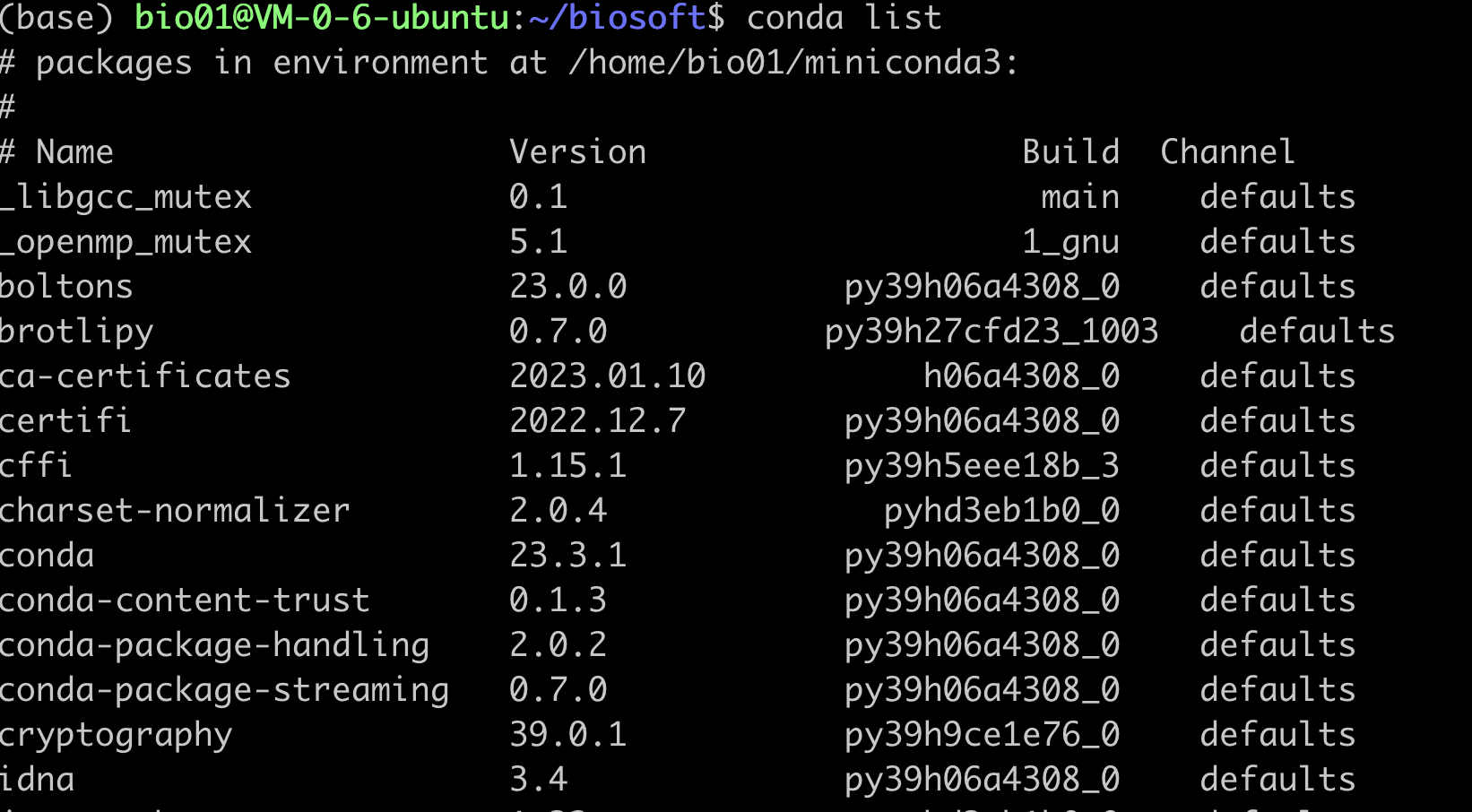
查看软件列表
2 安装软件,以fastqc软件为例, conda install fastqc -y (-y是yes,安装过程中conda问你的问题全部回答yes)
默认安装最新版本,但是有的软件新版本bug比较多,可能需要用到老版本 如果要指定版本号,可以
conda install fastqc=0.11.7 -y
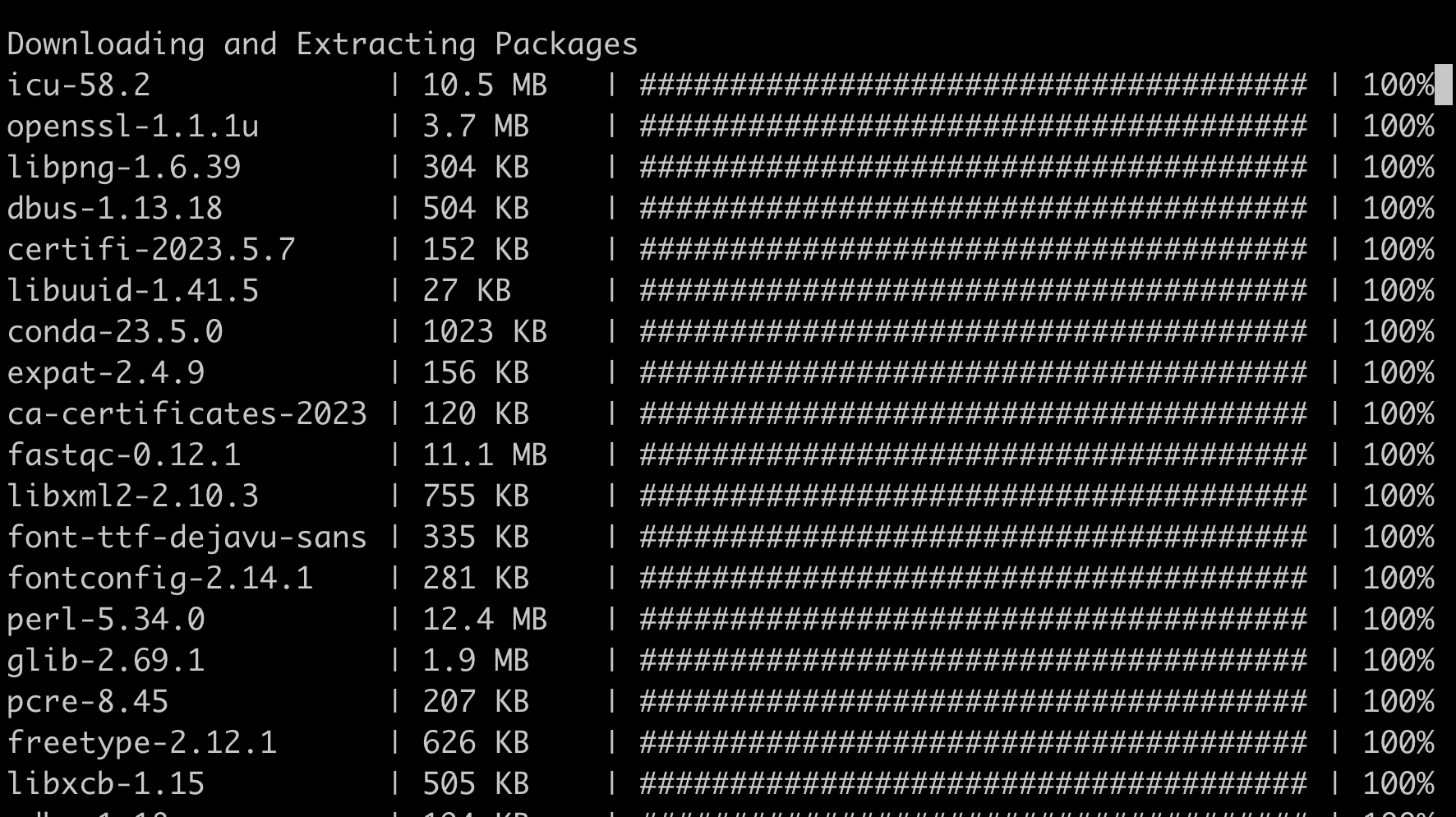
安装过程
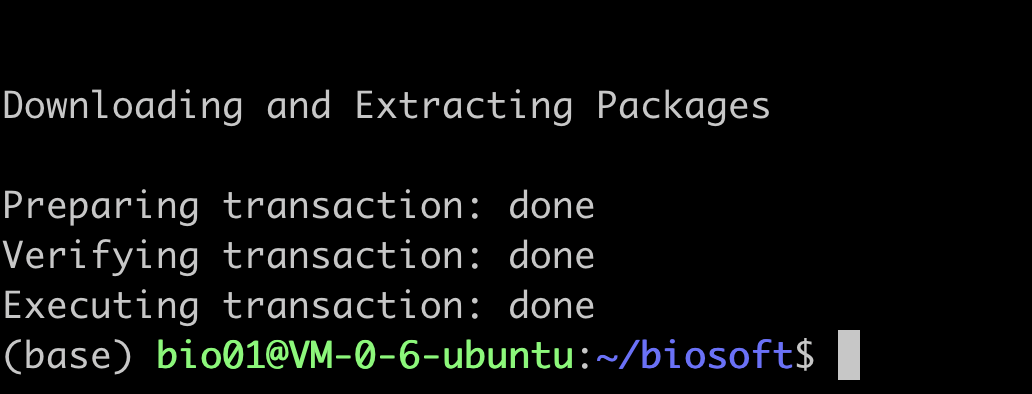
安装完成
3 确认fastqc软件是否安装成功
输入fastqc --help,出现大片文字,说明安装成功
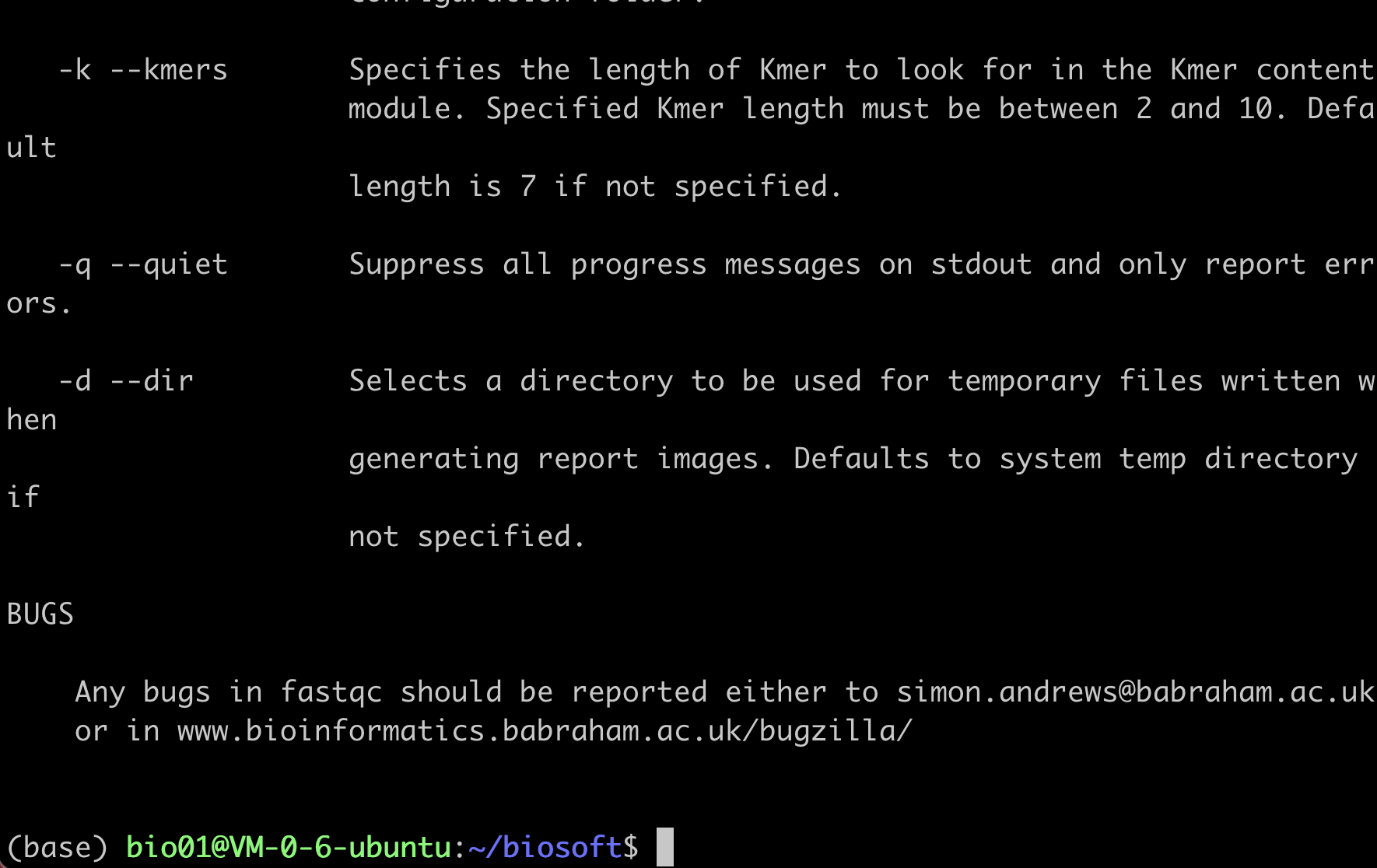
帮助文档
4 卸载软件conda remove fastqc -y
因练习服务器比较弱,任务没有成功
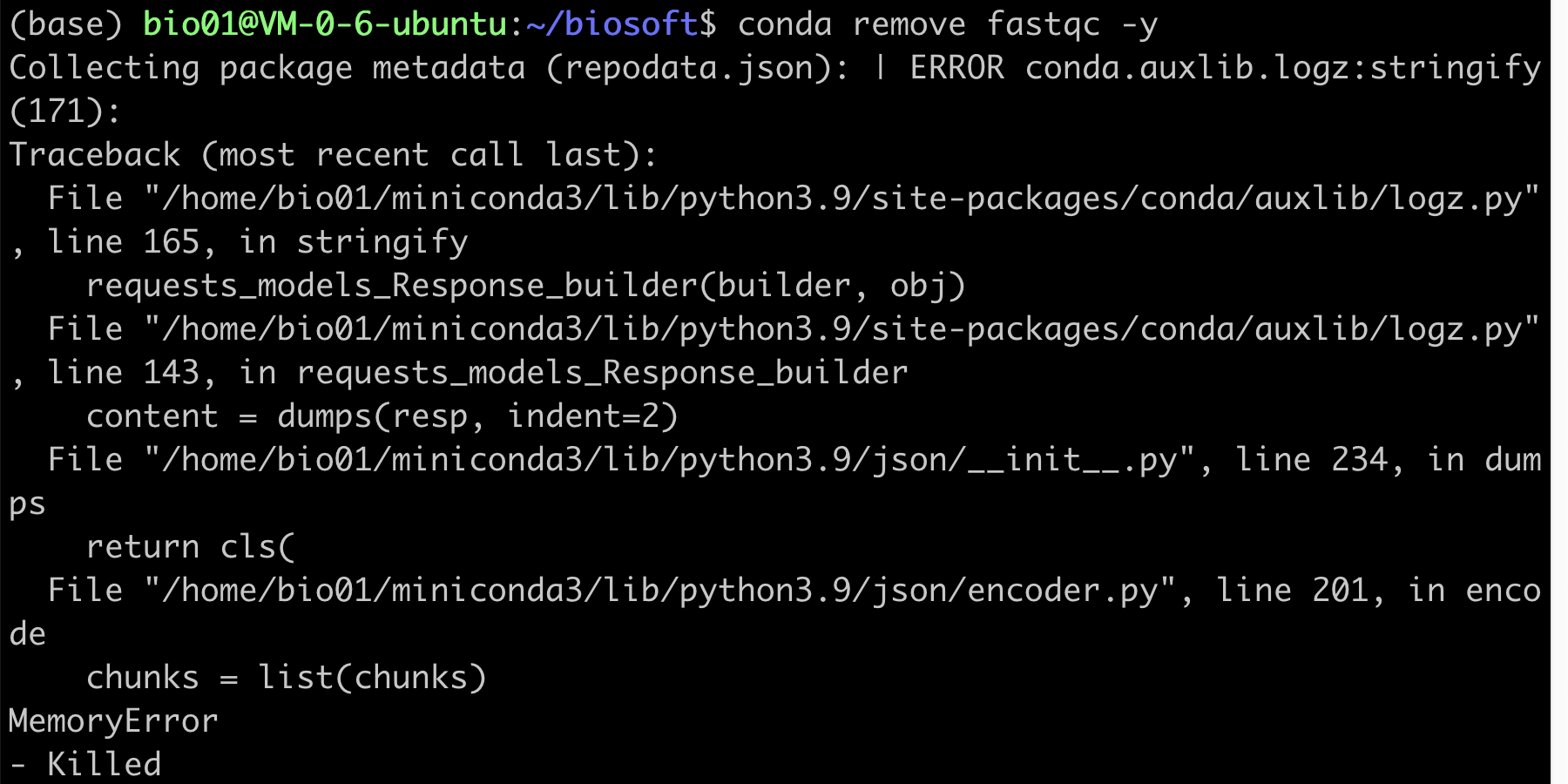
卸载失败
5 添加环境
- 先查看当前conda有哪些环境
conda info --envs(前面带*的就是默认的),可以看到,我们目前就一个conda环境
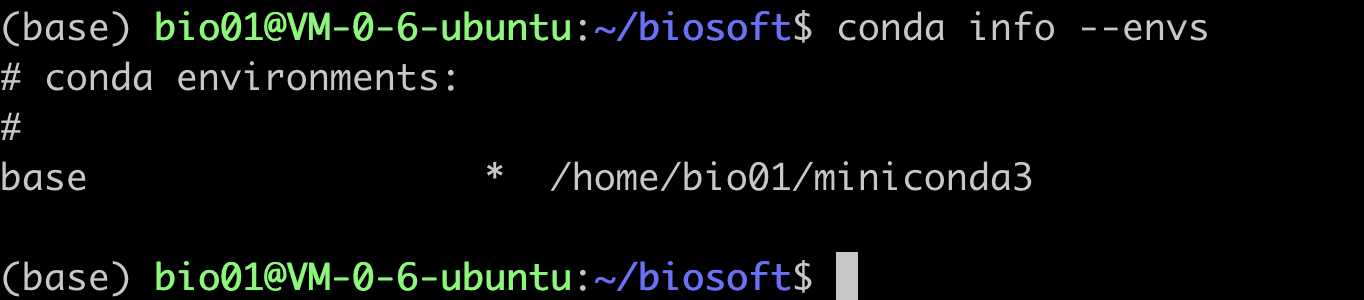
查看环境
比如我们要处理转录组数据了,好,先建立一个名叫rnaseq的conda环境,然后指定python版本是3,安装软件fastqc、trimmomatic(这两个可以一步完成)(这里指定python版本是因为有的软件是基于python开发的)
conda create -n rna-seq python=3 fastqc trimmomatic -y,这段代码可以创建一个新的 conda 环境,还能把fastqc、trimmomatic这两个软件安装在新的环境里。
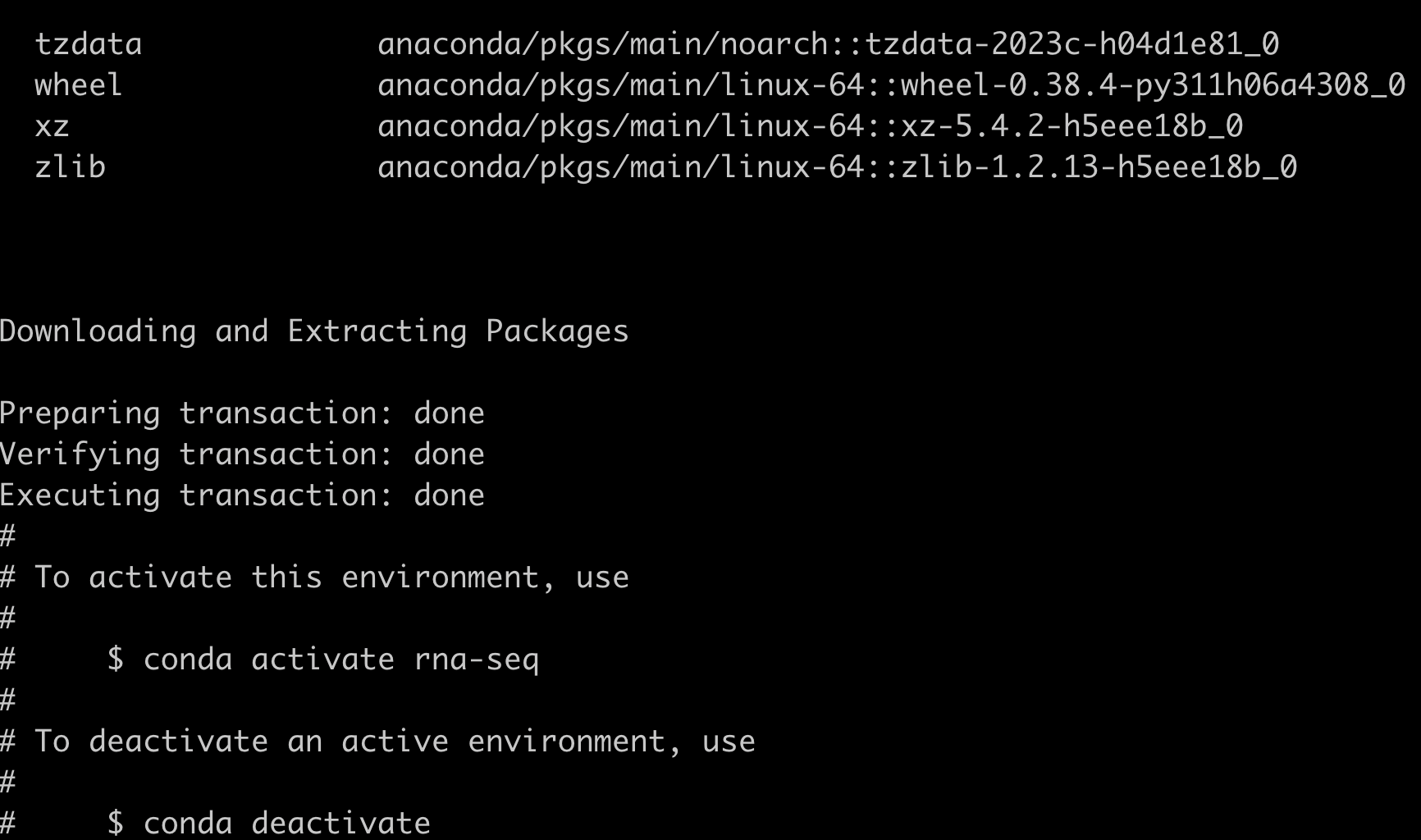
创建新环境并下载完成软件
创建完之后,再次查看一下我们的conda环境,
conda info --envs,看是不是多了一个rna-seq。但是发现,默认还是base
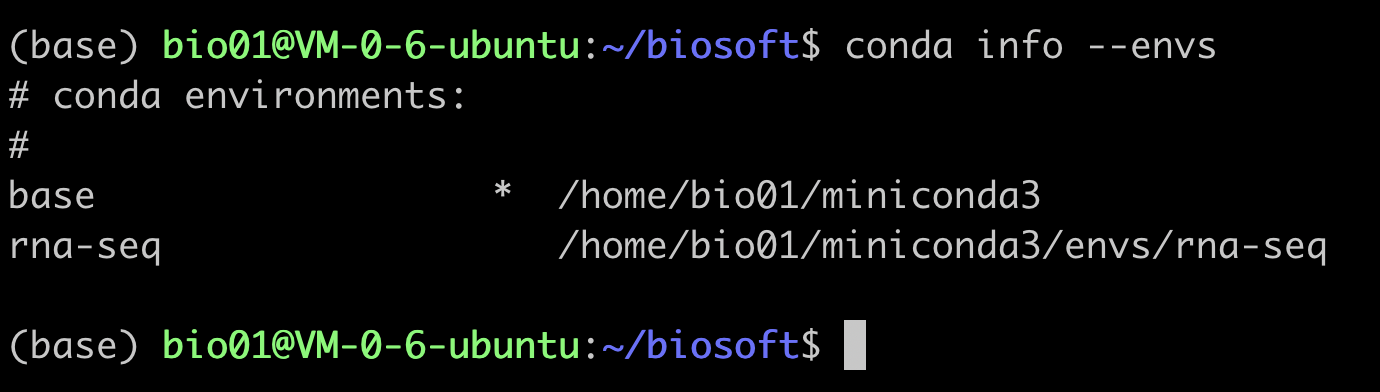
查看环境
6 激活环境
conda activate rna-seq,这时默认的*就会转移到rna-seq前面; 另外你会发现在用户名前面出现了(rna-seq)

激活环境
输入trimmomatic会出现该软件的用法文档
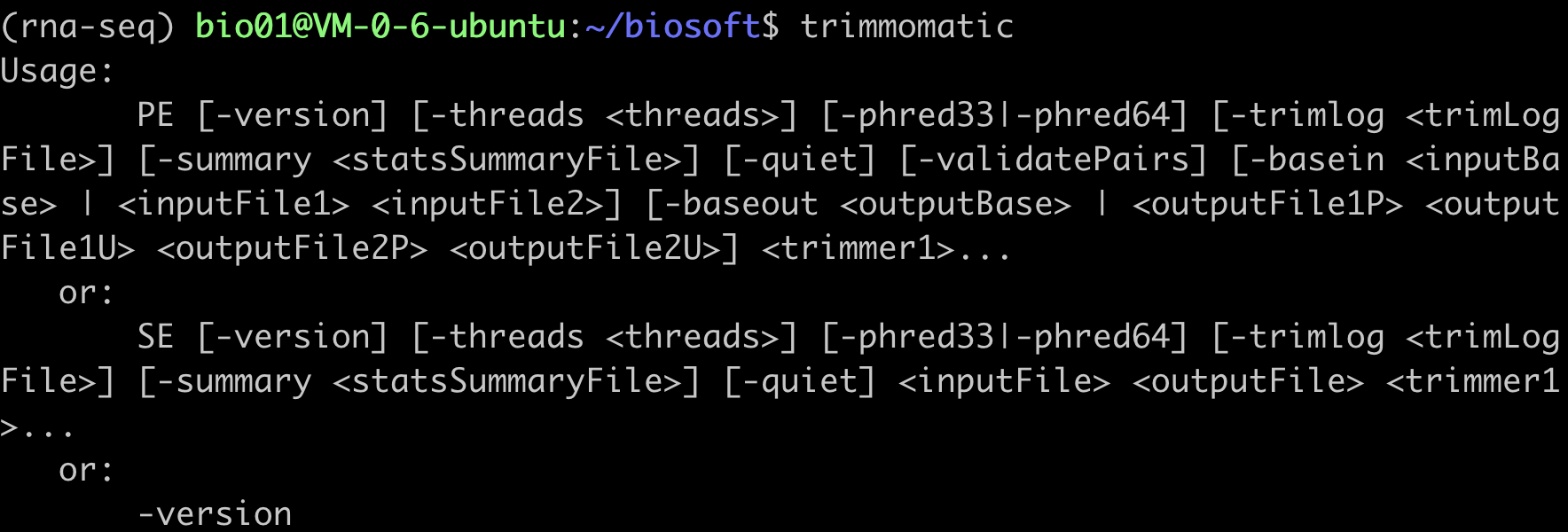
7 退出环境conda deactivate,又回到了 base 环境

退出环境
这次安装感觉还是很顺利的,但是也常常会出现各种 bug,大家一定利用好搜索功能,一般问题网上一般都会查到,不要气馁,问题总会解决,也祝大家在今后安装软件的时候大吉大利,BUG 全无!
原创声明:本文系作者授权腾讯云开发者社区发表,未经许可,不得转载。
如有侵权,请联系 cloudcommunity@tencent.com 删除。
原创声明:本文系作者授权腾讯云开发者社区发表,未经许可,不得转载。
如有侵权,请联系 cloudcommunity@tencent.com 删除。
评论
登录后参与评论
推荐阅读
目录

